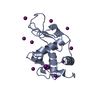
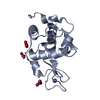
登録情報 データベース : PDB / ID : 2ydgタイトル Ascorbate co-crystallized HEWL. Lysozyme C キーワード / 機能・相同性 生物種 Gallus gallus (ニワトリ)手法 / / / 解像度 : 2 Å データ登録者 De la Mora, E. / Carmichael, I. / Garman, E.F. 資金援助 組織 認可番号 国 Consejo Nacional de Ciencia y Tecnologia (CONACYT)
ジャーナル : J.Synchrotron.Radiat. / 年 : 2011タイトル : Effective Scavenging at Cryotemperatures: Further Increasing the Dose Tolerance of Protein Crystals.著者 : De La Mora, E. / Carmichael, I. / Garman, E.F. 履歴 登録 2011年3月19日 登録サイト / 処理サイト 改定 1.0 2011年7月20日 Provider / タイプ 改定 2.0 2020年7月29日 Group Atomic model / Data collection ... Atomic model / Data collection / Derived calculations / Other / Structure summary カテゴリ atom_site / chem_comp ... atom_site / chem_comp / entity / pdbx_chem_comp_identifier / pdbx_database_status / pdbx_entity_nonpoly / pdbx_struct_conn_angle / pdbx_struct_special_symmetry / struct_conn / struct_site / struct_site_gen Item _atom_site.auth_atom_id / _atom_site.label_atom_id ... _atom_site.auth_atom_id / _atom_site.label_atom_id / _chem_comp.name / _chem_comp.type / _entity.pdbx_description / _pdbx_database_status.status_code_sf / _pdbx_entity_nonpoly.name / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id 解説 / Provider / タイプ 改定 3.0 2023年10月4日 Group Advisory / Atomic model ... Advisory / Atomic model / Author supporting evidence / Data collection / Database references / Derived calculations / Experimental preparation / Non-polymer description / Other / Refinement description / Source and taxonomy / Structure summary カテゴリ atom_site / atom_sites ... atom_site / atom_sites / chem_comp / chem_comp_atom / chem_comp_bond / database_2 / diffrn / diffrn_source / entity / entity_name_com / entity_src_nat / exptl_crystal_grow / pdbx_audit_support / pdbx_chem_comp_identifier / pdbx_contact_author / pdbx_database_status / pdbx_entity_nonpoly / pdbx_entry_details / pdbx_nonpoly_scheme / pdbx_struct_assembly_prop / pdbx_struct_conn_angle / pdbx_struct_sheet_hbond / pdbx_struct_special_symmetry / pdbx_validate_close_contact / pdbx_validate_rmsd_angle / pdbx_validate_torsion / refine / refine_hist / refine_ls_restr / refine_ls_shell / reflns / reflns_shell / software / struct / struct_conf / struct_conn / struct_ref / struct_sheet / struct_sheet_order / struct_sheet_range Item _atom_sites.fract_transf_matrix[2][1] / _atom_sites.fract_transf_matrix[3][2] ... _atom_sites.fract_transf_matrix[2][1] / _atom_sites.fract_transf_matrix[3][2] / _chem_comp.formula / _chem_comp.formula_weight / _chem_comp.id / _chem_comp.mon_nstd_flag / _chem_comp.name / _chem_comp.pdbx_synonyms / _chem_comp.type / _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _diffrn.pdbx_serial_crystal_experiment / _diffrn_source.pdbx_wavelength / _diffrn_source.pdbx_wavelength_list / _entity.formula_weight / _entity.pdbx_description / _entity.pdbx_number_of_molecules / _entity_name_com.name / _entity_src_nat.common_name / _entity_src_nat.pdbx_beg_seq_num / _entity_src_nat.pdbx_end_seq_num / _entity_src_nat.pdbx_organism_scientific / _exptl_crystal_grow.method / _exptl_crystal_grow.temp / _pdbx_contact_author.email / _pdbx_contact_author.id / _pdbx_contact_author.identifier_ORCID / _pdbx_contact_author.name_first / _pdbx_contact_author.name_salutation / _pdbx_contact_author.organization_type / _pdbx_database_status.SG_entry / _pdbx_entity_nonpoly.comp_id / _pdbx_entity_nonpoly.name / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.value / _pdbx_struct_sheet_hbond.sheet_id / _pdbx_validate_torsion.phi / _pdbx_validate_torsion.psi / _refine.B_iso_mean / _refine.aniso_B[1][1] / _refine.aniso_B[2][2] / _refine.aniso_B[3][3] / _refine.correlation_coeff_Fo_to_Fc / _refine.correlation_coeff_Fo_to_Fc_free / _refine.details / _refine.ls_R_factor_R_free / _refine.ls_R_factor_R_work / _refine.ls_R_factor_obs / _refine.ls_d_res_low / _refine.ls_number_reflns_R_free / _refine.ls_number_reflns_obs / _refine.ls_percent_reflns_R_free / _refine.overall_SU_B / _refine.overall_SU_ML / _refine.pdbx_overall_ESU_R / _refine.pdbx_overall_ESU_R_Free / _refine.pdbx_solvent_ion_probe_radii / _refine.pdbx_solvent_shrinkage_radii / _refine.pdbx_solvent_vdw_probe_radii / _refine_hist.d_res_low / _refine_hist.number_atoms_solvent / _refine_hist.number_atoms_total / _refine_ls_restr.dev_ideal / _refine_ls_restr.dev_ideal_target / _refine_ls_restr.number / _refine_ls_shell.R_factor_R_free / _refine_ls_shell.R_factor_R_work / _refine_ls_shell.number_reflns_R_free / _refine_ls_shell.number_reflns_R_work / _reflns.B_iso_Wilson_estimate / _reflns_shell.d_res_low / _reflns_shell.number_unique_obs / _reflns_shell.percent_possible_all / _software.version / _struct.pdbx_CASP_flag / _struct_conn.pdbx_dist_value / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_ref.pdbx_align_begin / _struct_ref.pdbx_seq_one_letter_code / _struct_sheet.id / _struct_sheet_order.sheet_id / _struct_sheet_range.sheet_id 解説 / 詳細 / Provider / タイプ 改定 3.1 2023年12月20日 Group / カテゴリ
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード HYDROLASE (加水分解酵素) / SCAVENGERS
HYDROLASE (加水分解酵素) / SCAVENGERS 機能・相同性情報
機能・相同性情報 抗微生物ペプチド / Neutrophil degranulation /
抗微生物ペプチド / Neutrophil degranulation /  beta-N-acetylglucosaminidase activity / cell wall macromolecule catabolic process /
beta-N-acetylglucosaminidase activity / cell wall macromolecule catabolic process /  リゾチーム /
リゾチーム /  lysozyme activity / killing of cells of another organism / defense response to Gram-negative bacterium / defense response to Gram-positive bacterium / defense response to bacterium ...
lysozyme activity / killing of cells of another organism / defense response to Gram-negative bacterium / defense response to Gram-positive bacterium / defense response to bacterium ... 抗微生物ペプチド / Neutrophil degranulation /
抗微生物ペプチド / Neutrophil degranulation /  beta-N-acetylglucosaminidase activity / cell wall macromolecule catabolic process /
beta-N-acetylglucosaminidase activity / cell wall macromolecule catabolic process /  リゾチーム /
リゾチーム /  lysozyme activity / killing of cells of another organism / defense response to Gram-negative bacterium / defense response to Gram-positive bacterium / defense response to bacterium /
lysozyme activity / killing of cells of another organism / defense response to Gram-negative bacterium / defense response to Gram-positive bacterium / defense response to bacterium /  小胞体 /
小胞体 /  extracellular space / identical protein binding /
extracellular space / identical protein binding /  細胞質
細胞質
 Gallus gallus (ニワトリ)
Gallus gallus (ニワトリ) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2 Å
分子置換 / 解像度: 2 Å  データ登録者
データ登録者 メキシコ, 1件
メキシコ, 1件  引用
引用 ジャーナル: J.Synchrotron.Radiat. / 年: 2011
ジャーナル: J.Synchrotron.Radiat. / 年: 2011 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2ydg.cif.gz
2ydg.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2ydg.ent.gz
pdb2ydg.ent.gz PDB形式
PDB形式 2ydg.json.gz
2ydg.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/yd/2ydg
https://data.pdbj.org/pub/pdb/validation_reports/yd/2ydg ftp://data.pdbj.org/pub/pdb/validation_reports/yd/2ydg
ftp://data.pdbj.org/pub/pdb/validation_reports/yd/2ydg リンク
リンク 集合体
集合体
 要素
要素
 Gallus gallus (ニワトリ) / 参照: UniProt: P00698,
Gallus gallus (ニワトリ) / 参照: UniProt: P00698,  リゾチーム
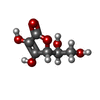
リゾチーム ビタミンC
ビタミンC 水
水 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製
 シンクロトロン / サイト:
シンクロトロン / サイト:  ESRF
ESRF  / ビームライン: ID14-4 / 波長: 0.939 Å
/ ビームライン: ID14-4 / 波長: 0.939 Å : 0.939 Å / 相対比: 1
: 0.939 Å / 相対比: 1  解析
解析 :
:  分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー





































































































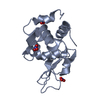
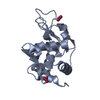

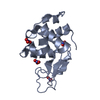

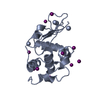



































































































































































 PDBj
PDBj