-検索条件
-検索結果
検索 (著者・登録者: inami & m)の結果75件中、1から50件目までを表示しています

EMDB-60995: 
P ring on polyrod-P ring complex from Salmonella TH26292 strain

PDB-9iyc: 
P ring on polyrod-P ring complex from Salmonella TH26292 strain

EMDB-61731: 
Polyrod formed by FlgG (G65V) from the Salmonella TH26292 strain

EMDB-61835: 
Polyrod-P ring complex from Salmonella TH26292 strain

PDB-9jqo: 
Polyrod formed by FlgG (G65V) from the Salmonella TH26292 strain

EMDB-61993: 
Structure of the Salmonella flagellar FliPQR complex reconstituted in the peptidisc

PDB-9k29: 
Structure of the Salmonella flagellar FliPQR complex reconstituted in the peptidisc

EMDB-60989: 
Class 2 state of the GfsA KSQ-ancestralAT chimeric didomain in complex with the GfsA ACP domain

EMDB-61520: 
Class 3 state of the GfsA KSQ-ancestralAT chimeric didomain in complex with the GfsA ACP domain

EMDB-61522: 
Class 1 state of the GfsA KSQ-ancestralAT chimeric didomain in complex with the GfsA ACP domain

PDB-9jj9: 
Class 3 state of the GfsA KSQ-ancestralAT chimeric didomain in complex with the GfsA ACP domain

PDB-9jjb: 
Class 1 state of the GfsA KSQ-ancestralAT chimeric didomain in complex with the GfsA ACP domain

EMDB-60747: 
Cryo-EM structure of Escherichia coli hibernating ribosome with RNase I mutant

PDB-9iot: 
Cryo-EM structure of Escherichia coli hibernating ribosome with RNase I mutant

EMDB-63714: 
Structure of photosynthetic LH1-RC complex the Halophilic Nonsulfur Purple Bacterium, Rhodothalassium salexigens

EMDB-64946: 
Map including micelle density from the photosynthetic LH1-RC complex of the halophilic nonsulfur purple bacterium Rhodothalassium salexigens

PDB-9m8m: 
Structure of photosynthetic LH1-RC complex the Halophilic Nonsulfur Purple Bacterium, Rhodothalassium salexigens

EMDB-63392: 
The chimeric flagellar motor complex between MotA1B1 from Paenibacillus sp. TCA20 and MotAB from E.coli, state 1

EMDB-63393: 
The chimeric flagellar motor complex between MotA1B1 from Paenibacillus sp. TCA20 and MotAB from E.coli, state 2

EMDB-63394: 
The chimeric flagellar motor complex between MotA1B1 from Paenibacillus sp. TCA20 and MotAB from E.coli, state 3

PDB-9lu9: 
The chimeric flagellar motor complex between MotA1B1 from Paenibacillus sp. TCA20 and MotAB from E.coli, state 1

PDB-9lub: 
The chimeric flagellar motor complex between MotA1B1 from Paenibacillus sp. TCA20 and MotAB from E.coli, state 2

PDB-9luc: 
The chimeric flagellar motor complex between MotA1B1 from Paenibacillus sp. TCA20 and MotAB from E.coli, state 3

EMDB-39679: 
A tetrameric STAT1-DNA complex

EMDB-39680: 
A dimeric STAT1-DNA complex

PDB-8yyu: 
A tetrameric STAT1-DNA complex

PDB-8yyv: 
A dimeric STAT1-DNA complex

EMDB-60158: 
Cryo-EM structure of photosynthetic LH1' complex of Roseospirillum parvum

EMDB-60165: 
Cryo-EM structure of photosynthetic LH1-RC core complex of Roseospirillum parvum

PDB-8zjw: 
Cryo-EM structure of photosynthetic LH1' complex of Roseospirillum parvum

PDB-8zk2: 
Cryo-EM structure of photosynthetic LH1-RC core complex of Roseospirillum parvum

EMDB-60007: 
Structure of the Salmonella flagellar MS-ring with C11 symmetry applied

EMDB-60008: 
Structure of the RBM3 ring of Salmonella flagellar MS-ring protein FliF with C33 symmetry applied

EMDB-60009: 
Structure of the RBM3 ring of Salmonella flagellar MS-ring protein FliF with C34 symmetry applied

EMDB-62210: 
Structure of the 34-mer RBM3 ring of Salmonella flagellar MS-ring protein FliF with C1 symmetry applied

EMDB-62211: 
Structure of the 33-mer RBM3 ring of Salmonella flagellar MS-ring protein FliF with C1 symmetry applied

PDB-8zds: 
Structure of the Salmonella flagellar MS-ring with C11 symmetry applied
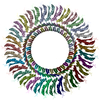
PDB-8zdt: 
Structure of the RBM3 ring of Salmonella flagellar MS-ring protein FliF with C33 symmetry applied
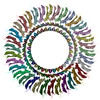
PDB-8zdu: 
Structure of the RBM3 ring of Salmonella flagellar MS-ring protein FliF with C34 symmetry applied

EMDB-60274: 
SARS-CoV-2 XBB.1.5 spike glycoprotein trimer in complex with antigen-binding fragments (Fabs)

EMDB-39761: 
Structure of the S-ring region of the Vibrio flagellar MS-ring protein FliF with 34-fold symmetry applied

EMDB-39763: 
Structure of the S-ring region of the Vibrio flagellar MS-ring protein FliF with 35-fold symmetry applied

EMDB-39764: 
Homomeric 34mer of the Vibrio flagellar MS-ring protein FliF without symmetry imposition

EMDB-39765: 
Homomeric 35mer of the Vibrio flagellar MS-ring protein FliF without symmetry imposition

PDB-8z4d: 
Structure of the S-ring region of the Vibrio flagellar MS-ring protein FliF with 34-fold symmetry applied
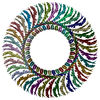
PDB-8z4g: 
Structure of the S-ring region of the Vibrio flagellar MS-ring protein FliF with 35-fold symmetry applied

EMDB-60959: 
Salmonella enterica serovar Typhimurium FliC(G426A)delta(204-292) forming the L-type straight filament

PDB-9iwq: 
Salmonella enterica serovar Typhimurium FliC(G426A)delta(204-292) forming the L-type straight filament

EMDB-37465: 
Photosynthetic LH1-RC complex from the purple sulfur bacterium Allochromatium vinosum purified by sucrose density

EMDB-37466: 
Photosynthetic LH1-RC complex from the purple sulfur bacterium Allochromatium vinosum purified by Ca2+-DEAE
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
