-検索条件
-検索結果
検索 (著者・登録者: lu & k)の結果7,697件中、1から50件目までを表示しています

EMDB-42603: 
Human p97/VCP structure with a triazole inhibitor (NSC799462/hexamer)

EMDB-42625: 
Human p97/VCP R155H mutant structure with a triazole inhibitor (NSC804515)

EMDB-42626: 
Human p97/VCP R155H mutant structure with a triazole inhibitor (NSC819701/up)

EMDB-42627: 
Human p97/VCP R155H mutant structure with a triazole inhibitor (NSC819701/down)

EMDB-44748: 
Human p97/VCP structure with a triazole inhibitor (NSC799462/dodecamer)

EMDB-41766: 
CryoEM structure of D2 dopamine receptor in complex with GoA KE mutant, scFv16, and dopamine

EMDB-41776: 
CryoEM structure of D2 dopamine receptor in complex with GoA KE mutant and dopamine

EMDB-45973: 
Bufavirus 1 at pH 2.6

EMDB-44246: 
Cryo-EM structure of HIV-1 JRFL v6 Env in complex with vaccine-elicited, Membrane Proximal External Region (MPER) directed antibody DH1317.4.

EMDB-51031: 
Cryo-electron tomogram of AL59 amyloids interacting with collagen VI

EMDB-51032: 
Cryo-electron tomogram of AL59 amyloids interacting with collagen VI

EMDB-51033: 
Cryo-electron tomogram of AL59 amyloids interacting with collagen VI

EMDB-51038: 
Cryo-electron tomogram of AL59 amyloids interacting with collagen VI

EMDB-19397: 
Composite map of the C. elegans Intron Lariat Spliceosome primed for disassembly (ILS')

EMDB-19398: 
Structure of the C. elegans Intron Lariat Spliceosome double-primed for disassembly (ILS'')

PDB-8ro0: 
Structure of the C. elegans Intron Lariat Spliceosome primed for disassembly (ILS')

PDB-8ro1: 
Structure of the C. elegans Intron Lariat Spliceosome double-primed for disassembly (ILS'')

EMDB-38758: 
Structural of methylmalonate semialdehyde dehydrogenase ALDH6A1

EMDB-19822: 
Helical reconstruction of yeast eisosome protein Pil1 bound to membrane composed of lipid mixture +PIP2/+bromosterol (DOPC, DOPE, DOPS, bromo-ergosterol, PI(4,5)P2 35:20:20:15:10)

EMDB-44482: 
Cryo-EM structure of the HIV-1 JR-FL IDL Env trimer in complex with PGT122 Fab
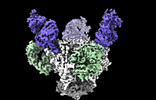
EMDB-44484: 
Cryo-EM structure of the HIV-1 BG505 IDL Env trimer in complex with 3BNC117 and 10-1074 Fabs
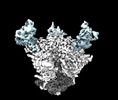
EMDB-44491: 
Cryo-EM structure of the HIV-1 WITO IDL Env trimer in complex with PGT122 Fab

PDB-9ber: 
Cryo-EM structure of the HIV-1 JR-FL IDL Env trimer in complex with PGT122 Fab

PDB-9bew: 
Cryo-EM structure of the HIV-1 BG505 IDL Env trimer in complex with 3BNC117 and 10-1074 Fabs

PDB-9bf6: 
Cryo-EM structure of the HIV-1 WITO IDL Env trimer in complex with PGT122 Fab

EMDB-42400: 
RORC mRNA 3'UTR riboswitch A97G/G98A mutant class C

EMDB-42401: 
RORC mRNA 3'UTR riboswitch 77-GA mutant class A

EMDB-42403: 
RORC mRNA 3'UTR riboswitch 117-AC mutant class C

EMDB-42404: 
RORC mRNA 3'UTR riboswitch 117-AC mutant class B

EMDB-37499: 
Cryo-EM structure of CRISPR-Csm effector complex from Mycobacterium canettii

PDB-8wfx: 
Cryo-EM structure of CRISPR-Csm effector complex from Mycobacterium canettii

EMDB-15127: 
Structure of mammalian Pol II-DSIF-SPT6-PAF1-TFIIS-hexasome elongation complex

PDB-8a3y: 
Structure of mammalian Pol II-DSIF-SPT6-PAF1-TFIIS-hexasome elongation complex

EMDB-18307: 
Native eisosome lattice bound to plasma membrane microdomain

EMDB-18308: 
Helical reconstruction of yeast eisosome protein Pil1 bound to membrane composed of lipid mixture -PIP2/+sterol (DOPC, DOPE, DOPS, cholesterol 30:20:20:30)

EMDB-18309: 
Helical reconstruction of yeast eisosome protein Pil1 bound to membrane composed of lipid mixture +PIP2/-sterol (DOPC, DOPE, DOPS, PI(4,5)P2 50:20:20:10)

EMDB-18310: 
Helical reconstruction of yeast eisosome protein Pil1 bound to membrane composed of lipid mixture +PIP2/+sterol (DOPC, DOPE, DOPS, cholesterol, PI(4,5)P2 35:20:20:15:10)

EMDB-18311: 
Compact state - Native eisosome lattice bound to plasma membrane microdomain

EMDB-18312: 
Stretched state - Native eisosome lattice bound to plasma membrane microdomain

PDB-8qb7: 
Pil1 in native eisosome lattice bound to plasma membrane microdomain

PDB-8qb8: 
Lsp1 in native eisosome lattice bound to plasma membrane microdomain

PDB-8qb9: 
Helical reconstruction of yeast eisosome protein Pil1 bound to membrane composed of lipid mixture -PIP2/+sterol (DOPC, DOPE, DOPS, cholesterol 30:20:20:30)

PDB-8qbb: 
Helical reconstruction of yeast eisosome protein Pil1 bound to membrane composed of lipid mixture +PIP2/-sterol (DOPC, DOPE, DOPS, PI(4,5)P2 50:20:20:10)

PDB-8qbd: 
Helical reconstruction of yeast eisosome protein Pil1 bound to membrane composed of lipid mixture +PIP2/+sterol (DOPC, DOPE, DOPS, cholesterol, PI(4,5)P2 35:20:20:15:10)

PDB-8qbe: 
Compact state - Pil1 in native eisosome lattice bound to plasma membrane microdomain

PDB-8qbf: 
Compact state - Pil1 dimer with lipid headgroups fitted in native eisosome lattice bound to plasma membrane microdomain

PDB-8qbg: 
Stretched state - Pil1 in native eisosome lattice bound to plasma membrane microdomain

EMDB-43551: 
CCHFV GP38 bound with ADI-46143 and ADI-46158 Fabs

EMDB-43552: 
CCHFV GP38 bound with ADI-58062 and ADI-63530 Fabs

EMDB-43553: 
CCHFV GP38 bound with ADI-58026 and ADI-63547 Fabs
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
