-検索条件
-検索結果
検索 (著者・登録者: meyer & h)の結果430件中、1から50件目までを表示しています

EMDB-41578: 
mGluR3 class 1 in the presence of the antagonist LY 341495

EMDB-45242: 
mGluR3 in the presence of the antagonist LY 341495 and positive allosteric modulator VU6023326 class 2

PDB-8trd: 
mGluR3 class 1 in the presence of the antagonist LY 341495

EMDB-18538: 
p97 in DNA origami cage

EMDB-41501: 
mGluR3 in the presence of the agonist LY379268 and PAM VU6023326

EMDB-41567: 
Metabotropic glutamate receptor 3 class 3 bound to antagonist LY 341495

EMDB-41568: 
mGluR3 in the presence of the agonist LY379268

EMDB-41577: 
mGluR3 in the presence of the antagonist LY 341495 and positive allosteric modulator VU6023326

EMDB-44861: 
metabotropic glutamate receptor subtype three bound to the antagonist LY 341495, class two

PDB-8tqb: 
mGluR3 in the presence of the agonist LY379268 and PAM VU6023326

PDB-8tr0: 
Metabotropic glutamate receptor 3 class 3 bound to antagonist LY 341495

PDB-8tr2: 
mGluR3 in the presence of the agonist LY379268

PDB-8trc: 
mGluR3 in the presence of the antagonist LY 341495 and positive allosteric modulator VU6023326
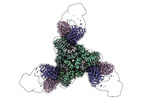
EMDB-42527: 
Pre-fusion Measles virus fusion protein complexed with Fab 77
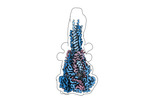
EMDB-42539: 
Structure of the Measles virus Fusion protein in the post-fusion conformation
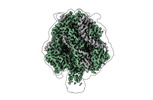
EMDB-42593: 
Structure of the Measles virus Fusion protein in the pre-fusion conformation

EMDB-42595: 
Structure of the Measles virus Fusion protein in the pre-fusion conformation with bound [FIP-HRC]2-PEG11
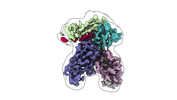
EMDB-43827: 
Fab 77-stabilized MeV F ectodomain fragment

PDB-8ut2: 
Pre-fusion Measles virus fusion protein complexed with Fab 77

PDB-8utf: 
Structure of the Measles virus Fusion protein in the post-fusion conformation

PDB-8uup: 
Structure of the Measles virus Fusion protein in the pre-fusion conformation

PDB-8uuq: 
Structure of the Measles virus Fusion protein in the pre-fusion conformation with bound [FIP-HRC]2-PEG11

PDB-9at8: 
Fab 77-stabilized MeV F ectodomain fragment

EMDB-18701: 
Endosomal membrane tethering complex CORVET

EMDB-18702: 
Endosomal membrane tethering complex CORVET, Vps8-Vps11 local refinement map

EMDB-18703: 
Endosomal membrane tethering complex CORVET, Vps8 beta propeller local refinement map

EMDB-18704: 
Endosomal membrane tethering complex CORVET, SNARE binding module local refinement map

EMDB-18705: 
Endosomal membrane tethering complex CORVET, core local refinement map

EMDB-18706: 
Endosomal membrane tethering complex CORVET, Vps18 beta propeller local refinement map

EMDB-18707: 
Endosomal membrane tethering complex CORVET, consensus map

EMDB-18708: 
Endosomal membrane tethering complex CORVET, Vps11deltaN mutant

PDB-8qx8: 
Endosomal membrane tethering complex CORVET

EMDB-19845: 
Outward-open structure of human dopamine transporter bound to cocaine

PDB-9eo4: 
Outward-open structure of human dopamine transporter bound to cocaine

EMDB-19426: 
Escherichia coli 50S subunit in complex with the antimicrobial peptide Api137

EMDB-19427: 
Escherichia coli 50S subunit in complex with the antimicrobial peptide Api88 - conformation I

EMDB-19428: 
Escherichia coli 50S subunit in complex with the antimicrobial peptide Api88 - conformation II

EMDB-19429: 
Escherichia coli 50S subunit in complex with the antimicrobial peptide Api88 - conformation III

PDB-8rpy: 
Escherichia coli 50S subunit in complex with the antimicrobial peptide Api137

PDB-8rpz: 
Escherichia coli 50S subunit in complex with the antimicrobial peptide Api88 - conformation I

PDB-8rq0: 
Escherichia coli 50S subunit in complex with the antimicrobial peptide Api88 - conformation II

PDB-8rq2: 
Escherichia coli 50S subunit in complex with the antimicrobial peptide Api88 - conformation III
EMDB-18639: 
Locally refined SARS-CoV-2 BA-2.86 Spike receptor binding domain (RBD) complexed with angiotensin converting enzyme 2 (ACE2)

EMDB-18649: 
Local refinement of SARS-CoV-2 BA.2.86 Spike and XBB-7 Fab

EMDB-19002: 
XBB-4 Fab in complex with SARS-CoV-2 BA.2.12.1 Spike Glycoprotein

PDB-8qsq: 
Locally refined SARS-CoV-2 BA-2.86 Spike receptor binding domain (RBD) complexed with angiotensin converting enzyme 2 (ACE2)

PDB-8qtd: 
Local refinement of SARS-CoV-2 BA.2.86 Spike and XBB-7 Fab

PDB-8r8k: 
XBB-4 Fab in complex with SARS-CoV-2 BA.2.12.1 Spike Glycoprotein

EMDB-44496: 
Cryo-EM co-structure of AcrB with the CU032 efflux pump inhibitor

EMDB-44500: 
Cryo-EM co-structure of AcrB with the EPM35 efflux pump inhibitor
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
