-検索条件
-検索結果
検索 (著者・登録者: gold & s)の結果318件中、1から50件目までを表示しています
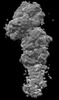
EMDB-44479: 
Cryo-EM structure of synthetic claudin-4 complex with Clostridium perfringens enterotoxin C-terminal domain, sFab COP-2, and Nanobody

PDB-9bei: 
Cryo-EM structure of synthetic claudin-4 complex with Clostridium perfringens enterotoxin C-terminal domain, sFab COP-2, and Nanobody

EMDB-19562: 
Vimentin intermediate filament protofibril stoichiometry

EMDB-19563: 
Vimentin intermediate filament structure (delta tail)

PDB-8rve: 
Vimentin intermediate filament

EMDB-16844: 
Vimentin intermediate filament structure

EMDB-19440: 
Cryo-EM structure of human NTCP-Bulevirtide complex

PDB-8rqf: 
Cryo-EM structure of human NTCP-Bulevirtide complex

EMDB-41888: 
Structure of Apo CXCR4/Gi complex

EMDB-41889: 
Structure of CXCL12-bound CXCR4/Gi complex

EMDB-41890: 
Structure of AMD3100-bound CXCR4/Gi complex

EMDB-41891: 
Structure of REGN7663 Fab-bound CXCR4/Gi complex

EMDB-41892: 
Structure of REGN7663-Fab bound CXCR4

EMDB-41893: 
Structure of trimeric CXCR4 in complex with REGN7663 Fab

EMDB-41894: 
Structure of tetrameric CXCR4 in complex with REGN7663 Fab

PDB-8u4n: 
Structure of Apo CXCR4/Gi complex

PDB-8u4o: 
Structure of CXCL12-bound CXCR4/Gi complex

PDB-8u4p: 
Structure of AMD3100-bound CXCR4/Gi complex

PDB-8u4q: 
Structure of REGN7663 Fab-bound CXCR4/Gi complex

PDB-8u4r: 
Structure of REGN7663-Fab bound CXCR4

PDB-8u4s: 
Structure of trimeric CXCR4 in complex with REGN7663 Fab

PDB-8u4t: 
Structure of tetrameric CXCR4 in complex with REGN7663 Fab

EMDB-18119: 
Sulfolobus acidocaldarius AAP filament.

PDB-8q30: 
Sulfolobus acidocaldarius AAP filament.

PDB-8qox: 
Two-component assembly of SlaA and SlaB S-layer proteins of Sulfolobus acidocaldarius

PDB-8qp0: 
A hexamer pore in the S-layer of Sulfolobus acidocaldarius formed by SlaA protein

EMDB-18127: 
S-layer of archaeon Sulfolobus acidocaldarius by subtomogram averaging

EMDB-18991: 
Sub-tomogram average of the C. elegans ATP synthase dimer

EMDB-18728: 
Rat synaptosome
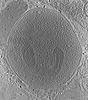
EMDB-18744: 
Stimulated rat synaptosome.

EMDB-18746: 
wild type neuronal synapse

EMDB-18748: 
SNAP-25-4E neuronal synapse

EMDB-18749: 
SNAP-25-4K neuronal synapse

EMDB-28036: 
Cryo-EM structure of the full-length human NF1 dimer

PDB-8edm: 
Cryo-EM structure of the full-length human NF1 dimer

EMDB-40185: 
Representative cryo-electron tomogram of pRLB-540 mixed with liposomes at pH 8.0

EMDB-40186: 
Representative cryo-electron tomogram of pRLB-540 mixed with liposomes (acidified to pH 5.5, plunge frozen after 20 s)

EMDB-40187: 
Representative cryo-electron tomogram of pRLB-540 mixed with liposomes, acidified to pH 5.5 and plunge frozen after 60s incubation.

EMDB-15530: 
S-layer protein SlaA from Sulfolobus acidocaldarius at pH 10.0

EMDB-15531: 
S-layer protein SlaA from Sulfolobus acidocaldarius at pH 7.0

PDB-8an2: 
S-layer protein SlaA from Sulfolobus acidocaldarius at pH 10.0

PDB-8an3: 
S-layer protein SlaA from Sulfolobus acidocaldarius at pH 7.0

EMDB-41158: 
CS2it1p2_F7K local refinement for HCMV Trimer in complex with CS2it1p2_F7K Fab and CS4tt1p1_E3K Fab

EMDB-41180: 
Global reconstruction for HCMV Pentamer in complex with CS2pt1p2_A10L Fab and CS3pt1p4_C1L Fab

EMDB-41156: 
HCMV Trimer in complex with CS2it1p2_F7K Fab and CS4tt1p1_E3K Fab

EMDB-41157: 
Global reconstruction for HCMV Trimer in complex with CS2it1p2_F7K Fab and CS4tt1p1_E3K Fab

EMDB-41160: 
CS4tt1p1_E3K local refinement for HCMV Trimer in complex with CS2it1p2_F7K Fab and CS4tt1p1_E3K Fab

EMDB-41161: 
gH base local refinement for HCMV Trimer in complex with CS2it1p2_F7K Fab and CS4tt1p1_E3K Fab

EMDB-41179: 
HCMV Pentamer in complex with CS2pt1p2_A10L Fab and CS3pt1p4_C1L Fab

EMDB-41181: 
CS3pt1p4_C1L local refinement for HCMV Pentamer in complex with CS2pt1p2_A10L Fab and CS3pt1p4_C1L Fab
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
