+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 3upt | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Crystal structure of a transketolase from Burkholderia pseudomallei bound to TPP, calcium and ribose-5-phosphate | |||||||||
 要素 要素 | Transketolase | |||||||||
 キーワード キーワード | TRANSFERASE / Structural Genomics / Seattle Structural Genomics Center for Infectious Disease / SSGCID / TPP / calcium-dependent / co-factor / e pentose phosphate pathway / Calvin cycle / tkt | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報transketolase / transketolase activity / pentose-phosphate shunt, non-oxidative branch / metal ion binding / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  Burkholderia thailandensis (バクテリア) Burkholderia thailandensis (バクテリア) | |||||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.4 Å 分子置換 / 解像度: 2.4 Å | |||||||||
 データ登録者 データ登録者 | Seattle Structural Genomics Center for Infectious Disease (SSGCID) | |||||||||
 引用 引用 |  ジャーナル: Plos One / 年: 2013 ジャーナル: Plos One / 年: 2013タイトル: Combining functional and structural genomics to sample the essential Burkholderia structome. 著者: Baugh, L. / Gallagher, L.A. / Patrapuvich, R. / Clifton, M.C. / Gardberg, A.S. / Edwards, T.E. / Armour, B. / Begley, D.W. / Dieterich, S.H. / Dranow, D.M. / Abendroth, J. / Fairman, J.W. / ...著者: Baugh, L. / Gallagher, L.A. / Patrapuvich, R. / Clifton, M.C. / Gardberg, A.S. / Edwards, T.E. / Armour, B. / Begley, D.W. / Dieterich, S.H. / Dranow, D.M. / Abendroth, J. / Fairman, J.W. / Fox, D. / Staker, B.L. / Phan, I. / Gillespie, A. / Choi, R. / Nakazawa-Hewitt, S. / Nguyen, M.T. / Napuli, A. / Barrett, L. / Buchko, G.W. / Stacy, R. / Myler, P.J. / Stewart, L.J. / Manoil, C. / Van Voorhis, W.C. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  3upt.cif.gz 3upt.cif.gz | 508.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb3upt.ent.gz pdb3upt.ent.gz | 414.4 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  3upt.json.gz 3upt.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/up/3upt https://data.pdbj.org/pub/pdb/validation_reports/up/3upt ftp://data.pdbj.org/pub/pdb/validation_reports/up/3upt ftp://data.pdbj.org/pub/pdb/validation_reports/up/3upt | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  3d63C  3dahC  3eizC  3ej2C  3ek2C  3ezoC  3f0fC  3ftpC  3gk0C  3gk3C  3gvfC  3gwaC  3gweC  3imlC  3sz8C  3t4cC  3tmlC  3tmqC  3txyC  3u7jC  3ue9C  3uk1SC  3uk2C  3undC  3urrC  3uw1C  3uw2C  3uw3C  3v2iC  3v7nC  3v8hC  3v9oC  3v9pC  3vavC  4ddoC  4dfeC  4dheC  4dhkC  4dutC  4dz4C  4e4tC  4efiC  4eg0C  4egjC  4ek2C  4eqyC  4ewgC  4exqC  4f2gC  4f32C  4f3nC  4f3yC  4f4hC  4f7dC  4fk8C  4fryC  4g1kC  4g67C  4ghkC  4h3yC  4h3zC  4h4gC S: 精密化の開始モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| その他のデータベース |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 / 糖 , 2種, 4分子 AB

| #1: タンパク質 | 分子量: 76727.477 Da / 分子数: 2 / 由来タイプ: 組換発現 由来: (組換発現)  Burkholderia thailandensis (バクテリア) Burkholderia thailandensis (バクテリア)株: E264 / ATCC 700388 / DSM 13276 / CIP 106301 / 遺伝子: BTH_I1195, tkt / 発現宿主:  #4: 糖 | |
|---|
-非ポリマー , 4種, 829分子 
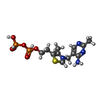





| #2: 化合物 | | #3: 化合物 | #5: 化合物 | ChemComp-BR / #6: 水 | ChemComp-HOH / | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.51 Å3/Da / 溶媒含有率: 51.08 % |
|---|---|
| 結晶化 | 温度: 289 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 7.5 詳細: ButhA.01294.a.A1 at 38 mg/mL with 5 mM TPP, 5 mM ribose-5-phosphate, 5 mM CaCl2 against PACT screen condition G2, 0.2 M NaBr, 0.1 M BisTris propane pH 7.5, 20% PEG 3350 cryo-protected with ...詳細: ButhA.01294.a.A1 at 38 mg/mL with 5 mM TPP, 5 mM ribose-5-phosphate, 5 mM CaCl2 against PACT screen condition G2, 0.2 M NaBr, 0.1 M BisTris propane pH 7.5, 20% PEG 3350 cryo-protected with crystallant, compounds and 25% ethylene glycol; crystal tracking ID 227593g2, VAPOR DIFFUSION, SITTING DROP, temperature 289K |
-データ収集
| 回折 | 平均測定温度: 100 K | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  ALS ALS  / ビームライン: 5.0.1 / 波長: 0.9774 Å / ビームライン: 5.0.1 / 波長: 0.9774 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 検出器 | タイプ: ADSC QUANTUM 315r / 検出器: CCD / 日付: 2011年11月11日 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 放射波長 | 波長: 0.9774 Å / 相対比: 1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 反射 | 解像度: 2.4→50 Å / Num. obs: 61439 / % possible obs: 99.7 % / Observed criterion σ(I): -3 / Biso Wilson estimate: 26.634 Å2 / Rmerge(I) obs: 0.152 / Net I/σ(I): 17.52 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 反射 シェル | Diffraction-ID: 1
|
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: 3UK1 解像度: 2.4→50 Å / Cor.coef. Fo:Fc: 0.957 / Cor.coef. Fo:Fc free: 0.927 / WRfactor Rfree: 0.1626 / WRfactor Rwork: 0.1239 / Occupancy max: 1 / Occupancy min: 0.3 / FOM work R set: 0.8818 / SU B: 10.932 / SU ML: 0.137 / SU R Cruickshank DPI: 0.3216 / SU Rfree: 0.2122 / 交差検証法: THROUGHOUT / σ(F): 0 / ESU R Free: 0.212 / 立体化学のターゲット値: MAXIMUM LIKELIHOOD 詳細: U VALUES: WITH TLS ADDED. HYDROGENS HAVE BEEN USED IF PRESENT IN THE INPUT
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.2 Å / 溶媒モデル: MASK | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso max: 101.68 Å2 / Biso mean: 19.5631 Å2 / Biso min: 7.25 Å2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.4→50 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 2.4→2.462 Å / Total num. of bins used: 20
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLS | 手法: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLSグループ |
|
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj









