+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 2wfj | ||||||
|---|---|---|---|---|---|---|---|
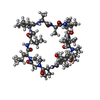
| タイトル | Atomic resolution crystal structure of the PPIase domain of human cyclophilin G in complex with cyclosporin A. | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | ISOMERASE/IMMUNOSUPPRESSANT / ISOMERASE-IMMUNOSUPPRESSANT COMPLEX / CYCLOPHILIN-CYCLOSPORIN COMPLEX / CYCLOSPORIN A / IMMUNOSUPPRESSANT / CYCLOPHILIN | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報cyclosporin A binding / mRNA Splicing - Major Pathway / RNA splicing / peptidyl-prolyl cis-trans isomerase activity / RNA polymerase II CTD heptapeptide repeat P3 isomerase activity / RNA polymerase II CTD heptapeptide repeat P6 isomerase activity / peptidylprolyl isomerase / nuclear matrix / SARS-CoV-1 activates/modulates innate immune responses / protein folding ...cyclosporin A binding / mRNA Splicing - Major Pathway / RNA splicing / peptidyl-prolyl cis-trans isomerase activity / RNA polymerase II CTD heptapeptide repeat P3 isomerase activity / RNA polymerase II CTD heptapeptide repeat P6 isomerase activity / peptidylprolyl isomerase / nuclear matrix / SARS-CoV-1 activates/modulates innate immune responses / protein folding / nuclear speck / RNA binding / nucleoplasm / nucleus / cytosol / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  HOMO SAPIENS (ヒト) HOMO SAPIENS (ヒト) TOLYPOCLADIUM INFLATUM (菌類) TOLYPOCLADIUM INFLATUM (菌類) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / DIRECT METHODS / 解像度: 0.75 Å シンクロトロン / DIRECT METHODS / 解像度: 0.75 Å | ||||||
 データ登録者 データ登録者 | Stegmann, C.M. / Sheldrick, G.M. / Wahl, M.C. | ||||||
 引用 引用 |  ジャーナル: Angew.Chem.Int.Ed.Engl. / 年: 2009 ジャーナル: Angew.Chem.Int.Ed.Engl. / 年: 2009タイトル: The Thermodynamic Influence of Trapped Water Molecules on a Protein-Ligand Interaction. 著者: Stegmann, C.M. / Seeliger, D. / Sheldrick, G.M. / De Groot, B.L. / Wahl, M.C. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  2wfj.cif.gz 2wfj.cif.gz | 105.3 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb2wfj.ent.gz pdb2wfj.ent.gz | 79.9 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  2wfj.json.gz 2wfj.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  2wfj_validation.pdf.gz 2wfj_validation.pdf.gz | 452.1 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  2wfj_full_validation.pdf.gz 2wfj_full_validation.pdf.gz | 456.3 KB | 表示 | |
| XML形式データ |  2wfj_validation.xml.gz 2wfj_validation.xml.gz | 15.3 KB | 表示 | |
| CIF形式データ |  2wfj_validation.cif.gz 2wfj_validation.cif.gz | 21.8 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/wf/2wfj https://data.pdbj.org/pub/pdb/validation_reports/wf/2wfj ftp://data.pdbj.org/pub/pdb/validation_reports/wf/2wfj ftp://data.pdbj.org/pub/pdb/validation_reports/wf/2wfj | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 / タンパク質・ペプチド , 2種, 2分子 AB
| #1: タンパク質 | 分子量: 19843.518 Da / 分子数: 1 / 断片: PPIASE DOMAIN, RESIDUES 1-177 / 由来タイプ: 組換発現 / 由来: (組換発現)  HOMO SAPIENS (ヒト) / プラスミド: PETM-11 / 発現宿主: HOMO SAPIENS (ヒト) / プラスミド: PETM-11 / 発現宿主:  |
|---|---|
| #2: タンパク質・ペプチド | |
-非ポリマー , 4種, 302分子 






| #3: 化合物 | ChemComp-EDO / | ||||
|---|---|---|---|---|---|
| #4: 化合物 | | #5: 化合物 | ChemComp-CL / | #6: 水 | ChemComp-HOH / | |
-詳細
| 構成要素の詳細 | CYCLOSPORIN IS A CYCLIC UNDECAPEPTIDE. HERE, CYCLOSPORIN A IS REPRESENTED BY THE SEQUENCE (SEQRES) ...CYCLOSPORI |
|---|---|
| Has protein modification | Y |
| 配列の詳細 | INITIAL GA RESIDUES ARE CLONING ARTEFACTS. |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 1.87 Å3/Da / 溶媒含有率: 34.4 % 解説: STRUCTURE WAS SOLVED BY APPLYING DIRECT METHODS IN SHELXD IN TWO STAGES FIRST SEARCHING FOR 9 SULFUR ATOMS WITH THE HELP OF PATTERSON SEEDING AND DUAL-SPACE DIRECT METHODS AND THEN EXPANDING ...解説: STRUCTURE WAS SOLVED BY APPLYING DIRECT METHODS IN SHELXD IN TWO STAGES FIRST SEARCHING FOR 9 SULFUR ATOMS WITH THE HELP OF PATTERSON SEEDING AND DUAL-SPACE DIRECT METHODS AND THEN EXPANDING THE MOST PROMISING SOLUTIONS TO THE FULL STRUCTURE. DATA WERE COLLECTED FROM A SINGLE CRYSTAL FIRST ON A BRUKER ROTATING-ANODE GENERATOR, PRODUCING CUKALPHA RADIATION, AND A SMART6000 16-MEGAPIXEL CCD TO A RESOLUTION OF 1.12A. DATA FROM THE SAME CRYSTAL WERE THEN COLLECTED ON BEAMLINE PXII OF THE SWISS LIGHT SOURCE (SLS, VILLIGEN, SWITZERLAND) USING A MAR CCD 225 DETECTOR AND MERGED WITH THE IN-HOUSE DATA. |
|---|---|
| 結晶化 | pH: 8.5 / 詳細: 28-32% (W/V) PEG 4000, 0.2M MGCL2, 0.1M TRIS PH 8.5 |
-データ収集
| 回折 | 平均測定温度: 100 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  SLS SLS  / ビームライン: X10SA / 波長: 0.6888 / ビームライン: X10SA / 波長: 0.6888 |
| 検出器 | タイプ: MARRESEARCH / 検出器: CCD / 詳細: COLLIMATOR |
| 放射 | モノクロメーター: SI(111) / プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 0.6888 Å / 相対比: 1 |
| 反射 | 解像度: 0.75→40 Å / Num. obs: 212972 / % possible obs: 99.1 % / Observed criterion σ(I): 2 / 冗長度: 5.25 % / Rmerge(I) obs: 0.06 / Net I/σ(I): 11.6 |
| 反射 シェル | 解像度: 0.75→0.78 Å / 冗長度: 3.43 % / Rmerge(I) obs: 0.33 / Mean I/σ(I) obs: 3.63 / % possible all: 90.4 |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法: DIRECT METHODS 開始モデル: NONE 解像度: 0.75→10 Å / Num. parameters: 16518 / Num. restraintsaints: 21007 / 交差検証法: FREE R-VALUE / σ(F): 0 / 立体化学のターゲット値: ENGH AND HUBER
| |||||||||||||||||||||||||||||||||
| Refine analyze | Num. disordered residues: 20 / Occupancy sum hydrogen: 1253.37 / Occupancy sum non hydrogen: 1660.65 | |||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 0.75→10 Å
| |||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー

















































 PDBj
PDBj