-検索条件
-検索結果
検索 (著者・登録者: jiang & l)の結果2,251件中、1から50件目までを表示しています

EMDB-39582: 
Cryo-EM structure of the amthamine-bound H2R-Gs complex

EMDB-39583: 
Cryo-EM structure of the histamine-bound H3R-Gi complex

EMDB-39584: 
Cryo-EM structure of the immepip-bound H3R-Gi complex

PDB-8yut: 
Cryo-EM structure of the amthamine-bound H2R-Gs complex

PDB-8yuu: 
Cryo-EM structure of the histamine-bound H3R-Gi complex

PDB-8yuv: 
Cryo-EM structure of the immepip-bound H3R-Gi complex

EMDB-39064: 
Structure of NET-Maprotiline in outward-open state
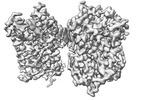
EMDB-39065: 
Structure of NET-Nefopam in outward-open state

EMDB-39066: 
Structure of NET-nomifensine in outward-open state

EMDB-39067: 
structure of NET-Atomoxetine in outward-open state

EMDB-39068: 
Structure of NET-Amitriptyline in outward-open state

EMDB-39069: 
Structure of Apo human norepinephrine transporter NET

EMDB-39070: 
Structure of NET-NE in Occluded state

EMDB-39533: 
Structure of NET-Nisoxetine in outward-open state

PDB-8y8z: 
Structure of NET-Maprotiline in outward-open state

PDB-8y90: 
Structure of NET-Nefopam in outward-open state

PDB-8y91: 
Structure of NET-nomifensine in outward-open state

PDB-8y92: 
structure of NET-Atomoxetine in outward-open state

PDB-8y93: 
Structure of NET-Amitriptyline in outward-open state

PDB-8y94: 
Structure of Apo human norepinephrine transporter NET

PDB-8y95: 
Structure of NET-NE in Occluded state

PDB-8yr2: 
Structure of NET-Nisoxetine in outward-open state

EMDB-41248: 
Structure of AT118-H Nanobody Antagonist in Complex with the Angiotensin II Type I Receptor

EMDB-41249: 
Structure of AT118-L Nanobody Antagonist in Complex with the Angiotensin II Type I Receptor and Losartan

PDB-8th3: 
Structure of AT118-H Nanobody Antagonist in Complex with the Angiotensin II Type I Receptor

PDB-8th4: 
Structure of AT118-L Nanobody Antagonist in Complex with the Angiotensin II Type I Receptor and Losartan

EMDB-36484: 
Cryo-EM structure of succinate receptor bound to cis-epoxysuccinic acid coupling to Gi

EMDB-36486: 
Cryo-EM structure of succinate receptor bound to succinate acid coupling MiniGsq

PDB-8jpn: 
Cryo-EM structure of succinate receptor bound to cis-epoxysuccinic acid coupling to Gi

PDB-8jpp: 
Cryo-EM structure of succinate receptor bound to succinate acid coupling MiniGsq

EMDB-36907: 
Cryo-EM structure of the RC-LH core comples from Halorhodospira halochloris

PDB-8k5o: 
Cryo-EM structure of the RC-LH core comples from Halorhodospira halochloris

EMDB-37727: 
Cryo-ET structure of RuBisCO from 3.9 angstroms Synechococcus elongatus PCC 7942

EMDB-37728: 
Cryo-ET map of RuBisCO at 4.4 angstroms from Synechococcus elongatus PCC 7942 beta-carboxysome

EMDB-37729: 
Cryo-ET map of RuBisCO-SSUL at 5.9 angstroms from Synechococcus elongatus PCC 7942 beta-carboxysome

EMDB-37730: 
Cryo-ET map of RuBisCO at the outermost layer that is loosely attached to the shell of Synechococcus elongatus PCC 7942 beta-carboxysome

EMDB-37731: 
Cryo-ET map of RuBisCO at the outermost layer that is tightly attached to the shell of Synechococcus elongatus PCC 7942 beta-carboxysome

PDB-8wpz: 
Cryo-ET structure of RuBisCO at 3.9 angstroms from Synechococcus elongatus PCC 7942
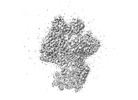
EMDB-36068: 
Monkeypox virus DNA replication holoenzyme F8, A22 and E4 in complex with a DNA duplex and dCTP

EMDB-36069: 
Monkeypox virus DNA replication holoenzyme F8, A22 and E4 in complex with a DNA duplex and cidofovir diphosphate

PDB-8j8f: 
Monkeypox virus DNA replication holoenzyme F8, A22 and E4 in complex with a DNA duplex and dCTP

PDB-8j8g: 
Monkeypox virus DNA replication holoenzyme F8, A22 and E4 in complex with a DNA duplex and cidofovir diphosphate
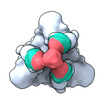
EMDB-36850: 
SARS-CoV-2 Omicron BA.1 spike protein in complex with a self-assembling trivalent nanobody Tr67

EMDB-36061: 
Monkeypox virus DNA replication holoenzyme F8, A22 and E4 complex in a DNA binding form

PDB-8j86: 
Monkeypox virus DNA replication holoenzyme F8, A22 and E4 complex in a DNA binding form
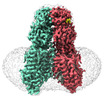
EMDB-36008: 
SIDT1 protein
EMDB-36009: 
transport T2

PDB-8j6m: 
SIDT1 protein

PDB-8j6o: 
transport T2

EMDB-36594: 
Cryo-EM structure of a designed AAV8-based vector
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
