+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 2bxi | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
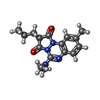
| タイトル | Human serum albumin complexed with myristate and azapropazone | |||||||||
 要素 要素 | SERUM ALBUMIN | |||||||||
 キーワード キーワード | TRANSPORT PROTEIN / ALBUMIN / CARRIER PROTEIN / LIPID-BINDING / METAL-BINDING / DRUG-BINDING / AZAPROPAZONE / MYRISTATE | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報bilirubin transport / Ciprofloxacin ADME / exogenous protein binding / cellular response to calcium ion starvation / enterobactin binding / Heme biosynthesis / HDL remodeling / molecular carrier activity / negative regulation of mitochondrial depolarization / Prednisone ADME ...bilirubin transport / Ciprofloxacin ADME / exogenous protein binding / cellular response to calcium ion starvation / enterobactin binding / Heme biosynthesis / HDL remodeling / molecular carrier activity / negative regulation of mitochondrial depolarization / Prednisone ADME / Heme degradation / Aspirin ADME / antioxidant activity / Scavenging of heme from plasma / toxic substance binding / Recycling of bile acids and salts / platelet alpha granule lumen / fatty acid binding / cellular response to starvation / Post-translational protein phosphorylation / Cytoprotection by HMOX1 / response to nutrient levels / Regulation of Insulin-like Growth Factor (IGF) transport and uptake by Insulin-like Growth Factor Binding Proteins (IGFBPs) / Platelet degranulation / pyridoxal phosphate binding / protein-folding chaperone binding / blood microparticle / endoplasmic reticulum lumen / copper ion binding / endoplasmic reticulum / Golgi apparatus / protein-containing complex / : / DNA binding / extracellular exosome / extracellular region / identical protein binding / nucleus 類似検索 - 分子機能 | |||||||||
| 生物種 |  HOMO SAPIENS (ヒト) HOMO SAPIENS (ヒト) | |||||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.5 Å 分子置換 / 解像度: 2.5 Å | |||||||||
 データ登録者 データ登録者 | Ghuman, J. / Zunszain, P.A. / Petitpas, I. / Bhattacharya, A.A. / Curry, S. | |||||||||
 引用 引用 |  ジャーナル: J.Mol.Biol. / 年: 2005 ジャーナル: J.Mol.Biol. / 年: 2005タイトル: Structural Basis of the Drug-Binding Specificity of Human Serum Albumin. 著者: Ghuman, J. / Zunszain, P.A. / Petitpas, I. / Bhattacharya, A.A. / Otagiri, M. / Curry, S. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  2bxi.cif.gz 2bxi.cif.gz | 127.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb2bxi.ent.gz pdb2bxi.ent.gz | 99.3 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  2bxi.json.gz 2bxi.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/bx/2bxi https://data.pdbj.org/pub/pdb/validation_reports/bx/2bxi ftp://data.pdbj.org/pub/pdb/validation_reports/bx/2bxi ftp://data.pdbj.org/pub/pdb/validation_reports/bx/2bxi | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  2bx8C  2bxaC  2bxbC  2bxcC  2bxdC  2bxeC  2bxfC  2bxgC  2bxhC  2bxkC  2bxlC  2bxmC  2bxnC  2bxoC  2bxpC  2bxqC  1e7gS S: 精密化の開始モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 66543.141 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  HOMO SAPIENS (ヒト) / 組織: PLASMA / 発現宿主: HOMO SAPIENS (ヒト) / 組織: PLASMA / 発現宿主:  PICHIA PASTORIS (菌類) / 参照: UniProt: P02768 PICHIA PASTORIS (菌類) / 参照: UniProt: P02768 | ||||||||
|---|---|---|---|---|---|---|---|---|---|
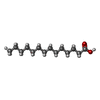
| #2: 化合物 | ChemComp-MYR / #3: 化合物 | #4: 水 | ChemComp-HOH / | Has protein modification | Y | 配列の詳細 | SEQUENCE CONTAINS SIGNAL AND PRO-PEPTIDE 9RESIDUES 1-24 IN DATABASE ENTRY. PROTEIN CRYSTALLISED WAS ...SEQUENCE CONTAINS SIGNAL AND PRO-PEPTIDE 9RESIDUES 1-24 IN DATABASE ENTRY. PROTEIN CRYSTALLIS | |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.54 Å3/Da / 溶媒含有率: 44 % |
|---|---|
| 結晶化 | pH: 7 / 詳細: pH 7.00 |
-データ収集
| 回折 | 平均測定温度: 298 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  EMBL/DESY, HAMBURG EMBL/DESY, HAMBURG  / ビームライン: X13 / 波長: 0.8013 / ビームライン: X13 / 波長: 0.8013 |
| 検出器 | タイプ: MARRESEARCH / 検出器: CCD / 日付: 2001年12月1日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 0.8013 Å / 相対比: 1 |
| 反射 | 解像度: 2.45→34.4 Å / Num. obs: 24928 / % possible obs: 99.3 % / Observed criterion σ(I): 0 / 冗長度: 2.5 % / Biso Wilson estimate: 57.3 Å2 / Rmerge(I) obs: 0.05 / Net I/σ(I): 10.9 |
| 反射 シェル | 解像度: 2.45→2.58 Å / 冗長度: 2.5 % / Rmerge(I) obs: 0.38 / Mean I/σ(I) obs: 3.2 / % possible all: 99.9 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: PDB ENTRY 1E7G 解像度: 2.5→34.42 Å / Rfactor Rfree error: 0.008 / Data cutoff high absF: 1759630.51 / Isotropic thermal model: GROUP / 交差検証法: THROUGHOUT / σ(F): 0 / 立体化学のターゲット値: MLF
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 溶媒モデル: FLAT MODEL / Bsol: 42.0902 Å2 / ksol: 0.295701 e/Å3 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 56.2 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.5→34.42 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 2.45→2.6 Å / Rfactor Rfree error: 0.036 / Total num. of bins used: 6
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Xplor file |
|
 ムービー
ムービー コントローラー
コントローラー










































 PDBj
PDBj