-検索条件
-検索結果
検索 (著者・登録者: shaw & s)の結果438件中、1から50件目までを表示しています

EMDB-50814: 
Real space helical reconstruction of cofilin actin in the microtubule lumen of human platelets

EMDB-50845: 
Real space helical reconstruction of cofilin actin in the microtubule lumen of HAP1 cells

PDB-8tym: 
Cryo-EM of the GDP-bound human dynamin (full-length) polymer assembled on the membrane in the super constricted state

PDB-8tyn: 
Cryo-EM of the GDP-bound human dynamin polymer assembled on the membrane in the super constricted state (tetramer model)

EMDB-41024: 
MD65 N332-GT5 SOSIP in complex with RM_N332_03 Fab and RM20A3 Fab

EMDB-41025: 
MD65 N332-GT5 SOSIP in complex with RM_N332_36 Fab and RM20A3 Fab

EMDB-41026: 
MD65 N332-GT5 SOSIP in complex with RM_N332_32 Fab and RM20A3

EMDB-41027: 
MD65 N332-GT5 SOSIP in complex with RM_N332_08 Fab and RM20A3 Fab

EMDB-41034: 
MD64 N332-GT5 SOSIP

EMDB-41035: 
MD65 N332-GT5 SOSIP in complex with RM_N332_07 Fab and RM20A3 Fab

PDB-8t49: 
MD65 N332-GT5 SOSIP in complex with RM_N332_03 Fab and RM20A3 Fab

PDB-8t4a: 
MD65 N332-GT5 SOSIP in complex with RM_N332_36 Fab and RM20A3 Fab

PDB-8t4b: 
MD65 N332-GT5 SOSIP in complex with RM_N332_32 Fab and RM20A3

PDB-8t4d: 
MD65 N332-GT5 SOSIP in complex with RM_N332_08 Fab and RM20A3 Fab

PDB-8t4k: 
MD64 N332-GT5 SOSIP

PDB-8t4l: 
MD65 N332-GT5 SOSIP in complex with RM_N332_07 Fab and RM20A3 Fab

EMDB-40861: 
Cryo-EM of the GDP-bound human dynamin polymer assembled on the membrane in the super constricted state
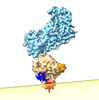
EMDB-40901: 
Cryo-EM of the GDP-bound human dynamin polymer assembled on the membrane in the super constricted state showing the PH domain
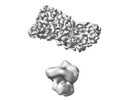
EMDB-40902: 
Cryo-EM of the GDP-bound human dynamin polymer assembled on the membrane in the super constricted state showing the second PH domain

EMDB-40903: 
Cryo-EM of the GDP-bound human dynamin polymer assembled on the membrane in the super constricted state (full helix)

EMDB-40942: 
Cryo-EM of the GDP-bound human dynamin (full-length) polymer assembled on the membrane in the super constricted state

EMDB-40946: 
Cryo-EM of the GDP-bound human dynamin (full-length) polymer assembled on the membrane in the super constricted state (full helix)

PDB-8sxz: 
Cryo-EM of the GDP-bound human dynamin polymer assembled on the membrane in the super constricted state

PDB-8sz4: 
Cryo-EM of the GDP-bound human dynamin polymer assembled on the membrane in the super constricted state showing the PH domain

PDB-8sz7: 
Cryo-EM of the GDP-bound human dynamin polymer assembled on the membrane in the super constricted state showing the second PH domain

PDB-8sz8: 
Cryo-EM of the GDP-bound human dynamin polymer assembled on the membrane in the super constricted state (full helix)

PDB-8t0k: 
Cryo-EM of the GDP-bound human dynamin (full-length) polymer assembled on the membrane in the super constricted state

PDB-8t0r: 
Cryo-EM of the GDP-bound human dynamin (full-length) polymer assembled on the membrane in the super constricted state (full helix)

EMDB-40180: 
MsbA bound to cerastecin C

PDB-8gk7: 
MsbA bound to cerastecin C

EMDB-40918: 
Human glutaminase C (Y466W) with L-Gln and Pi, filamentous form

EMDB-40920: 
Human liver-type glutaminase (Apo form)
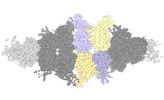
EMDB-40950: 
Human liver-type glutaminase (K253A) with L-Gln, filamentous form

EMDB-43533: 
Human liver-type glutaminase, bound with inhibitor Compound 968

PDB-8szj: 
Human glutaminase C (Y466W) with L-Gln and Pi, filamentous form

PDB-8szl: 
Human liver-type glutaminase (Apo form)

PDB-8t0z: 
Human liver-type glutaminase (K253A) with L-Gln, filamentous form

EMDB-41805: 
Cryo-EM structure of murine Thrombopoietin receptor ectodomain in complex with Tpo

PDB-8u18: 
Cryo-EM structure of murine Thrombopoietin receptor ectodomain in complex with Tpo

EMDB-41374: 
Antibody N3-1 bound to RBDs in the up and down conformations

EMDB-41382: 
Antibody N3-1 bound to RBD in the up conformation

EMDB-41399: 
Antibody N3-1 bound to SARS-CoV-2 spike

PDB-8tm1: 
Antibody N3-1 bound to RBDs in the up and down conformations

PDB-8tma: 
Antibody N3-1 bound to RBD in the up conformation

EMDB-40856: 
Single particle reconstruction of the human LINE-1 ORF2p without substrate (apo)
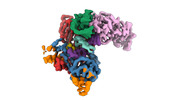
EMDB-40858: 
Structure of LINE-1 ORF2p with template:primer hybrid
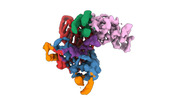
EMDB-40859: 
Structure of LINE-1 ORF2p with an oligo(A) template

PDB-8sxt: 
Structure of LINE-1 ORF2p with template:primer hybrid

PDB-8sxu: 
Structure of LINE-1 ORF2p with an oligo(A) template
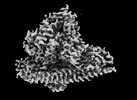
EMDB-41617: 
CryoEM structure of PI3Kalpha
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
