-検索条件
-検索結果
検索 (著者・登録者: ping & y)の結果1,983件中、1から50件目までを表示しています

EMDB-38216: 
Cryo-EM structure of SARS-CoV-2 S-BQ.1 in complex with antibody O5C2

PDB-8xbf: 
Cryo-EM structure of SARS-CoV-2 S-BQ.1 in complex with antibody O5C2

EMDB-35827: 
Structure of CbCas9 bound to 20-nucleotide complementary DNA substrate

EMDB-37652: 
Structure of CbCas9 bound to 6-nucleotide complementary DNA substrate

EMDB-37656: 
Structure of CbCas9-PcrIIC1 complex bound to 28-bp DNA substrate (20-nt complementary)

EMDB-37657: 
Structure of CbCas9-PcrIIC1 complex bound to 62-bp DNA substrate (symmetric 20-nt complementary)

EMDB-37762: 
Structure of CbCas9-PcrIIC1 complex bound to 62-bp DNA substrate (non-targeting complex)

PDB-8iyq: 
Structure of CbCas9 bound to 20-nucleotide complementary DNA substrate

PDB-8wmh: 
Structure of CbCas9 bound to 6-nucleotide complementary DNA substrate

PDB-8wmm: 
Structure of CbCas9-PcrIIC1 complex bound to 28-bp DNA substrate (20-nt complementary)

PDB-8wmn: 
Structure of CbCas9-PcrIIC1 complex bound to 62-bp DNA substrate (symmetric 20-nt complementary)

PDB-8wr4: 
Structure of CbCas9-PcrIIC1 complex bound to 62-bp DNA substrate (non-targeting complex)

EMDB-36960: 
F8-A22-E4 complex of MPXV in complex with DNA and Ara-CTP

EMDB-36962: 
F8-A22-E4 complex of MPXV in complex with DNA and dCTP

EMDB-36963: 
the local map of DNA and Ara-CTP binding site

EMDB-36964: 
the local map of DNA and dCTP binding site

PDB-8k8s: 
F8-A22-E4 complex of MPXV in complex with DNA and Ara-CTP

PDB-8k8u: 
F8-A22-E4 complex of MPXV in complex with DNA and dCTP

EMDB-41409: 
Cryo-EM structure of PCSK9 mimic HIT01-K21Q-R218E with AMG145 Fab

EMDB-36907: 
Cryo-EM structure of the RC-LH core comples from Halorhodospira halochloris

PDB-8k5o: 
Cryo-EM structure of the RC-LH core comples from Halorhodospira halochloris

EMDB-41152: 
Cryo-EM Structure of Spike Glycoprotein from Civet Coronavirus SZ3 in Closed Conformation

PDB-8tc5: 
Cryo-EM Structure of Spike Glycoprotein from Civet Coronavirus SZ3 in Closed Conformation

EMDB-36366: 
Cryo-EM structure of Symbiodinium photosystem I

PDB-8jjr: 
Cryo-EM structure of Symbiodinium photosystem I

EMDB-36776: 
The Anoxybacillus pushchinoensis ORF-less Group IIC Intron HYER1 at symmetric apo state

EMDB-36777: 
The Anoxybacillus pushchinoensis ORF-less Group IIC Intron DR1 at symmetric pre-cleavage state

EMDB-36778: 
The Anoxybacillus pushchinoensis ORF-less Group IIC Intron HYER1 at symmetric post cleavge state

EMDB-36786: 
The Streptococcus azizii ORF-less Group IIC intron HYER2 at apo state

PDB-8k0p: 
The Anoxybacillus pushchinoensis ORF-less Group IIC Intron HYER1 at symmetric apo state

PDB-8k0q: 
The Anoxybacillus pushchinoensis ORF-less Group IIC Intron HYER1 at symmetric pre-cleavage state

PDB-8k0r: 
The Anoxybacillus pushchinoensis ORF-less Group IIC Intron HYER1 at symmetric post cleavge state

PDB-8k15: 
The Streptococcus azizii ORF-less Group IIC intron HYER2 at apo state

EMDB-36659: 
Structure of human TRPV4 with antagonist A1

EMDB-36660: 
Structure of human TRPV4 with antagonist GSK279
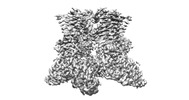
EMDB-36675: 
Structure of human TRPV4 with antagonist A2

EMDB-36676: 
Structure of human TRPV4 with antagonist A2 and RhoA

PDB-8ju5: 
Structure of human TRPV4 with antagonist A1

PDB-8ju6: 
Structure of human TRPV4 with antagonist GSK279

PDB-8jvi: 
Structure of human TRPV4 with antagonist A2

PDB-8jvj: 
Structure of human TRPV4 with antagonist A2 and RhoA

EMDB-41149: 
Cryo-EM Structure of Spike Glycoprotein from Bat Coronavirus WIV1 in Closed Conformation

EMDB-41150: 
Cryo-EM Structure of Spike Glycoprotein from Civet Coronavirus 007 in Closed Conformation

PDB-8tc0: 
Cryo-EM Structure of Spike Glycoprotein from Bat Coronavirus WIV1 in Closed Conformation

PDB-8tc1: 
Cryo-EM Structure of Spike Glycoprotein from Civet Coronavirus 007 in Closed Conformation
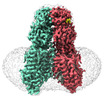
EMDB-36008: 
SIDT1 protein
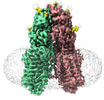
EMDB-36009: 
transport T2

PDB-8j6m: 
SIDT1 protein

PDB-8j6o: 
transport T2

EMDB-36779: 
The Anoxybacillus pushchinoensis ORF-less Group IIC Intron HYER1 with 10-nt TRS at symmetric apo state
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
