-検索条件
-検索結果
検索 (著者・登録者: lee & sc)の結果948件中、1から50件目までを表示しています

EMDB-42527: 
Pre-fusion Measles virus fusion protein complexed with Fab 77

EMDB-42539: 
Structure of the Measles virus Fusion protein in the post-fusion conformation

EMDB-42593: 
Structure of the Measles virus Fusion protein in the pre-fusion conformation

EMDB-42595: 
Structure of the Measles virus Fusion protein in the pre-fusion conformation with bound [FIP-HRC]2-PEG11

EMDB-43827: 
Fab 77-stabilized MeV F ectodomain fragment

PDB-8ut2: 
Pre-fusion Measles virus fusion protein complexed with Fab 77

PDB-8utf: 
Structure of the Measles virus Fusion protein in the post-fusion conformation

PDB-8uup: 
Structure of the Measles virus Fusion protein in the pre-fusion conformation

PDB-8uuq: 
Structure of the Measles virus Fusion protein in the pre-fusion conformation with bound [FIP-HRC]2-PEG11

PDB-9at8: 
Fab 77-stabilized MeV F ectodomain fragment

EMDB-41041: 
Open human HCN1 F186C S264C bound to cAMP, reconstituted in LMNG + SPL

PDB-8t50: 
Open human HCN1 F186C S264C bound to cAMP, reconstituted in LMNG + SPL

EMDB-41040: 
Human HCN1 F186C S264C C309A bound to cAMP, reconstituted in LMNG + SPL

PDB-8t4y: 
Human HCN1 F186C S264C C309A bound to cAMP, reconstituted in LMNG + SPL

EMDB-17377: 
Structure of human SIT1 (focussed map / refinement)

EMDB-17378: 
Structure of human SIT1:ACE2 complex (open PD conformation)

EMDB-17379: 
Structure of human SIT1:ACE2 complex (closed PD conformation)

EMDB-17380: 
Structure of human SIT1 bound to L-pipecolate (focussed map / refinement)

EMDB-17381: 
Structure of human SIT1:ACE2 complex (open PD conformation) bound to L-pipecolate

EMDB-17382: 
Structure of human SIT1:ACE2 complex (closed PD conformation) bound to L-pipecolate

EMDB-41036: 
Closed human HCN1 F186C S264C bound to cAMP, reconstituted in LMNG + SPL

PDB-8t4m: 
Closed human HCN1 F186C S264C bound to cAMP, reconstituted in LMNG + SPL

EMDB-28966: 
CryoEM map of de novo designed oligomeric protein C4-71_6x

EMDB-28967: 
CryoEM map of de novo designed oligomeric protein C4-71_8x
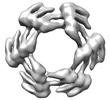
EMDB-28968: 
CryoEM map of de novo designed oligomeric protein C6-71

EMDB-28969: 
CryoEM map of de novo designed oligomeric protein C6-71_6x

EMDB-28970: 
CryoEM map of de novo designed oligomeric protein C6-71_8x

EMDB-28971: 
CryoEM map of de novo designed oligomeric protein C8-71_6x

EMDB-28972: 
CryoEM map of de novo designed oligomeric protein C8-71_8x
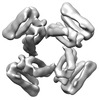
EMDB-28973: 
CryoEM map of de novo designed oligomeric protein C4-81

EMDB-28974: 
CryoEM map of designed oligomeric protein C4-71

EMDB-19014: 
PDCoV spike glycoprotein ectodomain in complex with the 22C10 antibody Fab fragment

EMDB-19015: 
Local refinement of the PDCoV spike glycoprotein ectodomain in complex with the 22C10 antibody Fab fragment

EMDB-19016: 
S1B domain of the PDCoV spike glycoprotein in complex with the 67B12 and 42H3 antibody Fab fragments

EMDB-19017: 
S1B domain of the PDCoV spike glycoprotein in complex with the 67B12 and 46E6 antibody Fab fragments

PDB-8r9w: 
PDCoV spike glycoprotein ectodomain in complex with the 22C10 antibody Fab fragment

PDB-8r9x: 
Local refinement of the PDCoV spike glycoprotein ectodomain in complex with the 22C10 antibody Fab fragment

PDB-8r9y: 
S1B domain of the PDCoV spike glycoprotein in complex with the 67B12 and 42H3 antibody Fab fragments

PDB-8r9z: 
S1B domain of the PDCoV spike glycoprotein in complex with the 67B12 and 46E6 antibody Fab fragments
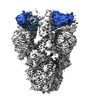
EMDB-39546: 
SARS-CoV-2 Delta Spike in complex with JL-8C

EMDB-39547: 
SARS-CoV-2 Delta Spike in complex with JM-1A

EMDB-39685: 
SARS-CoV-2 Delta Spike in complex with Fab of JE-5C

EMDB-39686: 
SARS-CoV-2 Spike (BA.1) in complex with Fab of JH-8B

PDB-8yro: 
SARS-CoV-2 Delta Spike in complex with JL-8C

PDB-8yrp: 
SARS-CoV-2 Delta Spike in complex with JM-1A

PDB-8yz5: 
SARS-CoV-2 Delta Spike in complex with Fab of JE-5C

PDB-8yz6: 
SARS-CoV-2 Spike (BA.1) in complex with Fab of JH-8B

EMDB-29330: 
N332-GT5 SOSIP in complex with base polyclonal Fabs isolated at day 42 from protein immunized wild type mice

EMDB-29333: 
N332-GT5 SOSIP in complex with base polyclonal Fabs isolated at day 42 from protein immunized BG18HCgl knock-in mice

EMDB-29334: 
N332-GT5 SOSIP in complex with V1V3 polyclonal Fabs isolated at day 16 from mRNA immunized wild type mice
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
