-検索条件
-検索結果
検索 (著者・登録者: gao & q)の結果1,697件中、1から50件目までを表示しています

EMDB-38966: 
Cryo-EM structure of human urate transporter GLUT9 bound to substrate urate

EMDB-38968: 
Cryo-EM structure of human urate transporter GLUT9 bound to inhibitor apigenin

PDB-8y65: 
Cryo-EM structure of human urate transporter GLUT9 bound to substrate urate

PDB-8y66: 
Cryo-EM structure of human urate transporter GLUT9 bound to inhibitor apigenin

EMDB-36892: 
Structure of BtKY72 spike receptor-binding domain (RBD) complexed with bat ACE2

PDB-8k4u: 
Structure of BtKY72 spike receptor-binding domain (RBD) complexed with bat ACE2

EMDB-37756: 
Cryo-EM structure of bsAb3 Fab-Gn-Gc complex

PDB-8wqw: 
Cryo-EM structure of bsAb3 Fab-Gn-Gc complex

EMDB-38613: 
Structure of MPXV B6 and D68 fab complex

PDB-8xs3: 
Structure of MPXV B6 and D68 fab complex

EMDB-35827: 
Structure of CbCas9 bound to 20-nucleotide complementary DNA substrate

EMDB-37652: 
Structure of CbCas9 bound to 6-nucleotide complementary DNA substrate

EMDB-37656: 
Structure of CbCas9-PcrIIC1 complex bound to 28-bp DNA substrate (20-nt complementary)

EMDB-37657: 
Structure of CbCas9-PcrIIC1 complex bound to 62-bp DNA substrate (symmetric 20-nt complementary)

EMDB-37762: 
Structure of CbCas9-PcrIIC1 complex bound to 62-bp DNA substrate (non-targeting complex)

PDB-8iyq: 
Structure of CbCas9 bound to 20-nucleotide complementary DNA substrate

PDB-8wmh: 
Structure of CbCas9 bound to 6-nucleotide complementary DNA substrate

PDB-8wmm: 
Structure of CbCas9-PcrIIC1 complex bound to 28-bp DNA substrate (20-nt complementary)

PDB-8wmn: 
Structure of CbCas9-PcrIIC1 complex bound to 62-bp DNA substrate (symmetric 20-nt complementary)

PDB-8wr4: 
Structure of CbCas9-PcrIIC1 complex bound to 62-bp DNA substrate (non-targeting complex)
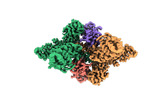
EMDB-36599: 
Structure of E6AP-E6 complex in Att1 state
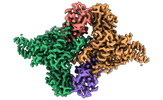
EMDB-36600: 
Structure of E6AP-E6 complex in Att2 state
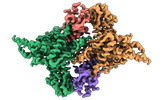
EMDB-36601: 
Structure of E6AP-E6 complex in Att3 state
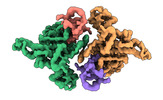
EMDB-36602: 
Structure of E6AP-E6 complex in Det1 state
EMDB-36603: 
Structure of E6AP-E6 complex in Det2 state

EMDB-36604: 
Structure of human full-length E6AP

PDB-8jrn: 
Structure of E6AP-E6 complex in Att1 state

PDB-8jro: 
Structure of E6AP-E6 complex in Att2 state

PDB-8jrp: 
Structure of E6AP-E6 complex in Att3 state

PDB-8jrq: 
Structure of E6AP-E6 complex in Det1 state

PDB-8jrr: 
Structure of E6AP-E6 complex in Det2 state

EMDB-39920: 
SARS-CoV-2 Omicron BA.2 spike trimer (6P) in complex with D1F6 Fab, head-to-head aggregate

EMDB-39924: 
SARS-CoV-2 Omicron BA.4 spike trimer (6P) in complex with D1F6 Fab, head-to-head aggregate

PDB-8zc2: 
SARS-CoV-2 Omicron BA.2 spike trimer (6P) in complex with D1F6 Fab, head-to-head aggregate

PDB-8zc6: 
SARS-CoV-2 Omicron BA.4 spike trimer (6P) in complex with D1F6 Fab, head-to-head aggregate

EMDB-38156: 
Structure of enterovirus protease in complex host factor

PDB-8x8q: 
Structure of enterovirus protease in complex host factor

EMDB-36672: 
Cryo-EM structure of the N-terminal domain of Omicron BA.1 in complex with nanobody N235 and S2L20 Fab

PDB-8jva: 
Cryo-EM structure of the N-terminal domain of Omicron BA.1 in complex with nanobody N235 and S2L20 Fab

EMDB-37606: 
Cryo-EM structure of DSR2-TUBE complex

EMDB-37607: 
Cryo-EM structure of DSR2-DSAD1 complex

EMDB-37610: 
Cryo-EM structure of DSR2

PDB-8wks: 
Cryo-EM structure of DSR2-TUBE complex

PDB-8wkt: 
Cryo-EM structure of DSR2-DSAD1 complex

PDB-8wkx: 
Cryo-EM structure of DSR2

EMDB-39916: 
SARS-CoV-2 Omicron BA.1 spike trimer (x2-4P) in complex with 3 D1F6 Fabs (0 RBD up)

EMDB-39917: 
SARS-CoV-2 Omicron BA.2 spike trimer (6P) in complex with 3 D1F6 Fabs (1 RBD up)

EMDB-39918: 
SARS-CoV-2 Omicron BA.2 spike trimer (6P) in complex with 3 D1F6 Fabs (2 RBD up)

EMDB-39919: 
SARS-CoV-2 Omicron BA.2 spike trimer (6P) in complex with D1F6 Fab, focused refinement of RBD region

EMDB-39921: 
SARS-CoV-2 Omicron BA.4 spike trimer (6P) in complex with 3 D1F6 Fabs (1 RBD up)
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
