-検索条件
-検索結果
検索 (著者・登録者: blanco & j)の結果104件中、1から50件目までを表示しています

EMDB-38453: 
Structure of the SARS-CoV-2 EG.5.1 spike glycoprotein in complex with ACE2 (1-up state)

EMDB-38454: 
Structure of the SARS-CoV-2 EG.5.1 spike RBD in complex with ACE2

PDB-8xlm: 
Structure of the SARS-CoV-2 EG.5.1 spike glycoprotein in complex with ACE2 (1-up state)

PDB-8xln: 
Structure of the SARS-CoV-2 EG.5.1 spike RBD in complex with ACE2

EMDB-37648: 
SARS-CoV-2 EG.5.1 spike glycoprotein (1-up state)

EMDB-37650: 
SARS-CoV-2 EG.5.1 spike glycoprotein (closed-2 state)

EMDB-37651: 
SARS-CoV-2 EG.5.1 spike glycoprotein (closed-1 state)

PDB-8wmd: 
Structure of the SARS-CoV-2 EG.5.1 spike glycoprotein (closed-2 state)

PDB-8wmf: 
Structure of the SARS-CoV-2 EG.5.1 spike glycoprotein (closed-1 state)
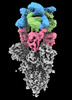
EMDB-16453: 
SARS-CoV-2 Omicron Variant Spike Trimer in complex with three 17T2 Fabs

EMDB-16473: 
SARS-CoV-2 spike in complex with the 17T2 neutralizing antibody Fab fragment (local refinement of RBD and Fab)

PDB-8c89: 
SARS-CoV-2 spike in complex with the 17T2 neutralizing antibody Fab fragment (local refinement of RBD and Fab)

EMDB-13177: 
Ser40 phosphorylated tyrosine hydroxylase

EMDB-23757: 
Cryo-electron microscopy structure of TnsC(1-503)A225V bound to DNA

PDB-7mcs: 
Cryo-electron microscopy structure of TnsC(1-503)A225V bound to DNA

EMDB-13442: 
Partial structure of tyrosine hydroxylase lacking the first 35 residues in complex with dopamine.

PDB-7pim: 
Partial structure of tyrosine hydroxylase lacking the first 35 residues in complex with dopamine.

EMDB-11309: 
Partial structure of tyrosine hydroxylase in complex with dopamine showing the catalytic domain and an alpha-helix from the regulatory domain involved in dopamine binding.

PDB-6zn2: 
Partial structure of tyrosine hydroxylase in complex with dopamine showing the catalytic domain and an alpha-helix from the regulatory domain involved in dopamine binding.

EMDB-11624: 
Full-length structure of the substrate-free tyrosine hydroxylase (apo-TH).

PDB-7a2g: 
Full-length structure of the substrate-free tyrosine hydroxylase (apo-TH).

EMDB-11467: 
Atomic model of the EM-based structure of the full-length tyrosine hydroxylase in complex with dopamine (residues 40-497) in which the regulatory domain (residues 40-165) has been included only with the backbone atoms

EMDB-11587: 
Partial structure of the substrate-free tyrosine hydroxylase (apo-TH).

PDB-6zvp: 
Atomic model of the EM-based structure of the full-length tyrosine hydroxylase in complex with dopamine (residues 40-497) in which the regulatory domain (residues 40-165) has been included only with the backbone atoms

PDB-6zzu: 
Partial structure of the substrate-free tyrosine hydroxylase (apo-TH).

EMDB-22490: 
Structure of human TRPA1 in complex with antagonist compound 21

PDB-7jup: 
Structure of human TRPA1 in complex with antagonist compound 21

EMDB-21688: 
Structure of human TRPA1 in complex with inhibitor GDC-0334

PDB-6wj5: 
Structure of human TRPA1 in complex with inhibitor GDC-0334

EMDB-21558: 
30S-Activated-high-Mg2+

EMDB-21569: 
30S-Inactivated-high-Mg2+ Class A

EMDB-21570: 
30S-Inactive-high-Mg2+ Class B

EMDB-21571: 
30S-Inactive-high-Mg2+ + carbon layer

EMDB-21572: 
30S-Inactive-low-Mg2+ Class A

EMDB-21573: 
30S-Inactive-low-Mg2+ Class B

EMDB-22690: 
30S-Inactive-low-Mg2+ Carbon

PDB-6w6k: 
30S-Activated-high-Mg2+

PDB-6w77: 
30S-Inactivated-high-Mg2+ Class A

PDB-6w7m: 
30S-Inactive-high-Mg2+ + carbon layer

PDB-6w7n: 
30S-Inactive-low-Mg2+ Class A

PDB-6w7w: 
30S-Inactive-low-Mg2+ Class B

EMDB-4551: 
Near Atomic Structure of an Atadenovirus Shows a possible gene duplication event and Intergenera Variations in Cementing Proteins

PDB-6qi5: 
Near Atomic Structure of an Atadenovirus Shows a possible gene duplication event and Intergenera Variations in Cementing Proteins

EMDB-11008: 
Icosahedral reconstruction of human adenovirus D26 capsid

EMDB-11012: 
Localized reconstruction of human adenovirus D26 hexon type 3

EMDB-11009: 
Localized reconstruction of the trimeric fibre and its interactions with the penton base of human adenovirus HAdV-D26

EMDB-11010: 
Localized reconstruction of human adenovirus D26 hexon type 1

EMDB-11011: 
Localized reconstruction of human adenovirus D26 hexon type 2

EMDB-11013: 
Localized reconstruction of human adenovirus D26 hexon type 4

EMDB-10080: 
Human polymerase delta holoenzyme Conformer 1
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
