-検索条件
-検索結果
検索 (著者・登録者: yao & m)の結果1,113件中、1から50件目までを表示しています

EMDB-42287: 
Cryo-EM map of human clmap-clamp loader ATAD5-RFC-gapped PCNA complex in intermediate state 3

EMDB-42288: 
Cryo-EM map of human clamp-clamp loader ATAD5-RFC-two PCNAs complex in intermediate state 3

EMDB-42289: 
Cryo-EM map of human clamp-clamp loader ATAD5-RFC-cracked PCNA complex in intermediate state 2

EMDB-42295: 
Cryo-EM map of human clamp-clamp loader ATAD5-RFC-closed PCNA complex in intermediate state 1

PDB-8ui7: 
Cryo-EM map of human clmap-clamp loader ATAD5-RFC-gapped PCNA complex in intermediate state 3

PDB-8ui8: 
Cryo-EM map of human clamp-clamp loader ATAD5-RFC-two PCNAs complex in intermediate state 3

PDB-8ui9: 
Cryo-EM map of human clamp-clamp loader ATAD5-RFC-cracked PCNA complex in intermediate state 2

PDB-8uii: 
Cryo-EM map of human clamp-clamp loader ATAD5-RFC-closed PCNA complex in intermediate state 1

EMDB-38142: 
Structure of CCT6-HR-ATP-AlFx

EMDB-38143: 
Structure of apoferritin
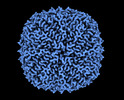
EMDB-38145: 
Consensus map of TBCA-apoferritin

EMDB-38147: 
Structure of CCT6-HR

EMDB-39651: 
Structure of the focused refined TBCA-apoferritin

EMDB-41252: 
Cryo-EM map of the Saccharomyces cerevisiae PCNA clamp unloader Elg1-RFC complex

EMDB-41253: 
Cryo-EM map of the Saccharomyces cerevisiae clamp unloader Elg1-RFC bound to a cracked PCNA

EMDB-41254: 
Cryo-EM map of the Saccharomyces cerevisiae clamp unloader Elg1-RFC bound to PCNA

PDB-8thb: 
Structure of the Saccharomyces cerevisiae PCNA clamp unloader Elg1-RFC complex

PDB-8thc: 
Structure of the Saccharomyces cerevisiae clamp unloader Elg1-RFC bound to a cracked PCNA

PDB-8thd: 
Structure of the Saccharomyces cerevisiae clamp unloader Elg1-RFC bound to PCNA

EMDB-36760: 
Cryo-EM structure of conformation 1 of complex of Nipah virus attachment glycoprotein G with 1E5 neutralizing antibody

EMDB-36761: 
Cryo-EM structure of conformation 2 of complex of Nipah virus attachment G with 1E5 neutralizing antibody

PDB-8k0c: 
Cryo-EM structure of conformation 1 of complex of Nipah virus attachment glycoprotein G with 1E5 neutralizing antibody

PDB-8k0d: 
Cryo-EM structure of conformation 2 of complex of Nipah virus attachment G with 1E5 neutralizing antibody
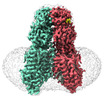
EMDB-36008: 
SIDT1 protein
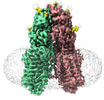
EMDB-36009: 
transport T2

PDB-8j6m: 
SIDT1 protein

PDB-8j6o: 
transport T2

EMDB-36849: 
Nipah virus Attachment glycoprotein with 41-6 antibody fragment

PDB-8k3c: 
Nipah virus Attachment glycoprotein with 41-6 antibody fragment
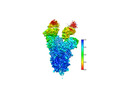
EMDB-37240: 
SARS-CoV-2 Omicron spike in complex with 5817 Fab

EMDB-37241: 
The interface structure of Omicron RBD binding to 5817 Fab

PDB-8khc: 
SARS-CoV-2 Omicron spike in complex with 5817 Fab

PDB-8khd: 
The interface structure of Omicron RBD binding to 5817 Fab

EMDB-35602: 
Cryo-EM structure of human HCN3 channel in apo state

PDB-8inz: 
Cryo-EM structure of human HCN3 channel in apo state

EMDB-38200: 
Cryo-EM structure of OSCA1.2-liposome-inside-in open state

EMDB-38503: 
Cryo-EM structure of OSCA1.2-liposome-inside-out closed state

EMDB-38611: 
Cryo-EM structure of OSCA3.1-1.1ver(Y367N-G454S-Y458I)-open/open state

EMDB-38612: 
Cryo-EM structure of OSCA3.1-1.1ver(Y367N-G454S-Y458I)-open/'desensitized' state

EMDB-38614: 
Cryo-EM structure of OSCA1.2-DOPC-1:20-contracted1 state

EMDB-38615: 
Cryo-EM structure of OSCA1.2-DOPC-1:20-contracted2 state

EMDB-38721: 
Cryo-EM structure of OSCA1.2-DOPC-1:20-expanded state

EMDB-38722: 
Cryo-EM structure of OSCA1.2-DOPC-1:50-betaCD state

EMDB-38723: 
Cryo-EM structure of OSCA3.1-2E(R611E-R619E)-closed/open state

EMDB-38724: 
Cryo-EM structure of OSCA3.1-2E(R611E-R619E)-closed/'desensitized' state

EMDB-38725: 
Cryo-EM structure of OSCA3.1-GDN state

EMDB-38726: 
Cryo-EM structure of OSCA3.1-liposome-inside-in state

EMDB-38727: 
Cryo-EM structure of OSCA1.2-V335W-DDM state

EMDB-38728: 
Cryo-EM structure of OSCA1.2-DOPC-1:50-contracted state

EMDB-38729: 
Cryo-EM structure of OSCA1.2-DOPC-1:50-expanded state
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
