-検索条件
-検索結果
検索 (著者・登録者: jr & jb)の結果全48件を表示しています

EMDB-28198: 
Cryo-EM map of SARS-CoV-2 Omicron BA.2 spike in complex with LLNL-199

EMDB-28199: 
Cryo-EM map of SARS-CoV-2 Omicron BA.2 spike in complex with 2130-1-0114-112

EMDB-41667: 
Cryo-EM structure of the PP2A:B55-FAM122A complex, B55 body

EMDB-41668: 
Cryo-EM structure of the PP2A:B55-FAM122A complex, PP2Ac body

EMDB-40644: 
Cryo-EM structure of the PP2A:B55-FAM122A complex

EMDB-41604: 
Cryo-EM structure of the PP2A:B55-ARPP19 complex
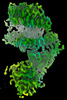
EMDB-29530: 
SARS-CoV-2 XBB.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment
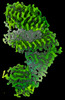
EMDB-29531: 
SARS-CoV-2 BQ.1.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment
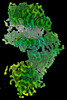
EMDB-40240: 
SARS-CoV-2 BN.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment

EMDB-28041: 
Cryo-EM Structure of human ABCA7 in BPL/Ch Nanodiscs

EMDB-28044: 
Human ABCA7 in BPL/Ch nanodiscs (Map 2)

EMDB-28047: 
Cryo-EM Structure of human ABCA7 in PE/Ch nanodiscs

EMDB-28050: 
Cryo-EM structure of human ABCA7 in Digitonin

EMDB-28451: 
Cryo-EM Structure of Nanodisc reconstituted human ABCA7 EQ mutant in ATP bound closed state

EMDB-25062: 
In-situ structure of SIV trimer

EMDB-26507: 
SARS-CoV-2 spike in complex with Multivalent miniprotein inhibitor FUS231-P24 (2RBDs open)

EMDB-26508: 
SARS-CoV-2 spike in complex with multivalent miniprotein inhibitor FUS231-P24 (3RBDs open)

EMDB-26509: 
SARS-CoV-2 spike in complex with multivalent miniprotein inhibitor FUS31-G10 (2RBDs open)

EMDB-26510: 
SARS-CoV-2 spike in complex with multivalent miniprotein inhibitor FUS31-G10 (3RBDs open)

EMDB-26511: 
SARS-CoV-2 spike in complex with AHB2-2GS-SB175 (local refinement of the RBD and AHB2)

EMDB-26512: 
SARS-CoV-2 spike in complex with AHB2-2GS-SB175

EMDB-25448: 
Negative-stain EM reconstruction of SpFN_1B-06-PL, a SARS-CoV-2 spike fused to H.pylori ferritin nanoparticle vaccine candidate
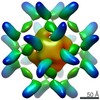
EMDB-25449: 
RFN_131, a Ferritin-based Nanoparticle Vaccine Candidate Displaying the SARS-CoV-2 Receptor-Binding Domain

EMDB-25450: 
pCoV146, a Ferritin-based Nanoparticle Vaccine Candidate Displaying the SARS-CoV-2 Spike Receptor-Binding and N-Terminal Domains

EMDB-25451: 
pCoV111, a Ferritin-based Nanoparticle Vaccine Candidate Displaying the SARS-CoV-2 Spike S1 Subunit

EMDB-13857: 
Beta049 fab in complex with SARS-CoV2 beta-Spike glycoprotein, The Beta mAb response underscores the antigenic distance to other SARS-CoV-2 variants

EMDB-13868: 
Beta-50 fab in complex with SARS-CoV-2 beta-Spike glycoprotein

EMDB-13869: 
COVOX-222 fab in complex with SARS-CoV-2 beta-Spike glycoprotein

EMDB-13870: 
Beta-43 fab in complex with SARS-CoV-2 beta-Spike glycoprotein

EMDB-13871: 
Beta-26 fab in complex with SARS-CoV-2 beta-Spike glycoprotein

EMDB-13872: 
Beta-32 fab in complex with SARS-CoV-2 beta-Spike glycoprotein

EMDB-13873: 
Beta-53 fab in complex with SARS-CoV-2 beta-Spike glycoprotein

EMDB-13874: 
Beta-44 fab in complex with SARS-CoV-2 beta-Spike glycoprotein

EMDB-13875: 
Beta-06 fab in complex with SARS-CoV-2 beta-Spike glycoprotein

EMDB-23719: 
EBOV GP bound to rEBOV-442 and rEBOV-515 Fabs

EMDB-24663: 
Cryo-EM density map of the outer dynein arm core from bovine tracheal cilia

EMDB-24664: 
Composite cryo-EM density map of the 48-nm repeat doublet microtubule from bovine tracheal cilia

EMDB-12095: 
Cryo-EM structure of mitochondrial complex I from Mus musculus inhibited by IACS-2858 at 3.0 A

EMDB-23898: 
SARS-CoV-2 Spike in complex with neutralizing Fab SARS2-38 (three down conformation)

EMDB-23899: 
SARS-CoV-2 Spike RBD in complex with neutralizing Fab SARS2-38 (local refinement)

EMDB-22106: 
High resolution cryoEM structure of huntingtin in complex with HAP40

EMDB-22078: 
Characterization of the SARS-CoV-2 S Protein: Biophysical, Biochemical, Structural, and Antigenic Analysis

EMDB-21965: 
Negative stain EM map of SARS CoV-2 spike protein (trimer)

EMDB-21974: 
Negative stain EM map of SARS-CoV-2 spike protein (trimer) with Fab COV2-2165

EMDB-21975: 
Negative stain EM map of SARS-CoV-2 spike protein (trimer) with Fab COV2-2196

EMDB-21976: 
Negative stain EM map of SARS-CoV-2 spike protein (trimer) with Fab COV2-2130

EMDB-21977: 
Negative stain EM map of SARS-CoV-2 spike protein (trimer) with Fab COV2-2130 and Fab COV2-2196

EMDB-3459: 
Hsp21 dodecamer, structural model based on cryo-EM and homology modelling
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
