-検索条件
-検索結果
検索 (著者・登録者: hansen & k)の結果237件中、1から50件目までを表示しています

PDB-8p2w: 
Structure of human SIT1 (focussed map / refinement)

PDB-8p2z: 
Structure of human SIT1 bound to L-pipecolate (focussed map / refinement)

PDB-8p30: 
Structure of human SIT1:ACE2 complex (open PD conformation) bound to L-pipecolate

EMDB-17377: 
Structure of human SIT1 (focussed map / refinement)

EMDB-17378: 
Structure of human SIT1:ACE2 complex (open PD conformation)

EMDB-17379: 
Structure of human SIT1:ACE2 complex (closed PD conformation)

EMDB-17380: 
Structure of human SIT1 bound to L-pipecolate (focussed map / refinement)

EMDB-17381: 
Structure of human SIT1:ACE2 complex (open PD conformation) bound to L-pipecolate

EMDB-17382: 
Structure of human SIT1:ACE2 complex (closed PD conformation) bound to L-pipecolate

PDB-8p2x: 
Structure of human SIT1:ACE2 complex (open PD conformation)

PDB-8p2y: 
Structure of human SIT1:ACE2 complex (closed PD conformation)

PDB-8p31: 
Structure of human SIT1:ACE2 complex (closed PD conformation) bound to L-pipecolate

EMDB-43753: 
Yeast U1 snRNP with humanized U1C Zinc-Finger domain

PDB-8w2o: 
Yeast U1 snRNP with humanized U1C Zinc-Finger domain

EMDB-41363: 
Cryo-EM structure of DDB1deltaB-DDA1-DCAF5

PDB-8tl6: 
Cryo-EM structure of DDB1deltaB-DDA1-DCAF5

EMDB-18490: 
Cryo-electron tomogram of lift-out lamella from cell-derived extracellular matrix (example 1)

EMDB-18491: 
Cryo-electron tomogram of lift-out lamella from cell-derived extracellular matrix (example 2)

EMDB-18492: 
Cryo-electron tomogram of lift-out lamella from cell-derived extracellular matrix (example 3)

EMDB-18493: 
Cryo-electron tomogram of lift-out lamella from cell-derived extracellular matrix (example 4)

EMDB-18494: 
Cryo-electron tomogram of lift-out lamella from cell-derived extracellular matrix (example 5)

EMDB-18207: 
Ubiquitin ligation to substrate by a cullin-RING E3 ligase & Cdc34: NEDD8-CUL2-RBX1-ELOB/C-FEM1C with trapped UBE2R2~donor UB-Sil1 peptide, Glacios map

EMDB-18230: 
Ubiquitin ligation to substrate by a cullin-RING E3 ligase & Cdc34: NEDD8-CUL2-RBX1-ELOB/C-FEM1C with trapped UBE2R2~donor UB-Sil1 peptide
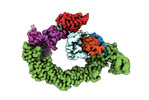
EMDB-18915: 
Ubiquitin ligation to neosubstrate by a cullin-RING E3 ligase & Cdc34: NEDD8-CUL2-RBX1-ELOB/C-VHL-MZ1 with trapped UBE2R2~donor UB-BRD4 BD2

PDB-8q7r: 
Ubiquitin ligation to substrate by a cullin-RING E3 ligase & Cdc34: NEDD8-CUL2-RBX1-ELOB/C-FEM1C with trapped UBE2R2~donor UB-Sil1 peptide

PDB-8r5h: 
Ubiquitin ligation to neosubstrate by a cullin-RING E3 ligase & Cdc34: NEDD8-CUL2-RBX1-ELOB/C-VHL-MZ1 with trapped UBE2R2~donor UB-BRD4 BD2

EMDB-17412: 
Vaccinia Virus flower-shaped pore-like structure

EMDB-40984: 
5TU-t1 - heterodimeric triplet polymerase ribozyme

PDB-8t2p: 
5TU-t1 - heterodimeric triplet polymerase ribozyme
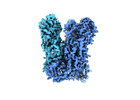
EMDB-17410: 
Vaccinia Virus palisade layer A10 trimer

EMDB-17411: 
Subtomogram averaging structure of the Vaccinia Virus core palisade layer

EMDB-17413: 
Cryo-electron tomogram of intact mature Vaccinia Virus particle

EMDB-17414: 
Cryo-electron tomogram of isolated Vaccinia Virus cores

EMDB-18452: 
Vaccinia virus inner core wall

PDB-8p4k: 
Vaccinia Virus palisade layer A10 trimer

EMDB-16024: 
SARS-CoV-2 S protein in complex with pT1644 Fab

EMDB-16026: 
SARS-CoV-2 S protein in complex with pT1696 Fab

PDB-8bg6: 
SARS-CoV-2 S protein in complex with pT1644 Fab

PDB-8bg8: 
SARS-CoV-2 S protein in complex with pT1696 Fab

EMDB-16416: 
HB3VAR03 apo headstructure (PfEMP1 A) complexed with EPCR

PDB-8c44: 
HB3VAR03 apo headstructure (PfEMP1 A) complexed with EPCR

EMDB-27920: 
3H03 Fab in complex with influenza virus neuraminidase from A/Brevig Mission/1/1918 (H1N1)

EMDB-27921: 
2H08 Fab in complex with influenza virus neuraminidase from A/Brevig Mission/1/1918 (H1N1)

PDB-8e6j: 
3H03 Fab in complex with influenza virus neuraminidase from A/Brevig Mission/1/1918 (H1N1)

PDB-8e6k: 
2H08 Fab in complex with influenza virus neuraminidase from A/Brevig Mission/1/1918 (H1N1)

EMDB-16415: 
HB3VAR03 apo headstructure (PfEMP1 A)

PDB-8c3y: 
HB3VAR03 apo headstructure (PfEMP1 A)

EMDB-27738: 
Negative stain EM map of the heterodimeric p110gamma-p84 complex

EMDB-27627: 
Structure of p110 gamma bound to the Ras inhibitory nanobody NB7

PDB-8dp0: 
Structure of p110 gamma bound to the Ras inhibitory nanobody NB7
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
