-検索条件
-検索結果
検索 (著者・登録者: fernando & rc)の結果52件中、1から50件目までを表示しています

EMDB-72358: 
Cryo-EM structure of F-box helicase 1 (FBH1) bound to an SCF ubiquitin ligase complex and a 3-way DNA fork (consensus structure)

EMDB-72359: 
Cryo-EM structure of F-box helicase 1 (FBH1) bound to an SCF ubiquitin ligase complex and a 3-way DNA fork (head structure)

EMDB-72361: 
Cryo-EM structure of F-box helicase 1 (FBH1) bound to an SCF ubiquitin ligase complex and a 3-way DNA fork (body structure)

EMDB-72362: 
Cryo-EM structure of F-box helicase 1 (FBH1) bound to an SCF ubiquitin ligase complex and a 3-way DNA fork (substrate structure)

PDB-9xzj: 
Cryo-EM structure of F-box helicase 1 (FBH1) bound to an SCF ubiquitin ligase complex and a 3-way DNA fork (consensus structure)

PDB-9xzk: 
Cryo-EM structure of F-box helicase 1 (FBH1) bound to an SCF ubiquitin ligase complex and a 3-way DNA fork (head structure)

PDB-9xzl: 
Cryo-EM structure of F-box helicase 1 (FBH1) bound to an SCF ubiquitin ligase complex and a 3-way DNA fork (body structure)

PDB-9xzm: 
Cryo-EM structure of F-box helicase 1 (FBH1) bound to an SCF ubiquitin ligase complex and a 3-way DNA fork (substrate structure)

EMDB-48671: 
C6 Herpes Virus Simplex Neutralizing Nanobody Bound to HSV Glycoprotein gB

EMDB-48677: 
D1 Herpes Virus Simplex Neutralizing Nanobody Bound to HSV Glycoprotein gB

EMDB-48730: 
D7 Herpes Virus Simplex Neutralizing Nanobody Bound to HSV Glycoprotein gD

PDB-9mvu: 
C6 Herpes Virus Simplex Neutralizing Nanobody Bound to HSV Glycoprotein gB

PDB-9mw5: 
D1 Herpes Virus Simplex Neutralizing Nanobody Bound to HSV Glycoprotein gB

PDB-9my8: 
D7 Herpes Virus Simplex Neutralizing Nanobody Bound to HSV Glycoprotein gD

EMDB-18047: 
3D Reconstruction of TH-DNAJC12 WT Complex

EMDB-18058: 
TH-DNAJC12 (108-198)

EMDB-18289: 
TH(DA)-DNAJC12 Complex 3D reconstruction

EMDB-15677: 
Cryo-EM structure for mouse leptin in complex with the mouse LEP-R ectodomain (1:2 mLEP:mLEPR model)

EMDB-15678: 
Mouse leptin:LEP-R complex cryoEM structure (3:3 model)

EMDB-15679: 
Cryo-EM structure for a 3:3 complex between mouse leptin and the mouse LEP-R ectodomain (local refinement)

EMDB-15680: 
Human leptin in complex with the human LEP-R ectodomain fused to a C-terminal trimeric isoleucine GCN4 zipper (2:2 model)

EMDB-15681: 
Human leptin in complex with the human LEP-R ectodomain fused to a C-terminal trimeric isoleucine GCN4 zipper (closed 3:3 model)

EMDB-15683: 
Human leptin in complex with the human LEP-R ectodomain fused to a C-terminal trimeric isoleucine GCN4 zipper (open 3:3 model).

EMDB-15899: 
Cryo-EM structure for the mouse LEPR-CRH2:Leptin:LEPR-Ig complex following symmetry expansion in combination with local refinement

PDB-8avb: 
Cryo-EM structure for mouse leptin in complex with the mouse LEP-R ectodomain (1:2 mLEP:mLEPR model).

PDB-8avc: 
Mouse leptin:LEP-R complex cryoEM structure (3:3 model)

PDB-8avd: 
Cryo-EM structure for a 3:3 complex between mouse leptin and the mouse LEP-R ectodomain (local refinement)

PDB-8ave: 
Human leptin in complex with the human LEP-R ectodomain fused to a C-terminal trimeric isoleucine GCN4 zipper (2:2 model)

PDB-8avf: 
Human leptin in complex with the human LEP-R ectodomain fused to a C-terminal trimeric isoleucine GCN4 zipper (closed 3:3 model)

PDB-8avo: 
Human leptin in complex with the human LEP-R ectodomain fused to a C-terminal trimeric isoleucine GCN4 zipper (open 3:3 model).

PDB-8b7q: 
Cryo-EM structure for the mouse LEPR-CRH2:Leptin:LEPR-Ig complex following symmetry expansion in combination with local refinement

EMDB-23046: 
Cryo-EM structure of Mal de Rio Cuarto virus P9-1 viroplasm protein (decamer)

EMDB-23047: 
Cryo-EM structure of Mal de Rio Cuarto virus P9-1 viroplasm protein (dodecamer)

PDB-7kvc: 
Cryo-EM structure of Mal de Rio Cuarto virus P9-1 viroplasm protein (decamer)

PDB-7kvd: 
Cryo-EM structure of Mal de Rio Cuarto virus P9-1 viroplasm protein (dodecamer)

EMDB-20074: 
Chimpanzee SIV Env trimeric ectodomain.

PDB-6ohy: 
Chimpanzee SIV Env trimeric ectodomain.

EMDB-3864: 
Negative stain electron microscopy reconstruction of a cellulose secretion (Bcs) macrocomplex from E. coli

EMDB-3877: 
Inner membrane Bcs complex (E. coli)

EMDB-8338: 
HCV E2 bound to AR1B, AR2A, and HCV1 Fabs

EMDB-8339: 
HCV E2 bound to AR1B, AR2A, and HCV1 Fabs

EMDB-8340: 
HCV E2 bound to AR1B, AR2A, and HCV1 Fabs

EMDB-3092: 
BG505 SOSIP.664 trimer in complex with PGT124 Fab with 32H heavy chain

EMDB-3093: 
BG505 SOSIP.664 N137A trimer in complex with PGT124 Fab with 3H heavy chain

EMDB-6379: 
Electron Microscopy of Bg505 in complex with 9H3L antibody

EMDB-6380: 
Bg505 SOSIP N137A in complex with 9H3L antibody

EMDB-6372: 
JRFL Env SOSIP.664 in complex with CD4-binding site broadly neutralizing antibody DRVIA7
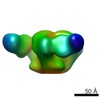
EMDB-6373: 
JRFL Env SOSIP.664 in complex with CD4-binding site hybrid broadly neutralizing antibody DRVIA7/VRC01

EMDB-2753: 
PGT124 in complex with BG505 SOSIP.664 Env trimer

EMDB-6182: 
3D structure of RepA-WH1 double filaments
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
