-検索条件
-検索結果
検索 (著者・登録者: banerjee & s)の結果151件中、1から50件目までを表示しています

EMDB-35817: 
Structure of Niacin-GPR109A-G protein complex

EMDB-35822: 
Structure of MK6892-GPR109A-G-protein complex

EMDB-35831: 
Structure of GSK256073-GPR109A-G-protein complex

EMDB-36193: 
Structure of Acipimox-GPR109A-G protein complex

EMDB-36280: 
Structure of MMF-GPR109A-G protein complex

PDB-8iy9: 
Structure of Niacin-GPR109A-G protein complex

PDB-8iyh: 
Structure of MK6892-GPR109A-G-protein complex

PDB-8iyw: 
Structure of GSK256073-GPR109A-G-protein complex

PDB-8jer: 
Structure of Acipimox-GPR109A-G protein complex

PDB-8jhn: 
Structure of MMF-GPR109A-G protein complex
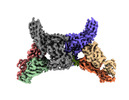
EMDB-34174: 
Structure of beta-arrestin2 in complex with a phosphopeptide corresponding to the human Atypical chemokine receptor 2, ACKR2 (D6R)
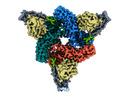
EMDB-36078: 
Structure of beta-arrestin2 in complex with M2Rpp
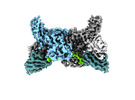
EMDB-36081: 
Structure of beta-arrestin2 in complex with D6Rpp (Local Refine)
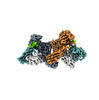
EMDB-36082: 
Structure of beta-arrestin1 in complex with D6Rpp
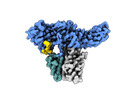
EMDB-36090: 
Structure of Muscarinic receptor (M2R) in complex with beta-arrestin1 (Local refine, cross-linked)
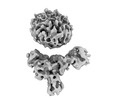
EMDB-36091: 
Muscarinic receptor (M2R) in complex with beta-arrestin1 (Low resolution full map, Cross-linked)
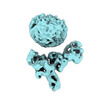
EMDB-36093: 
Muscarinic receptor (M2R) in complex with beta-arrestin1 (Low resolution full map, non-crosslinked)

EMDB-36110: 
Structure of basal beta-arrestin2
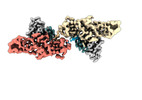
EMDB-36124: 
Structure of beta-arrestin1 in complex with C3aRpp
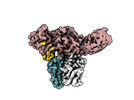
EMDB-36126: 
Structure of Muscarinic receptor (M2R) in complex with beta-arrestin1 (Local Refine, non-cross linked)

PDB-8go9: 
Structure of beta-arrestin2 in complex with a phosphopeptide corresponding to the human Atypical chemokine receptor 2, ACKR2 (D6R)

PDB-8j8r: 
Structure of beta-arrestin2 in complex with M2Rpp

PDB-8j8v: 
Structure of beta-arrestin2 in complex with D6Rpp (Local Refine)

PDB-8j8z: 
Structure of beta-arrestin1 in complex with D6Rpp

PDB-8j97: 
Structure of Muscarinic receptor (M2R) in complex with beta-arrestin1 (Local refine, cross-linked)

PDB-8j9k: 
Structure of basal beta-arrestin2

PDB-8ja3: 
Structure of beta-arrestin1 in complex with C3aRpp

PDB-8jaf: 
Structure of Muscarinic receptor (M2R) in complex with beta-arrestin1 (Local Refine, non-cross linked)

EMDB-40699: 
SARS-CoV-2 replication-transcription complex bound to nsp9 and UMPCPP, as a pre-catalytic NMPylation intermediate

EMDB-40707: 
SARS-CoV-2 replication-transcription complex bound to RNA-nsp9, as a noncatalytic RNA-nsp9 binding mode

EMDB-40708: 
SARS-CoV-2 replication-transcription complex bound to RNA-nsp9 and GDP-betaS, as a pre-catalytic deRNAylation/mRNA capping intermediate

PDB-8sq9: 
SARS-CoV-2 replication-transcription complex bound to nsp9 and UMPCPP, as a pre-catalytic NMPylation intermediate

PDB-8sqj: 
SARS-CoV-2 replication-transcription complex bound to RNA-nsp9, as a noncatalytic RNA-nsp9 binding mode

PDB-8sqk: 
SARS-CoV-2 replication-transcription complex bound to RNA-nsp9 and GDP-betaS, as a pre-catalytic deRNAylation/mRNA capping intermediate

EMDB-35257: 
Structure of EP54-C3aR-Go complex

EMDB-35259: 
Structure of Apo-C3aR-Go complex (Glacios)

EMDB-35263: 
Structure of EP54-C3aR-Gq complex

EMDB-35275: 
Structure of C3a-C3aR-Go complex (Composite map)

EMDB-35282: 
Structure of Apo-C3aR-Go complex (Titan)

EMDB-35292: 
Structure of C5a bound human C5aR1 in complex with Go (Composite map)

EMDB-35293: 
C3a-C3aR-Go (C3aR-Go complex only, Original Map)

EMDB-35294: 
C3a-C3aR-Go (C3a only, Original Map)

EMDB-35295: 
C5a-hC5aR1-Go (hC5aR1-Go complex only, Original map)
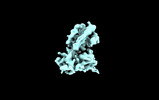
EMDB-35296: 
C5a-hC5aR1-Go complex (C5a only, Original map)

EMDB-36001: 
Structure of EP141-C3aR-Go complex

EMDB-36755: 
Structure of human C5a-desArg bound human C5aR1 in complex with Go

PDB-8i95: 
Structure of EP54-C3aR-Go complex

PDB-8i97: 
Structure of Apo-C3aR-Go complex (Glacios)

PDB-8i9a: 
Structure of EP54-C3aR-Gq complex

PDB-8i9l: 
Structure of C3a-C3aR-Go complex (Composite map)
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
