+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 4dxh | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Horse liver alcohol dehydrogenase complexed with NAD+ and 2,2,2-trifluoroethanol | ||||||
 要素 要素 | Alcohol dehydrogenase E chain | ||||||
 キーワード キーワード | OXIDOREDUCTASE / ALCOHOL DEHYDROGENASE / NAD+ / TRIFLUOROETHANOL / MICHAELIS COMPLEX ROSSMANN FOLD | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報all-trans-retinol dehydrogenase (NAD+) activity / alcohol dehydrogenase / retinoic acid metabolic process / retinol metabolic process / zinc ion binding / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.12 Å 分子置換 / 解像度: 1.12 Å | ||||||
 データ登録者 データ登録者 | Plapp, B.V. / Ramaswamy, S. | ||||||
 引用 引用 |  ジャーナル: Biochemistry / 年: 2012 ジャーナル: Biochemistry / 年: 2012タイトル: Atomic-Resolution Structures of Horse Liver Alcohol Dehydrogenase with NAD(+) and Fluoroalcohols Define Strained Michaelis Complexes. 著者: Plapp, B.V. / Ramaswamy, S. #1:  ジャーナル: Acta Crystallogr D Struct Biol / 年: 2022 ジャーナル: Acta Crystallogr D Struct Biol / 年: 2022タイトル: Dependence of crystallographic atomic displacement parameters on temperature (25-150 K) for complexes of horse liver alcohol dehydrogenase. 著者: Plapp, B.V. / Gakhar, L. / Subramanian, R. #2:  ジャーナル: Biochemistry / 年: 2003 ジャーナル: Biochemistry / 年: 2003タイトル: Amino acid residues in the nicotinamide binding site contribute to catalysis by horse liver alcohol dehydrogenase. 著者: Rubach, J.K. / Plapp, B.V. #3:  ジャーナル: J.Biol.Chem. / 年: 2003 ジャーナル: J.Biol.Chem. / 年: 2003タイトル: Formamides mimic aldehydes and inhibit liver alcohol dehydrogenases and ethanol metabolism. 著者: Venkataramaiah, T.H. / Plapp, B.V. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  4dxh.cif.gz 4dxh.cif.gz | 346.8 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb4dxh.ent.gz pdb4dxh.ent.gz | 280.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  4dxh.json.gz 4dxh.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  4dxh_validation.pdf.gz 4dxh_validation.pdf.gz | 970.7 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  4dxh_full_validation.pdf.gz 4dxh_full_validation.pdf.gz | 974.5 KB | 表示 | |
| XML形式データ |  4dxh_validation.xml.gz 4dxh_validation.xml.gz | 39.4 KB | 表示 | |
| CIF形式データ |  4dxh_validation.cif.gz 4dxh_validation.cif.gz | 62.7 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/dx/4dxh https://data.pdbj.org/pub/pdb/validation_reports/dx/4dxh ftp://data.pdbj.org/pub/pdb/validation_reports/dx/4dxh ftp://data.pdbj.org/pub/pdb/validation_reports/dx/4dxh | HTTPS FTP |
-関連構造データ
| 関連構造データ |  4dwvC  1hldS C: 同じ文献を引用 ( S: 精密化の開始モデル |
|---|---|
| 類似構造データ | |
| 実験データセット #1 | データ参照:  10.15785/SBGRID/890 / データの種類: diffraction image data 10.15785/SBGRID/890 / データの種類: diffraction image data |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 , 1種, 2分子 AB
| #1: タンパク質 | 分子量: 39853.273 Da / 分子数: 2 / 由来タイプ: 天然 / 詳細: Liver / 由来: (天然)  |
|---|
-非ポリマー , 5種, 1037分子 
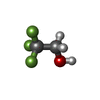
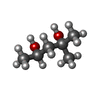





| #2: 化合物 | ChemComp-ZN / #3: 化合物 | #4: 化合物 | #5: 化合物 | ChemComp-MRD / ( #6: 水 | ChemComp-HOH / | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.39 Å3/Da / 溶媒含有率: 48.54 % |
|---|---|
| 結晶化 | 温度: 278 K / 手法: microdialysis / pH: 6.7 詳細: 50 MM AMMONIUM N-[TRIS(HYDROXYMETHYL) METHYL]-2-AMINOETHANE SULFONATE, PH 6.7 (AT 25 C), 0.25 MM EDTA, 10 MG/ML PROTEIN, 1 MM NAD+, 100 MM 2,2,2-TRIFLUOROETHANOL, 12 TO 25 % 2-METHYL-2,4- ...詳細: 50 MM AMMONIUM N-[TRIS(HYDROXYMETHYL) METHYL]-2-AMINOETHANE SULFONATE, PH 6.7 (AT 25 C), 0.25 MM EDTA, 10 MG/ML PROTEIN, 1 MM NAD+, 100 MM 2,2,2-TRIFLUOROETHANOL, 12 TO 25 % 2-METHYL-2,4-PENTANEDIOL, TEMPERATURE 278K, MICRODIALYSIS |
-データ収集
| 回折 | 平均測定温度: 100 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  APS APS  / ビームライン: 19-ID / 波長: 0.9184 Å / ビームライン: 19-ID / 波長: 0.9184 Å |
| 検出器 | タイプ: ADSC QUANTUM 315r / 検出器: CCD / 日付: 2009年6月24日 詳細: Rosenbaum Rock vertical focusing mirror with Pt, glass, Pd lanes |
| 放射 | モノクロメーター: Rosenbaum Rock high resolution double crystal monochromator, LN2 cooled, sagittal focussing 2nd mirror, Si(111) プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 0.9184 Å / 相対比: 1 |
| 反射 | 解像度: 1.12→20 Å / Num. all: 283954 / Num. obs: 267668 / % possible obs: 94.3 % / Observed criterion σ(F): 0 / Observed criterion σ(I): 0 / 冗長度: 4 % / Rmerge(I) obs: 0.046 / Net I/σ(I): 9.7 |
| 反射 シェル | 解像度: 1.12→1.16 Å / 冗長度: 4 % / Rmerge(I) obs: 0.365 / Mean I/σ(I) obs: 2.1 / % possible all: 91.4 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: pdb entry 1HLD 解像度: 1.12→20 Å / Cor.coef. Fo:Fc: 0.983 / Cor.coef. Fo:Fc free: 0.979 / Occupancy max: 1 / Occupancy min: 0.2 / SU B: 0.94 / SU ML: 0.019 / 交差検証法: THROUGHOUT / ESU R: 0.027 / ESU R Free: 0.027 / 立体化学のターゲット値: MAXIMUM LIKELIHOOD / 詳細: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.2 Å / 溶媒モデル: MASK | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 13.289 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.12→20 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 1.12→1.149 Å / Total num. of bins used: 20
|
 ムービー
ムービー コントローラー
コントローラー


























 PDBj
PDBj





