-検索条件
-検索結果
検索 (著者・登録者: nguyen & c)の結果624件中、1から50件目までを表示しています

EMDB-18438: 
mt-SSU assembly intermediate in GTPBP8 knock-out cells, state 1

EMDB-18439: 
mt-SSU assembly intermediate in GTPBP8 knock-out cells, state 2

EMDB-18440: 
mt-SSU assembly intermediate in GTPBP8 knock-out cells, state 3

EMDB-18443: 
mt-SSU assembly intermediate in GTPBP8 knock-out cells, state 4

EMDB-18460: 
mt-LSU assembly intermediate in GTPBP8 knock-out cells, state 1

EMDB-18461: 
mt-LSU assembly intermediate in GTPBP8 knock-out cells, state 2
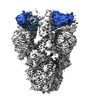
EMDB-39546: 
SARS-CoV-2 Delta Spike in complex with JL-8C

EMDB-39547: 
SARS-CoV-2 Delta Spike in complex with JM-1A

EMDB-39685: 
SARS-CoV-2 Delta Spike in complex with Fab of JE-5C

EMDB-39686: 
SARS-CoV-2 Spike (BA.1) in complex with Fab of JH-8B

PDB-8yro: 
SARS-CoV-2 Delta Spike in complex with JL-8C

PDB-8yrp: 
SARS-CoV-2 Delta Spike in complex with JM-1A

PDB-8yz5: 
SARS-CoV-2 Delta Spike in complex with Fab of JE-5C

PDB-8yz6: 
SARS-CoV-2 Spike (BA.1) in complex with Fab of JH-8B

EMDB-18658: 
Structure of the NCOA4 (Nuclear Receptor Coactivator 4)-FTH1 (H-Ferritin) complex

PDB-8qu9: 
Structure of the NCOA4 (Nuclear Receptor Coactivator 4)-FTH1 (H-Ferritin) complex

EMDB-18334: 
Cryo-EM structure of the inward-facing FLVCR1

EMDB-18335: 
Cryo-EM structure of the inward-facing choline-bound FLVCR1

EMDB-18336: 
Cryo-EM structure of the inward-facing FLVCR2

EMDB-18337: 
Cryo-EM structure of the outward-facing FLVCR2

EMDB-18339: 
Cryo-EM structure of the inward-facing choline-bound FLVCR2

EMDB-19009: 
Cryo-EM structure of the inward-facing ethanolamine-bound FLVCR1

PDB-8qcs: 
Cryo-EM structure of the inward-facing FLVCR1

PDB-8qct: 
Cryo-EM structure of the inward-facing choline-bound FLVCR1

PDB-8qcx: 
Cryo-EM structure of the inward-facing FLVCR2

PDB-8qcy: 
Cryo-EM structure of the outward-facing FLVCR2

PDB-8qd0: 
Cryo-EM structure of the inward-facing choline-bound FLVCR2

PDB-8r8t: 
Cryo-EM structure of the inward-facing ethanolamine-bound FLVCR1

EMDB-40918: 
Human glutaminase C (Y466W) with L-Gln and Pi, filamentous form

EMDB-40920: 
Human liver-type glutaminase (Apo form)
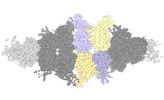
EMDB-40950: 
Human liver-type glutaminase (K253A) with L-Gln, filamentous form

EMDB-43533: 
Human liver-type glutaminase, bound with inhibitor Compound 968

PDB-8szj: 
Human glutaminase C (Y466W) with L-Gln and Pi, filamentous form

PDB-8szl: 
Human liver-type glutaminase (Apo form)

PDB-8t0z: 
Human liver-type glutaminase (K253A) with L-Gln, filamentous form

EMDB-29907: 
Structure of human NDS.1 Fab and 1G01 Fab in complex with influenza virus neuraminidase from A/Indiana/10/2011 (H3N2v); consensus map with only Fab 1G01 resolved

EMDB-29908: 
Structure of human NDS.1 Fab and 1G01 Fab in complex with influenza virus neuraminidase from A/Indiana/10/2011 (H3N2v), locally refined map

EMDB-29909: 
Structure of human NDS.3 Fab in complex with influenza virus neuraminidase from A/Darwin/09/2021 (H3N2)

PDB-8gat: 
Structure of human NDS.1 Fab and 1G01 Fab in complex with influenza virus neuraminidase from A/Indiana/10/2011 (H3N2v), based on consensus cryo-EM map with only Fab 1G01 resolved

PDB-8gau: 
Structure of human NDS.1 Fab and 1G01 Fab in complex with influenza virus neuraminidase from A/Indiana/10/2011 (H3N2v)

PDB-8gav: 
Structure of human NDS.3 Fab in complex with influenza virus neuraminidase from A/Darwin/09/2021 (H3N2)

EMDB-29920: 
Cardiac amyloid fibrils extracted from a wild-type ATTR amyloidosis patient

PDB-8gbr: 
Cardiac amyloid fibrils extracted from a wild-type ATTR amyloidosis patient

EMDB-28198: 
Cryo-EM map of SARS-CoV-2 Omicron BA.2 spike in complex with LLNL-199

EMDB-28199: 
Cryo-EM map of SARS-CoV-2 Omicron BA.2 spike in complex with 2130-1-0114-112

PDB-8ekd: 
Cryo-EM map of SARS-CoV-2 Omicron BA.2 spike in complex with 2130-1-0114-112

EMDB-29874: 
Cardiac amyloid fibrils extracted from a wild-type ATTR amyloidosis patient

PDB-8g9r: 
Cardiac amyloid fibrils extracted from a wild-type ATTR amyloidosis patient
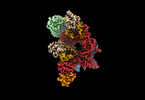
EMDB-17190: 
The H/ACA RNP lobe of human telomerase with the dyskerin thumb loop in a semi-closed conformation
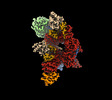
EMDB-17191: 
The H/ACA RNP lobe of human telomerase with the dyskerin thumb loop in an open conformation
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
