[English] 日本語
 Yorodumi
Yorodumi- PDB-6k6b: Application of anti-helix antibodies in protein structure determi... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 6k6b | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | Application of anti-helix antibodies in protein structure determination (8496-3LRH) | |||||||||
 Components Components |
| |||||||||
 Keywords Keywords | STRUCTURAL PROTEIN / antibody / protein design | |||||||||
| Function / homology |  Function and homology information Function and homology informationsymbiont-mediated suppression of host signal transduction pathway via antagonism of host cell surface receptor / IgG binding / extracellular region Similarity search - Function | |||||||||
| Biological species |  Homo sapiens (human) Homo sapiens (human) | |||||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 2.06 Å MOLECULAR REPLACEMENT / Resolution: 2.06 Å | |||||||||
 Authors Authors | Lee, J.O. / Jin, M.S. / Kim, J.W. / Kim, S. / Lee, H. / Cho, G.Y. | |||||||||
| Funding support |  Korea, Republic Of, 2items Korea, Republic Of, 2items
| |||||||||
 Citation Citation |  Journal: Proc.Natl.Acad.Sci.USA / Year: 2019 Journal: Proc.Natl.Acad.Sci.USA / Year: 2019Title: Application of antihelix antibodies in protein structure determination. Authors: Kim, J.W. / Kim, S. / Lee, H. / Cho, G. / Kim, S.C. / Lee, H. / Jin, M.S. / Lee, J.O. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  6k6b.cif.gz 6k6b.cif.gz | 81.9 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb6k6b.ent.gz pdb6k6b.ent.gz | 59.2 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  6k6b.json.gz 6k6b.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/k6/6k6b https://data.pdbj.org/pub/pdb/validation_reports/k6/6k6b ftp://data.pdbj.org/pub/pdb/validation_reports/k6/6k6b ftp://data.pdbj.org/pub/pdb/validation_reports/k6/6k6b | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  6k3mC  6k64C  6k65C  6k67C  6k68C  6k69C  6k6aC  1deeS  3lrhS S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 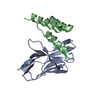
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
| #1: Protein | Mass: 14203.453 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Homo sapiens (human) / Production host: Homo sapiens (human) / Production host:  |
|---|---|
| #2: Protein | Mass: 8590.640 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Source: (gene. exp.)   |
| #3: Water | ChemComp-HOH / |
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 1.64 Å3/Da / Density % sol: 25.08 % |
|---|---|
| Crystal grow | Temperature: 296 K / Method: vapor diffusion, sitting drop / Details: 35% PEG 4000, 0.1M MES pH 6.5 |
-Data collection
| Diffraction | Mean temperature: 103 K / Serial crystal experiment: N |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: PAL/PLS SYNCHROTRON / Site: PAL/PLS  / Beamline: 7A (6B, 6C1) / Wavelength: 0.979 Å / Beamline: 7A (6B, 6C1) / Wavelength: 0.979 Å |
| Detector | Type: ADSC QUANTUM 315r / Detector: CCD / Date: Jun 8, 2016 |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 0.979 Å / Relative weight: 1 |
| Reflection | Resolution: 2→50 Å / Num. obs: 9479 / % possible obs: 99 % / Redundancy: 6.7 % / Rpim(I) all: 0.035 / Net I/σ(I): 25.2 |
| Reflection shell | Resolution: 2→2.1 Å / Num. unique obs: 1369 / Rpim(I) all: 0.19 |
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 3LRH, 1DEE Resolution: 2.06→26.279 Å / SU ML: 0.24 / Cross valid method: FREE R-VALUE / σ(F): 1.42 / Phase error: 24.4
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 2.06→26.279 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller












 PDBj
PDBj