+ データを開く
データを開く
- 基本情報
基本情報
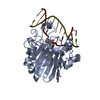
| 登録情報 | データベース: PDB / ID: 3g38 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | The catalytically inactive mutant Mth0212 (D151N) in complex with an 8 bp dsDNA | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | HYDROLASE/DNA / protein-DNA complex / 3'- phosphate moiety bound / HYDROLASE-DNA COMPLEX | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報exodeoxyribonuclease III / double-stranded DNA 3'-5' DNA exonuclease activity / phosphoric diester hydrolase activity / class I DNA-(apurinic or apyrimidinic site) endonuclease activity / DNA-(apurinic or apyrimidinic site) lyase / base-excision repair / DNA binding / metal ion binding 類似検索 - 分子機能 | ||||||
| 生物種 |   Methanothermobacter thermautotrophicus (古細菌) Methanothermobacter thermautotrophicus (古細菌) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 3.04 Å 分子置換 / 解像度: 3.04 Å | ||||||
 データ登録者 データ登録者 | Lakomek, K. / Dickmanns, A. / Ficner, R. | ||||||
 引用 引用 |  ジャーナル: J.Mol.Biol. / 年: 2010 ジャーナル: J.Mol.Biol. / 年: 2010タイトル: Crystal Structure Analysis of DNA Uridine Endonuclease Mth212 Bound to DNA 著者: Lakomek, K. / Dickmanns, A. / Ciirdaeva, E. / Schomacher, L. / Ficner, R. #1: ジャーナル: Nucleic Acids Res. / 年: 2006 タイトル: The Methanothermobacter thermautotrophicus ExoIII homologue Mth212 is a DNA uridine endonuclease 著者: Georg, J. / Schomacher, L. / Chong, J.P.J. / Majernik, A.I. / Raabe, M. / Urlaub, H. / Muller, S. / Ciirdaeva, E. / Kramer, W. / Fritz, H.-J. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  3g38.cif.gz 3g38.cif.gz | 75.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb3g38.ent.gz pdb3g38.ent.gz | 51.2 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  3g38.json.gz 3g38.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/g3/3g38 https://data.pdbj.org/pub/pdb/validation_reports/g3/3g38 ftp://data.pdbj.org/pub/pdb/validation_reports/g3/3g38 ftp://data.pdbj.org/pub/pdb/validation_reports/g3/3g38 | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  3fziSC  3g00C  3g0aC  3g0rC  3g1kC  3g2cC  3g2dC  3g3cC  3g3yC  3g4tC  3g8vC  3g91C  3ga6C S: 精密化の開始モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 31429.666 Da / 分子数: 1 / 変異: T2A, D151N / 由来タイプ: 組換発現 由来: (組換発現)   Methanothermobacter thermautotrophicus (古細菌) Methanothermobacter thermautotrophicus (古細菌)株: Delta H (DSM 1053) / 遺伝子: mth0212, MTH212, MTH_212 / プラスミド: pET_B_001-mth212 (D151N) / 発現宿主:  | ||
|---|---|---|---|
| #2: DNA鎖 | 分子量: 3021.964 Da / 分子数: 1 / 由来タイプ: 合成 | ||
| #3: DNA鎖 | 分子量: 2741.800 Da / 分子数: 1 / 由来タイプ: 合成 | ||
| #4: 化合物 | ChemComp-GOL / #5: 水 | ChemComp-HOH / | |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.55 Å3/Da / 溶媒含有率: 51.75 % | ||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 結晶化 | 温度: 293 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 5.6 詳細: reservoir: 5% (w/v) PEG 4000, 50mM KCl, 100mM MES pH 5.6, 10mM MgCl2; complex solution: 230mM NaCl, 8mM HEPES-KOH pH 7.6, 2mM MgCl2, 3mM DTT, VAPOR DIFFUSION, SITTING DROP, temperature 293K | ||||||||||||||||||||||||||||||||||||||||||||
| 溶液の組成 |
|
-データ収集
| 回折 | 平均測定温度: 100 K | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  EMBL/DESY, HAMBURG EMBL/DESY, HAMBURG  / ビームライン: X11 / 波長: 0.8015 Å / ビームライン: X11 / 波長: 0.8015 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 検出器 | タイプ: MAR CCD 165 mm / 検出器: CCD / 日付: 2007年5月17日 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 放射波長 | 波長: 0.8015 Å / 相対比: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 反射 | 解像度: 2.74→36.424 Å / Num. obs: 10553 / % possible obs: 100 % / 冗長度: 7.6 % / Biso Wilson estimate: 54.9 Å2 / Rmerge(I) obs: 0.117 / Rsym value: 0.117 / Net I/σ(I): 5.881 / Num. measured all: 80599 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 反射 シェル | Diffraction-ID: 1
|
-位相決定
| 位相決定 | 手法:  分子置換 分子置換 |
|---|
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: PDN ENTRY 3FZI 解像度: 3.04→34.13 Å / Cor.coef. Fo:Fc: 0.878 / Cor.coef. Fo:Fc free: 0.779 / WRfactor Rfree: 0.303 / WRfactor Rwork: 0.235 / Occupancy max: 1 / Occupancy min: 0.99 / FOM work R set: 0.711 / SU B: 30.97 / SU ML: 0.55 / SU Rfree: 0.594 / 交差検証法: THROUGHOUT / σ(F): 0 / ESU R Free: 0.594 / 立体化学のターゲット値: MAXIMUM LIKELIHOOD 詳細: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS; The DNA conformation significantly deviates from ideal geometry due to the binding to the protein molecule
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.2 Å / 溶媒モデル: MASK | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso max: 93.28 Å2 / Biso mean: 37.113 Å2 / Biso min: 18.88 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 3.04→34.13 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 3.04→3.119 Å / Total num. of bins used: 20
|
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj





