+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1ab1 | ||||||
|---|---|---|---|---|---|---|---|
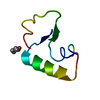
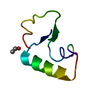
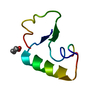
| タイトル | SI FORM CRAMBIN | ||||||
 要素 要素 | CRAMBIN (SER22/ILE25) | ||||||
 キーワード キーワード | PLANT SEED PROTEIN / THIONIN | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | ||||||
| 生物種 |  Crambe hispanica subsp. abyssinica (植物) Crambe hispanica subsp. abyssinica (植物) | ||||||
| 手法 |  X線回折 / ALREADY SOLVED / 解像度: 0.89 Å X線回折 / ALREADY SOLVED / 解像度: 0.89 Å | ||||||
 データ登録者 データ登録者 | Teeter, M.M. / Yamano, A. | ||||||
 引用 引用 |  ジャーナル: J.Biol.Chem. / 年: 1997 ジャーナル: J.Biol.Chem. / 年: 1997タイトル: Crystal structure of Ser-22/Ile-25 form crambin confirms solvent, side chain substate correlations. 著者: Yamano, A. / Heo, N.H. / Teeter, M.M. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1ab1.cif.gz 1ab1.cif.gz | 26.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1ab1.ent.gz pdb1ab1.ent.gz | 17.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1ab1.json.gz 1ab1.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1ab1_validation.pdf.gz 1ab1_validation.pdf.gz | 379.1 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1ab1_full_validation.pdf.gz 1ab1_full_validation.pdf.gz | 379 KB | 表示 | |
| XML形式データ |  1ab1_validation.xml.gz 1ab1_validation.xml.gz | 2.9 KB | 表示 | |
| CIF形式データ |  1ab1_validation.cif.gz 1ab1_validation.cif.gz | 3.4 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ab/1ab1 https://data.pdbj.org/pub/pdb/validation_reports/ab/1ab1 ftp://data.pdbj.org/pub/pdb/validation_reports/ab/1ab1 ftp://data.pdbj.org/pub/pdb/validation_reports/ab/1ab1 | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
| #1: タンパク質・ペプチド | 分子量: 4728.410 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)  Crambe hispanica subsp. abyssinica (植物) Crambe hispanica subsp. abyssinica (植物)生物種: Crambe hispanica / 株: subsp. abyssinica / 参照: UniProt: P01542 |
|---|---|
| #2: 化合物 | ChemComp-EOH / |
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 1.77 Å3/Da / 溶媒含有率: 30.37 % | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 結晶化 | 手法: vapor diffusion - hanging drop - microseeding / pH: 7 詳細: HPLC PURIFIED SI-CRAMBIN PROTEIN WAS DISSOLVED AT 25 MG/ML IN 80% ETHANOL/WATER (V/V), AND EQUILIBRATED AGAINS 60% ETHANOL. AFTER 10 DAYS, THE RESERVOIR WAS LOWERED TO 50% AND MICROSEEDED BY ...詳細: HPLC PURIFIED SI-CRAMBIN PROTEIN WAS DISSOLVED AT 25 MG/ML IN 80% ETHANOL/WATER (V/V), AND EQUILIBRATED AGAINS 60% ETHANOL. AFTER 10 DAYS, THE RESERVOIR WAS LOWERED TO 50% AND MICROSEEDED BY THE STREAK SEEDING METHOD (CAT WHISKER). AFTER LOWERING THE RESERVOIR TO 45%, GOOD CRYSTALS WERE FORMED., pH 7., vapor diffusion - hanging drop - microseeding | ||||||||||||||||||||
| 結晶化 | *PLUS 温度: 20 ℃ / 手法: 蒸気拡散法 / 詳細: Teeter, M.M., (1979) J. Mol. Biol., 127, 219. | ||||||||||||||||||||
| 溶液の組成 | *PLUS
|
-データ収集
| 回折 | 平均測定温度: 150 K |
|---|---|
| 放射光源 | 由来:  回転陽極 / タイプ: RIGAKU RUH2R / 波長: 1.5418 回転陽極 / タイプ: RIGAKU RUH2R / 波長: 1.5418 |
| 検出器 | タイプ: RIGAKU / 検出器: IMAGE PLATE / 日付: 1992年10月1日 / 詳細: COLLIMATOR |
| 放射 | モノクロメーター: GRAPHITE(002) / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.5418 Å / 相対比: 1 |
| 反射 | 解像度: 0.89→17.67 Å / Num. obs: 23165 / % possible obs: 88.77 % / Observed criterion σ(I): 0 / 冗長度: 1 % / Rmerge(I) obs: 0.04 / Rsym value: 0.1 / Net I/σ(I): 8.3 |
| 反射 シェル | 解像度: 0.89→0.897 Å / 冗長度: 0.1 % / Rmerge(I) obs: 0.1 / Mean I/σ(I) obs: 3.2 / Rsym value: 0.15 / % possible all: 74.96 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法: ALREADY SOLVED / 解像度: 0.89→10 Å / 交差検証法: DIFFERENCE DENSITY PEAKS / σ(F): 2 詳細: OVERALL WEIGHT WAS 1/(SIGDEL) AND SIGDEL=8-10(SINTH/L-0.166667) THIS STRUCTURE ILLUSTRATES THE CONFIRMATION OF THE ABILITY OF X-RAY DIFFRACTION TO DETECT SUBSTATES. HERE THE SUBSTATES WERE ...詳細: OVERALL WEIGHT WAS 1/(SIGDEL) AND SIGDEL=8-10(SINTH/L-0.166667) THIS STRUCTURE ILLUSTRATES THE CONFIRMATION OF THE ABILITY OF X-RAY DIFFRACTION TO DETECT SUBSTATES. HERE THE SUBSTATES WERE PHYSICALLY SEPARATED (TWO SEQUENCE FORMS OF CRAMBIN) AND SEPARATE STRUCTURES DETERMINED. FURTHER SUBSTATES ARE EXTENDED FROM PROTEIN TO SURROUNDING SOLVENT.
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 5.5 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze | Luzzati coordinate error obs: 0.08 Å / Luzzati d res low obs: 17.6 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 0.89→10 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj