+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-12616 | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | TFIIH in a post-translocated state (with ADP-BeF3) | ||||||||||||||||||
 マップデータ マップデータ | Local resolution filtered and sharpened map | ||||||||||||||||||
 試料 試料 |
| ||||||||||||||||||
 キーワード キーワード | Initiation / TRANSCRIPTION | ||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報MMXD complex / core TFIIH complex portion of holo TFIIH complex / Cytosolic iron-sulfur cluster assembly / nucleotide-excision repair, DNA duplex unwinding / central nervous system myelin formation / positive regulation of mitotic recombination / hair follicle maturation / ventricular system development / hair cell differentiation / nucleotide-excision repair factor 3 complex ...MMXD complex / core TFIIH complex portion of holo TFIIH complex / Cytosolic iron-sulfur cluster assembly / nucleotide-excision repair, DNA duplex unwinding / central nervous system myelin formation / positive regulation of mitotic recombination / hair follicle maturation / ventricular system development / hair cell differentiation / nucleotide-excision repair factor 3 complex / transcription factor TFIIE complex / nucleotide-excision repair, preincision complex assembly / CAK-ERCC2 complex / UV protection / transcription factor TFIIK complex / embryonic cleavage / transcription open complex formation at RNA polymerase II promoter / DNA 5'-3' helicase / adult heart development / G protein-coupled receptor internalization / transcription factor TFIIH holo complex / transcription factor TFIIH core complex / cyclin-dependent protein serine/threonine kinase activator activity / DNA 3'-5' helicase / RNA Polymerase I Transcription Termination / transcription preinitiation complex / nuclear thyroid hormone receptor binding / regulation of mitotic cell cycle phase transition / hematopoietic stem cell proliferation / 3'-5' DNA helicase activity / regulation of cyclin-dependent protein serine/threonine kinase activity / RNA Pol II CTD phosphorylation and interaction with CE during HIV infection / RNA Pol II CTD phosphorylation and interaction with CE / transcription factor TFIID complex / Formation of the Early Elongation Complex / Formation of the HIV-1 Early Elongation Complex / RNA polymerase II general transcription initiation factor activity / spinal cord development / mRNA Capping / HIV Transcription Initiation / RNA Polymerase II HIV Promoter Escape / Transcription of the HIV genome / RNA Polymerase II Promoter Escape / RNA Polymerase II Transcription Pre-Initiation And Promoter Opening / RNA Polymerase II Transcription Initiation / RNA Polymerase II Transcription Initiation And Promoter Clearance / bone mineralization / erythrocyte maturation / regulation of G1/S transition of mitotic cell cycle / RNA Polymerase I Transcription Initiation / transcription by RNA polymerase I / ATPase activator activity / DNA topological change / intrinsic apoptotic signaling pathway by p53 class mediator / RNA polymerase II transcribes snRNA genes / hematopoietic stem cell differentiation / Tat-mediated elongation of the HIV-1 transcript / transcription elongation by RNA polymerase I / Formation of HIV-1 elongation complex containing HIV-1 Tat / transcription-coupled nucleotide-excision repair / embryonic organ development / Formation of HIV elongation complex in the absence of HIV Tat / Cyclin E associated events during G1/S transition / RNA Polymerase II Transcription Elongation / Cyclin A/B1/B2 associated events during G2/M transition / cyclin-dependent protein kinase holoenzyme complex / Formation of RNA Pol II elongation complex / Cyclin A:Cdk2-associated events at S phase entry / response to UV / RNA Polymerase II Pre-transcription Events / DNA helicase activity / hormone-mediated signaling pathway / extracellular matrix organization / insulin-like growth factor receptor signaling pathway / post-embryonic development / maturation of SSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / isomerase activity / chromosome segregation / determination of adult lifespan / promoter-specific chromatin binding / TP53 Regulates Transcription of DNA Repair Genes / transcription initiation at RNA polymerase II promoter / nucleotide-excision repair / RNA Polymerase I Promoter Escape / transcription elongation by RNA polymerase II / positive regulation of smooth muscle cell proliferation / NoRC negatively regulates rRNA expression / multicellular organism growth / Transcription-Coupled Nucleotide Excision Repair (TC-NER) / cellular response to gamma radiation / Formation of TC-NER Pre-Incision Complex / Dual Incision in GG-NER / Formation of Incision Complex in GG-NER / spindle / Dual incision in TC-NER / response to calcium ion / Gap-filling DNA repair synthesis and ligation in TC-NER / G1/S transition of mitotic cell cycle / Cyclin D associated events in G1 / protein localization 類似検索 - 分子機能 | ||||||||||||||||||
| 生物種 |  Homo sapiens (ヒト) / Homo sapiens (ヒト) /  Human mastadenovirus C (ウイルス) Human mastadenovirus C (ウイルス) | ||||||||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.9 Å | ||||||||||||||||||
 データ登録者 データ登録者 | Aibara S / Schilbach S | ||||||||||||||||||
| 資金援助 |  ドイツ, 5件 ドイツ, 5件
| ||||||||||||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2021 ジャーナル: Nature / 年: 2021タイトル: Structures of mammalian RNA polymerase II pre-initiation complexes. 著者: Shintaro Aibara / Sandra Schilbach / Patrick Cramer /  要旨: The initiation of transcription is a focal point for the regulation of gene activity during mammalian cell differentiation and development. To initiate transcription, RNA polymerase II (Pol II) ...The initiation of transcription is a focal point for the regulation of gene activity during mammalian cell differentiation and development. To initiate transcription, RNA polymerase II (Pol II) assembles with general transcription factors into a pre-initiation complex (PIC) that opens promoter DNA. Previous work provided the molecular architecture of the yeast and human PIC and a topological model for DNA opening by the general transcription factor TFIIH. Here we report the high-resolution cryo-electron microscopy structure of PIC comprising human general factors and Sus scrofa domesticus Pol II, which is 99.9% identical to human Pol II. We determine the structures of PIC with closed and opened promoter DNA at 2.5-2.8 Å resolution, and resolve the structure of TFIIH at 2.9-4.0 Å resolution. We capture the TFIIH translocase XPB in the pre- and post-translocation states, and show that XPB induces and propagates a DNA twist to initiate the opening of DNA approximately 30 base pairs downstream of the TATA box. We also provide evidence that DNA opening occurs in two steps and leads to the detachment of TFIIH from the core PIC, which may stop DNA twisting and enable RNA chain initiation. | ||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_12616.map.gz emd_12616.map.gz | 306.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-12616-v30.xml emd-12616-v30.xml emd-12616.xml emd-12616.xml | 35.2 KB 35.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_12616_fsc.xml emd_12616_fsc.xml | 15.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_12616.png emd_12616.png | 198.8 KB | ||
| マスクデータ |  emd_12616_msk_1.map emd_12616_msk_1.map | 347.6 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-12616.cif.gz emd-12616.cif.gz | 9.2 KB | ||
| その他 |  emd_12616_additional_1.map.gz emd_12616_additional_1.map.gz emd_12616_half_map_1.map.gz emd_12616_half_map_1.map.gz emd_12616_half_map_2.map.gz emd_12616_half_map_2.map.gz | 205.7 MB 278.9 MB 279 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-12616 http://ftp.pdbj.org/pub/emdb/structures/EMD-12616 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12616 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12616 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_12616_validation.pdf.gz emd_12616_validation.pdf.gz | 674.1 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_12616_full_validation.pdf.gz emd_12616_full_validation.pdf.gz | 673.7 KB | 表示 | |
| XML形式データ |  emd_12616_validation.xml.gz emd_12616_validation.xml.gz | 23.9 KB | 表示 | |
| CIF形式データ |  emd_12616_validation.cif.gz emd_12616_validation.cif.gz | 32.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12616 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12616 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12616 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12616 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7nvxMC  7nvrC  7nvsC  7nvtC  7nvuC  7nvvC  7nvwC  7nvyC  7nvzC  7nw0C C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_12616.map.gz / 形式: CCP4 / 大きさ: 347.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_12616.map.gz / 形式: CCP4 / 大きさ: 347.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Local resolution filtered and sharpened map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.05 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
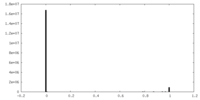
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_12616_msk_1.map emd_12616_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
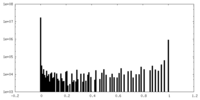
| 密度ヒストグラム |
-追加マップ: local resolution filtered map, unsharpened
| ファイル | emd_12616_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | local resolution filtered map, unsharpened | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Unfiltered half map 1
| ファイル | emd_12616_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unfiltered half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
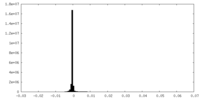
| 密度ヒストグラム |
-ハーフマップ: Unfiltered half map 2
| ファイル | emd_12616_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unfiltered half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : TFIIH (with ADP-BeF3)
+超分子 #1: TFIIH (with ADP-BeF3)
+分子 #1: TFIIH basal transcription factor complex helicase XPD subunit
+分子 #2: General transcription factor IIH subunit 1
+分子 #3: General transcription factor IIH subunit 4
+分子 #4: CDK-activating kinase assembly factor MAT1
+分子 #5: General transcription factor IIH subunit 3
+分子 #6: General transcription factor IIH subunit 5
+分子 #7: General transcription factor IIH subunit 2
+分子 #8: General transcription and DNA repair factor IIH helicase subunit XPB
+分子 #11: General transcription factor IIE subunit 1
+分子 #12: Unassigned Peptide, likely XPB
+分子 #13: Unassigned Peptide, likely TFIIE-Beta
+分子 #9: Non-template DNA
+分子 #10: Template DNA
+分子 #14: IRON/SULFUR CLUSTER
+分子 #15: ZINC ION
+分子 #16: ADENOSINE-5'-DIPHOSPHATE
+分子 #17: MAGNESIUM ION
+分子 #18: BERYLLIUM TRIFLUORIDE ION
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 43.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー


















































 X (Sec.)
X (Sec.) Y (Row.)
Y (Row.) Z (Col.)
Z (Col.)
















































 Trichoplusia ni (イラクサキンウワバ)
Trichoplusia ni (イラクサキンウワバ)