-検索条件
-検索結果
検索 (著者・登録者: jing & d)の結果2,444件中、1から50件目までを表示しています

EMDB-40954: 
ADP-bound Bcs1 (C7 symmetrized)

EMDB-41061: 
ATP-1 state of Bcs1 (C7 symmetrized)

EMDB-41095: 
ADP-bound Bcs1 (unsymmetrized)

EMDB-41148: 
Apo Bcs1, unsymmetrized

EMDB-41276: 
ATP-1 state of Bcs1 (unsymmetrized)
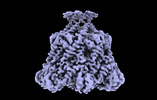
EMDB-41462: 
ATP-2 state of Bcs1 (C7 symmetrized)
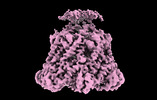
EMDB-41476: 
ATP-2 state of Bcs1 (unsymmetrized)

EMDB-41609: 
Bcs1 bound with ISP-ED

PDB-8t14: 
ADP-bound Bcs1 (C7 symmetrized)

PDB-8t5u: 
ATP-1 state of Bcs1 (C7 symmetrized)

PDB-8t7u: 
ADP-bound Bcs1 (unsymmetrized)

PDB-8tby: 
Apo Bcs1, unsymmetrized

PDB-8ti0: 
ATP-1 state of Bcs1 (unsymmetrized)

PDB-8tp1: 
ATP-2 state of Bcs1 (C7 symmetrized)

PDB-8tpl: 
ATP-2 state of Bcs1 (unsymmetrized)

EMDB-35827: 
Structure of CbCas9 bound to 20-nucleotide complementary DNA substrate

EMDB-37652: 
Structure of CbCas9 bound to 6-nucleotide complementary DNA substrate

EMDB-37656: 
Structure of CbCas9-PcrIIC1 complex bound to 28-bp DNA substrate (20-nt complementary)

EMDB-37657: 
Structure of CbCas9-PcrIIC1 complex bound to 62-bp DNA substrate (symmetric 20-nt complementary)

EMDB-37762: 
Structure of CbCas9-PcrIIC1 complex bound to 62-bp DNA substrate (non-targeting complex)

PDB-8iyq: 
Structure of CbCas9 bound to 20-nucleotide complementary DNA substrate

PDB-8wmh: 
Structure of CbCas9 bound to 6-nucleotide complementary DNA substrate

PDB-8wmm: 
Structure of CbCas9-PcrIIC1 complex bound to 28-bp DNA substrate (20-nt complementary)

PDB-8wmn: 
Structure of CbCas9-PcrIIC1 complex bound to 62-bp DNA substrate (symmetric 20-nt complementary)

PDB-8wr4: 
Structure of CbCas9-PcrIIC1 complex bound to 62-bp DNA substrate (non-targeting complex)

EMDB-38059: 
Cryo-EM structure of human gamma-secretase in complex with Abeta49

EMDB-38060: 
Cryo-EM structure of human gamma-secretase in complex with Abeta46

EMDB-38061: 
Cryo-EM structure of human gamma-secretase in complex with APP-C99

EMDB-40261: 
DDB1/CRBN in complex with ARV-471 and the ER ligand-binding domain

EMDB-43753: 
Yeast U1 snRNP with humanized U1C Zinc-Finger domain

PDB-8w2o: 
Yeast U1 snRNP with humanized U1C Zinc-Finger domain
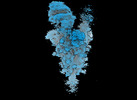
EMDB-18639: 
Locally refined SARS-CoV-2 BA-2.86 Spike receptor binding domain (RBD) complexed with angiotensin converting enzyme 2 (ACE2)

EMDB-18649: 
Local refinement of SARS-CoV-2 BA.2.86 Spike and XBB-7 Fab

EMDB-19002: 
XBB-4 Fab in complex with SARS-CoV-2 BA.2.12.1 Spike Glycoprotein

PDB-8qsq: 
Locally refined SARS-CoV-2 BA-2.86 Spike receptor binding domain (RBD) complexed with angiotensin converting enzyme 2 (ACE2)

PDB-8qtd: 
Local refinement of SARS-CoV-2 BA.2.86 Spike and XBB-7 Fab

PDB-8r8k: 
XBB-4 Fab in complex with SARS-CoV-2 BA.2.12.1 Spike Glycoprotein

EMDB-36659: 
Structure of human TRPV4 with antagonist A1

EMDB-36660: 
Structure of human TRPV4 with antagonist GSK279
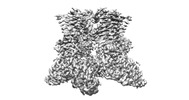
EMDB-36675: 
Structure of human TRPV4 with antagonist A2

EMDB-36676: 
Structure of human TRPV4 with antagonist A2 and RhoA

PDB-8ju5: 
Structure of human TRPV4 with antagonist A1

PDB-8ju6: 
Structure of human TRPV4 with antagonist GSK279

PDB-8jvi: 
Structure of human TRPV4 with antagonist A2

PDB-8jvj: 
Structure of human TRPV4 with antagonist A2 and RhoA

EMDB-36732: 
Cryo-EM structure of the gasdermin pore from Trichoplax adhaerens

EMDB-36733: 
Cryo-EM structure of the gasdermin pore from Trichoplax adhaerens

EMDB-36734: 
Cryo-EM structure of RCD-1 pore from Neurospora crassa

PDB-8jyw: 
Cryo-EM structure of the gasdermin pore from Trichoplax adhaerens

PDB-8jyz: 
Cryo-EM structure of RCD-1 pore from Neurospora crassa
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
