-検索条件
-検索結果
検索 (著者・登録者: duan & p)の結果308件中、1から50件目までを表示しています

EMDB-41610: 
AT8-Phosphomimetic Tau Filaments (Full-length, Cofactor-Free 0N4R Tau S202E, T205E, S208E)

EMDB-41611: 
PHF1-Phosphomimetic Tau Filaments (Full-length, Cofactor-Free 0N4R Tau S396E, S400E, T403E, S404E)
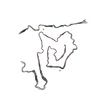
PDB-8ttl: 
AT8-Phosphomimetic Tau Filaments (Full-length, Cofactor-Free 0N4R Tau S202E, T205E, S208E)

PDB-8ttn: 
PHF1-Phosphomimetic Tau Filaments (Full-length, Cofactor-Free 0N4R Tau S396E, S400E, T403E, S404E)

EMDB-43824: 
Tau(291-407)-4E QHF

EMDB-43826: 
Tau(291-407)-4E THF

EMDB-44421: 
Tau(291-407)-4E THF type II

EMDB-44422: 
PHF filament generated from 4E-Tau(297-407) under neutral Mg2+ condition
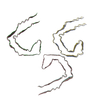
PDB-9bbl: 
THF filament generated from 4E-Tau(297-407) under neutral Mg2+ condition

PDB-9bbm: 
PHF filament generated from 4E-Tau(297-407) under neutral Mg2+ condition

EMDB-34928: 
Cryo-EM structure of SARS-CoV-2 Omicron BA.2 S-trimer in complex with fab L4.65 and L5.34

EMDB-34940: 
Cryo-EM structure of SARS-CoV-2 Omicron BA.4 S-trimer in complex with fab L4.65 and L5.34

EMDB-34945: 
Cryo-EM structure of SARS-CoV-2 Omicron Prototype S-trimer in complex with fab L4.65 and L5.34

PDB-8hp9: 
Cryo-EM structure of SARS-CoV-2 Omicron BA.2 S-trimer in complex with fab L4.65 and L5.34

PDB-8hpq: 
Cryo-EM structure of SARS-CoV-2 Omicron BA.4 S-trimer in complex with fab L4.65 and L5.34

PDB-8hpv: 
Cryo-EM structure of SARS-CoV-2 Omicron Prototype S-trimer in complex with fab L4.65 and L5.34

EMDB-41048: 
Lassa GPC Trimer in complex with Fab 8.11G and nanobody D5

PDB-8t5c: 
Lassa GPC Trimer in complex with Fab 8.11G and nanobody D5

EMDB-37008: 
16d-bound human SPNS2

PDB-8kae: 
16d-bound human SPNS2
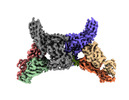
EMDB-34174: 
Structure of beta-arrestin2 in complex with a phosphopeptide corresponding to the human Atypical chemokine receptor 2, ACKR2 (D6R)
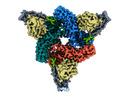
EMDB-36078: 
Structure of beta-arrestin2 in complex with M2Rpp
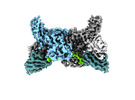
EMDB-36081: 
Structure of beta-arrestin2 in complex with D6Rpp (Local Refine)
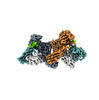
EMDB-36082: 
Structure of beta-arrestin1 in complex with D6Rpp
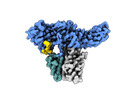
EMDB-36090: 
Structure of Muscarinic receptor (M2R) in complex with beta-arrestin1 (Local refine, cross-linked)
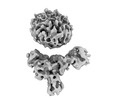
EMDB-36091: 
Muscarinic receptor (M2R) in complex with beta-arrestin1 (Low resolution full map, Cross-linked)
EMDB-36093: 
Muscarinic receptor (M2R) in complex with beta-arrestin1 (Low resolution full map, non-crosslinked)

EMDB-36110: 
Structure of basal beta-arrestin2
EMDB-36124: 
Structure of beta-arrestin1 in complex with C3aRpp
EMDB-36126: 
Structure of Muscarinic receptor (M2R) in complex with beta-arrestin1 (Local Refine, non-cross linked)

PDB-8go9: 
Structure of beta-arrestin2 in complex with a phosphopeptide corresponding to the human Atypical chemokine receptor 2, ACKR2 (D6R)

PDB-8j8r: 
Structure of beta-arrestin2 in complex with M2Rpp

PDB-8j8v: 
Structure of beta-arrestin2 in complex with D6Rpp (Local Refine)

PDB-8j8z: 
Structure of beta-arrestin1 in complex with D6Rpp

PDB-8j97: 
Structure of Muscarinic receptor (M2R) in complex with beta-arrestin1 (Local refine, cross-linked)

PDB-8j9k: 
Structure of basal beta-arrestin2

PDB-8ja3: 
Structure of beta-arrestin1 in complex with C3aRpp

PDB-8jaf: 
Structure of Muscarinic receptor (M2R) in complex with beta-arrestin1 (Local Refine, non-cross linked)
EMDB-34931: 
Cryo-EM structure of SARS-CoV-2 Omicron BA.2 RBD in complex with fab L4.65 and L5.34

EMDB-34944: 
Cryo-EM structure of SARS-CoV-2 Omicron BA.4 RBD in complex with fab L4.65 and L5.34

EMDB-34946: 
Cryo-EM structure of SARS-CoV-2 Omicron Prototype RBD in complex with fab L4.65 and L5.34

PDB-8hpf: 
Cryo-EM structure of SARS-CoV-2 Omicron BA.2 RBD in complex with fab L4.65 and L5.34

PDB-8hpu: 
Cryo-EM structure of SARS-CoV-2 Omicron BA.4 RBD in complex with fab L4.65 and L5.34

PDB-8hq7: 
Cryo-EM structure of SARS-CoV-2 Omicron Prototype RBD in complex with fab L4.65 and L5.34

EMDB-41167: 
GMPCPP-microtubule C1 reconstruction

EMDB-41169: 
GMPCPP-microtubule decorated with Abl2-557-1090

EMDB-41170: 
Protofilament reconstruction of microtubule decorated with Abl2-557-1090 (consensus map)

EMDB-41173: 
Protofilament reconstruction of microtubule decorated with Abl2-557-1090, Class 1

EMDB-41176: 
Protofilament reconstruction of microtubule decorated with Abl2-557-1090, Class 2

EMDB-41177: 
Protofilament reconstruction of microtubule decorated with Abl2-557-1090, Class 3
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
