-検索条件
-検索結果
検索 (著者・登録者: david & s)の結果5,548件中、1から50件目までを表示しています

EMDB-43746: 
Plasmodium falciparum 20S proteasome bound to an inhibitor

PDB-8w2f: 
Plasmodium falciparum 20S proteasome bound to an inhibitor

EMDB-28547: 
Cryo-EM structure of PRC2 in complex with the long isoform of AEBP2

PDB-8eqv: 
Cryo-EM structure of PRC2 in complex with the long isoform of AEBP2

EMDB-43435: 
Prefusion stabilized structure of the SARS-CoV-2 fusion machinery

EMDB-43436: 
Prefusion stabilized structure of the SARS-CoV-2 fusion machinery

EMDB-43437: 
Prefusion stabilized structure of the SARS-CoV-2 fusion machinery

PDB-8vq9: 
Prefusion stabilized structure of the SARS-CoV-2 fusion machinery

PDB-8vqa: 
Prefusion stabilized structure of the SARS-CoV-2 fusion machinery

PDB-8vqb: 
Prefusion stabilized structure of the SARS-CoV-2 fusion machinery

EMDB-43700: 
Cryo-EM map of LKB1-STRADalpha-MO25alpha from TFS Glacios with Gatan Alpine detector at 120 keV

EMDB-43701: 
Cryo-EM map of LKB1-STRADalpha-MO25alpha from TFS Glacios with Gatan Alpine detector at 200 keV

EMDB-43702: 
Cryo-EM map of LKB1-STRADalpha-MO25alpha from TFS Glacios with Gatan K3 detector at 200 keV

EMDB-43506: 
Cryo-EM structure of LKB1-STRADalpha-MO25alpha heterocomplex

PDB-8vsu: 
Cryo-EM structure of LKB1-STRADalpha-MO25alpha heterocomplex
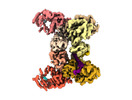
EMDB-41785: 
DdmD dimer in complex with ssDNA
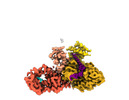
EMDB-41790: 
DdmD monomer in complex with ssDNA

EMDB-41865: 
DdmDE handover complex

PDB-8u0u: 
DdmD dimer in complex with ssDNA

PDB-8u0w: 
DdmD monomer in complex with ssDNA

PDB-8u3k: 
DdmDE handover complex

EMDB-43527: 
Apoferritin at 100 keV on Alpine detector with a side-entry cryoholder
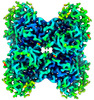
EMDB-43528: 
Aldolase at 100 keV on the Alpine detector with a side-entry cryoholder
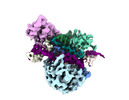
EMDB-41781: 
DdmE in complex with guide and target DNA

EMDB-44825: 
DdmD dimer apoprotein (CASP target)

PDB-8u0j: 
DdmE in complex with guide and target DNA

PDB-9bqv: 
DdmD dimer apoprotein

EMDB-19929: 
Structural basis of D9-THC analog activity at the Cannabinoid 1 receptor

PDB-9erx: 
Structural basis of D9-THC analog activity at the Cannabinoid 1 receptor
EMDB-41460: 
Structure of a mutated photosystem II complex reveals perturbation of the oxygen-evolving complex

PDB-8tow: 
Structure of a mutated photosystem II complex reveals perturbation of the oxygen-evolving complex

EMDB-50090: 
Vibrio cholerae DdmD apo complex

PDB-9ezx: 
Vibrio cholerae DdmD apo complex

EMDB-19163: 
Trimeric HSV-1F gB ectodomain in postfusion conformation with three bound HDIT101 Fab molecules.

EMDB-19164: 
Trimeric HSV-1F gB ectodomain in postfusion conformation with three bound HDIT102 Fab molecules.

EMDB-19165: 
Trimeric HSV-2F gB ectodomain in postfusion conformation with three bound HDIT101 Fab molecules.

EMDB-19166: 
Trimeric HSV-2G gB ectodomain in postfusion conformation with three bound HDIT102 Fab molecules.

PDB-8rgz: 
Trimeric HSV-1F gB ectodomain in postfusion conformation with three bound HDIT101 Fab molecules.

PDB-8rh0: 
Trimeric HSV-1F gB ectodomain in postfusion conformation with three bound HDIT102 Fab molecules.

PDB-8rh1: 
Trimeric HSV-2F gB ectodomain in postfusion conformation with three bound HDIT101 Fab molecules.

PDB-8rh2: 
Trimeric HSV-2G gB ectodomain in postfusion conformation with three bound HDIT102 Fab molecules.

EMDB-41569: 
Cryo-EM structure of HmAb64 scFv in complex with CNE40 SOSIP trimer

PDB-8tr3: 
Cryo-EM structure of HmAb64 scFv in complex with CNE40 SOSIP trimer

EMDB-40981: 
BG505 Boost2 SOSIP.664 in complex with NHP polyclonal antibody FP3

EMDB-40982: 
BG505 Boost2 SOSIP.664 in complex with NHP polyclonal antibody N289

PDB-8t2e: 
BG505 Boost2 SOSIP.664 in complex with NHP polyclonal antibody FP3

PDB-8t2f: 
BG505 Boost2 SOSIP.664 in complex with NHP polyclonal antibody N289

EMDB-17377: 
Structure of human SIT1 (focussed map / refinement)

EMDB-17378: 
Structure of human SIT1:ACE2 complex (open PD conformation)

EMDB-17379: 
Structure of human SIT1:ACE2 complex (closed PD conformation)
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
