+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-0070 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
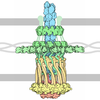
| タイトル | Structure of the type IV pilus from enterohemorrhagic Escherichia coli (EHEC) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 | Prokaryotic N-terminal methylation site. / Prokaryotic N-terminal methylation motif / Prokaryotic N-terminal methylation site /  Pilin-like / Pilin-like /  生体膜 / Prepilin peptidase-dependent pilin 生体膜 / Prepilin peptidase-dependent pilin 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |   Escherichia coli O157:H7 (大腸菌) Escherichia coli O157:H7 (大腸菌) | |||||||||
| 手法 | らせん対称体再構成法 /  クライオ電子顕微鏡法 / 解像度: 8.0 Å クライオ電子顕微鏡法 / 解像度: 8.0 Å | |||||||||
 データ登録者 データ登録者 | Zheng W / Egelman E / Bardiaux B / Luna-Rico A / Izadi-Pruneyre N / Francetic O | |||||||||
| 資金援助 |  フランス, 1件 フランス, 1件
| |||||||||
 引用 引用 |  ジャーナル: Structure / 年: 2019 ジャーナル: Structure / 年: 2019タイトル: Structure and Assembly of the Enterohemorrhagic Escherichia coli Type 4 Pilus. 著者: Benjamin Bardiaux / Gisele Cardoso de Amorim / Areli Luna Rico / Weili Zheng / Ingrid Guilvout / Camille Jollivet / Michael Nilges / Edward H Egelman / Nadia Izadi-Pruneyre / Olivera Francetic /   要旨: Bacterial type 4a pili are dynamic surface filaments that promote bacterial adherence, motility, and macromolecular transport. Their genes are highly conserved among enterobacteria and their ...Bacterial type 4a pili are dynamic surface filaments that promote bacterial adherence, motility, and macromolecular transport. Their genes are highly conserved among enterobacteria and their expression in enterohemorrhagic Escherichia coli (EHEC) promotes adhesion to intestinal epithelia and pro-inflammatory signaling. To define the molecular basis of EHEC pilus assembly, we determined the structure of the periplasmic domain of its major subunit PpdD (PpdDp), a prototype of an enterobacterial pilin subfamily containing two disulfide bonds. The structure of PpdDp, determined by NMR, was then docked into the density envelope of purified EHEC pili obtained by cryoelectron microscopy (cryo-EM). Cryo-EM reconstruction of EHEC pili at ∼8 Å resolution revealed extremely high pilus flexibility correlating with a large extended region of the pilin stem. Systematic mutagenesis combined with functional and interaction analyses identified charged residues essential for pilus assembly. Structural information on exposed regions and interfaces between EHEC pilins is relevant for vaccine and drug discovery. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_0070.map.gz emd_0070.map.gz | 3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-0070-v30.xml emd-0070-v30.xml emd-0070.xml emd-0070.xml | 11.6 KB 11.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_0070.png emd_0070.png | 35.1 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-0070 http://ftp.pdbj.org/pub/emdb/structures/EMD-0070 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0070 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0070 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_0070.map.gz / 形式: CCP4 / 大きさ: 27 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_0070.map.gz / 形式: CCP4 / 大きさ: 27 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.09 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : EHEC type IV pili
| 全体 | 名称: EHEC type IV pili |
|---|---|
| 要素 |
|
-超分子 #1: EHEC type IV pili
| 超分子 | 名称: EHEC type IV pili / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli O157:H7 (大腸菌) Escherichia coli O157:H7 (大腸菌) |
| 組換発現 | 生物種:   Escherichia coli BL21(DE3) (大腸菌) Escherichia coli BL21(DE3) (大腸菌) |
-分子 #1: Prepilin peptidase-dependent protein D
| 分子 | 名称: Prepilin peptidase-dependent protein D / タイプ: protein_or_peptide / ID: 1 / コピー数: 14 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli O157:H7 (大腸菌) Escherichia coli O157:H7 (大腸菌) |
| 分子量 | 理論値: 14.883821 KDa |
| 組換発現 | 生物種:   Escherichia coli BL21(DE3) (大腸菌) Escherichia coli BL21(DE3) (大腸菌) |
| 配列 | 文字列: FTLIELMVVI GIIAILSAIG IPAYQNYLRK AALTDMLQTF VPYRTAVELC ALEHGGLDTC DGGSNGIPSP TTTRYVSAMS VAKGVVSLT GQESLNGLSV VMTPGWDNAN GVTGWARNCN IQSDSALQQA CEDVFRFDDA N |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | filament |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| グリッド | 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: LACEY / 前処理 - タイプ: PLASMA CLEANING |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 297 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: INTEGRATING / 撮影したグリッド数: 1 / 平均露光時間: 2.0 sec. / 平均電子線量: 1.4 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| CTF補正 | ソフトウェア - 名称: CTFFIND (ver. 3) |
|---|---|
| 初期モデル | モデルのタイプ: OTHER / 詳細: featureless cylinder |
| 最終 角度割当 | タイプ: NOT APPLICABLE |
| 最終 再構成 | 想定した対称性 - らせんパラメータ - Δz: 11.2 Å 想定した対称性 - らせんパラメータ - ΔΦ: 96 ° 想定した対称性 - らせんパラメータ - 軸対称性: C1 (非対称) 解像度のタイプ: BY AUTHOR / 解像度: 8.0 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: SPIDER / 使用した粒子像数: 25669 |
-原子モデル構築 1
| 詳細 | Soluble domain structure and homology model of TM segment fitted as rigid-bodies. Linker region built ab initio. Real-space refinement after symmetrization. |
|---|---|
| 精密化 | 空間: REAL / プロトコル: OTHER |
| 得られたモデル |  PDB-6gv9: |
 ムービー
ムービー コントローラー
コントローラー