+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8k82 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of the yeast 80S ribosome with tigecycline, Not5 and P-site tRNA | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | RIBOSOME / 80S ribosome / tigecycline / antibiotic | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報CCR4-NOT core complex / deadenylation-independent decapping of nuclear-transcribed mRNA / regulation of stem cell population maintenance / nuclear-transcribed mRNA poly(A) tail shortening / deadenylation-dependent decapping of nuclear-transcribed mRNA / maturation of SSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, LSU-rRNA,5S) / negative regulation of glucose mediated signaling pathway / negative regulation of translational frameshifting / Negative regulators of DDX58/IFIH1 signaling / positive regulation of translational fidelity ...CCR4-NOT core complex / deadenylation-independent decapping of nuclear-transcribed mRNA / regulation of stem cell population maintenance / nuclear-transcribed mRNA poly(A) tail shortening / deadenylation-dependent decapping of nuclear-transcribed mRNA / maturation of SSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, LSU-rRNA,5S) / negative regulation of glucose mediated signaling pathway / negative regulation of translational frameshifting / Negative regulators of DDX58/IFIH1 signaling / positive regulation of translational fidelity / Protein methylation / RMTs methylate histone arginines / mTORC1-mediated signalling / Protein hydroxylation / ribosome-associated ubiquitin-dependent protein catabolic process / GDP-dissociation inhibitor activity / positive regulation of nuclear-transcribed mRNA catabolic process, deadenylation-dependent decay / pre-mRNA 5'-splice site binding / Formation of the ternary complex, and subsequently, the 43S complex / Translation initiation complex formation / Ribosomal scanning and start codon recognition / cleavage in ITS2 between 5.8S rRNA and LSU-rRNA of tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / preribosome, small subunit precursor / response to cycloheximide / mRNA destabilization / Major pathway of rRNA processing in the nucleolus and cytosol / SRP-dependent cotranslational protein targeting to membrane / GTP hydrolysis and joining of the 60S ribosomal subunit / Formation of a pool of free 40S subunits / Nonsense Mediated Decay (NMD) independent of the Exon Junction Complex (EJC) / Nonsense Mediated Decay (NMD) enhanced by the Exon Junction Complex (EJC) / negative regulation of mRNA splicing, via spliceosome / L13a-mediated translational silencing of Ceruloplasmin expression / preribosome, large subunit precursor / ribosomal large subunit export from nucleus / endonucleolytic cleavage to generate mature 3'-end of SSU-rRNA from (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / G-protein alpha-subunit binding / positive regulation of protein kinase activity / protein-RNA complex assembly / regulation of translational fidelity / Ub-specific processing proteases / ribosomal small subunit export from nucleus / translation regulator activity / ribosomal subunit export from nucleus / translational termination / endonucleolytic cleavage in ITS1 to separate SSU-rRNA from 5.8S rRNA and LSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / DNA-(apurinic or apyrimidinic site) endonuclease activity / cellular response to amino acid starvation / ribosome assembly / rescue of stalled ribosome / maturation of LSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / 90S preribosome / maturation of SSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / maturation of LSU-rRNA / ribosomal large subunit biogenesis / maturation of SSU-rRNA / transcription elongation by RNA polymerase II / macroautophagy / positive regulation of transcription elongation by RNA polymerase II / small-subunit processome / positive regulation of apoptotic signaling pathway / protein kinase C binding / maintenance of translational fidelity / P-body / ribosomal large subunit assembly / cytoplasmic stress granule / modification-dependent protein catabolic process / rRNA processing / protein tag activity / ribosome biogenesis / ribosome binding / ribosomal small subunit biogenesis / ribosomal small subunit assembly / small ribosomal subunit / small ribosomal subunit rRNA binding / 5S rRNA binding / large ribosomal subunit rRNA binding / cytosolic small ribosomal subunit / cytosolic large ribosomal subunit / cytoplasmic translation / rRNA binding / negative regulation of translation / ribosome / protein ubiquitination / structural constituent of ribosome / translation / positive regulation of protein phosphorylation / G protein-coupled receptor signaling pathway / negative regulation of gene expression / response to antibiotic / mRNA binding / ubiquitin protein ligase binding / nucleolus / mitochondrion / RNA binding / zinc ion binding / nucleoplasm / nucleus / metal ion binding / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3 Å | ||||||
 データ登録者 データ登録者 | Buschauer, R. / Beckmann, R. / Cheng, J. | ||||||
| 資金援助 | 1件
| ||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2024 ジャーナル: Nat Commun / 年: 2024タイトル: Structural basis for differential inhibition of eukaryotic ribosomes by tigecycline. 著者: Xiang Li / Mengjiao Wang / Timo Denk / Robert Buschauer / Yi Li / Roland Beckmann / Jingdong Cheng /   要旨: Tigecycline is widely used for treating complicated bacterial infections for which there are no effective drugs. It inhibits bacterial protein translation by blocking the ribosomal A-site. However, ...Tigecycline is widely used for treating complicated bacterial infections for which there are no effective drugs. It inhibits bacterial protein translation by blocking the ribosomal A-site. However, even though it is also cytotoxic for human cells, the molecular mechanism of its inhibition remains unclear. Here, we present cryo-EM structures of tigecycline-bound human mitochondrial 55S, 39S, cytoplasmic 80S and yeast cytoplasmic 80S ribosomes. We find that at clinically relevant concentrations, tigecycline effectively targets human 55S mitoribosomes, potentially, by hindering A-site tRNA accommodation and by blocking the peptidyl transfer center. In contrast, tigecycline does not bind to human 80S ribosomes under physiological concentrations. However, at high tigecycline concentrations, in addition to blocking the A-site, both human and yeast 80S ribosomes bind tigecycline at another conserved binding site restricting the movement of the L1 stalk. In conclusion, the observed distinct binding properties of tigecycline may guide new pathways for drug design and therapy. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8k82.cif.gz 8k82.cif.gz | 4.5 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8k82.ent.gz pdb8k82.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  8k82.json.gz 8k82.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  8k82_validation.pdf.gz 8k82_validation.pdf.gz | 2.1 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  8k82_full_validation.pdf.gz 8k82_full_validation.pdf.gz | 2.2 MB | 表示 | |
| XML形式データ |  8k82_validation.xml.gz 8k82_validation.xml.gz | 347.9 KB | 表示 | |
| CIF形式データ |  8k82_validation.cif.gz 8k82_validation.cif.gz | 607.3 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/k8/8k82 https://data.pdbj.org/pub/pdb/validation_reports/k8/8k82 ftp://data.pdbj.org/pub/pdb/validation_reports/k8/8k82 ftp://data.pdbj.org/pub/pdb/validation_reports/k8/8k82 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  36945  36836  36837  36838  36839  38629  38630  38631  38632  38633  38634  38635  38636  38637  38638  38639  39455  39456  8k2aC  8k2bC  8k2cC  8k2dC  8xsxC  8xsyC  8xszC  8xt0C  8xt1C  8xt2C  8xt3C  8yooC  8yopC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-RNA鎖 , 6種, 6分子 C2C7C5C1C4C3
| #1: RNA鎖 | 分子量: 579761.938 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|---|
| #2: RNA鎖 | 分子量: 935.620 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #3: RNA鎖 | 分子量: 24487.846 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #4: RNA鎖 | 分子量: 1097493.875 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #5: RNA鎖 | 分子量: 38951.105 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #6: RNA鎖 | 分子量: 50682.922 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
-Small ribosomal subunit protein ... , 18種, 18分子 SASDSFSKSLSMSPSQSRSSSTSUSVSZSaScSdSg
| #7: タンパク質 | 分子量: 28051.330 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|---|
| #10: タンパク質 | 分子量: 26542.789 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #12: タンパク質 | 分子量: 25072.600 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #17: タンパク質 | 分子量: 12757.445 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #18: タンパク質 | 分子量: 17785.934 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #19: タンパク質 | 分子量: 15488.631 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #22: タンパク質 | 分子量: 16031.907 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #23: タンパク質 | 分子量: 15877.490 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #24: タンパク質 | 分子量: 15820.413 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #25: タンパク質 | 分子量: 17071.641 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #26: タンパク質 | 分子量: 15942.125 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #27: タンパク質 | 分子量: 13929.044 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #28: タンパク質 | 分子量: 9758.829 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #32: タンパク質 | 分子量: 12067.272 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #33: タンパク質 | 分子量: 13480.886 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #35: タンパク質 | 分子量: 7605.847 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #36: タンパク質 | 分子量: 6675.723 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #39: タンパク質 | 分子量: 34841.219 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
-40S ribosomal protein ... , 14種, 14分子 SBSCSESGSHSISJSNSOSWSXSYSbSe
| #8: タンパク質 | 分子量: 28798.467 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|---|
| #9: タンパク質 | 分子量: 27490.826 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #11: タンパク質 | 分子量: 29469.330 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #13: タンパク質 | 分子量: 27054.486 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #14: タンパク質 | 分子量: 21658.209 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #15: タンパク質 | 分子量: 22537.803 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #16: タンパク質 | 分子量: 22487.893 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #20: タンパク質 | 分子量: 17059.945 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #21: タンパク質 | 分子量: 14562.655 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #29: タンパク質 | 分子量: 14650.062 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #30: タンパク質 | 分子量: 16073.896 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #31: タンパク質 | 分子量: 15362.848 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #34: タンパク質 | 分子量: 8893.391 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #37: タンパク質 | 分子量: 7137.541 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
-Ubiquitin-ribosomal protein ... , 2種, 2分子 SfLm
| #38: タンパク質 | 分子量: 17254.227 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|---|
| #78: タンパク質 | 分子量: 14583.077 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
+Large ribosomal subunit protein ... , 43種, 44分子 LALBLCLDLELFLGLHLILJLKLLLMLNLOLPLQLRLSLTLULVLWLXLYLZLaLbLcLd...
-タンパク質 , 1種, 1分子 CN
| #84: タンパク質 | 分子量: 65948.500 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|
-非ポリマー , 4種, 332分子 
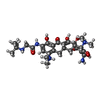





| #85: 化合物 | ChemComp-MG / #86: 化合物 | ChemComp-T1C / #87: 化合物 | ChemComp-SPD / | #88: 化合物 | ChemComp-ZN / |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: yeast 80S ribosome / タイプ: RIBOSOME / Entity ID: #1-#84 / 由来: NATURAL |
|---|---|
| 由来(天然) | 生物種:  |
| 緩衝液 | pH: 7.4 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 3500 nm / 最小 デフォーカス(公称値): 1000 nm |
| 撮影 | 電子線照射量: 44 e/Å2 フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) |
- 解析
解析
| CTF補正 | 詳細: Relion / タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION |
|---|---|
| 3次元再構成 | 解像度: 3 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 140917 / 対称性のタイプ: POINT |
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj



































