[English] 日本語
 Yorodumi
Yorodumi- PDB-6tpn: Crystal structure of the Orexin-2 receptor in complex with HTL664... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 6tpn | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal structure of the Orexin-2 receptor in complex with HTL6641 at 2.61 A resolution | ||||||
 Components Components | Orexin receptor type 2,GlgA glycogen synthase,Orexin receptor type 2 | ||||||
 Keywords Keywords | MEMBRANE PROTEIN / 7TM / GPCR | ||||||
| Function / homology |  Function and homology information Function and homology informationregulation of circadian sleep/wake cycle, wakefulness / circadian sleep/wake cycle process / orexin receptor activity / Orexin and neuropeptides FF and QRFP bind to their respective receptors / alpha-1,4-glucan glucosyltransferase (UDP-glucose donor) activity / neuropeptide receptor activity / feeding behavior / locomotion / peptide hormone binding / regulation of cytosolic calcium ion concentration ...regulation of circadian sleep/wake cycle, wakefulness / circadian sleep/wake cycle process / orexin receptor activity / Orexin and neuropeptides FF and QRFP bind to their respective receptors / alpha-1,4-glucan glucosyltransferase (UDP-glucose donor) activity / neuropeptide receptor activity / feeding behavior / locomotion / peptide hormone binding / regulation of cytosolic calcium ion concentration / cellular response to hormone stimulus / neuropeptide signaling pathway / glucose homeostasis / phospholipase C-activating G protein-coupled receptor signaling pathway / G alpha (q) signalling events / chemical synaptic transmission / synapse / nucleoplasm / plasma membrane Similarity search - Function | ||||||
| Biological species |  Homo sapiens (human) Homo sapiens (human)  Pyrococcus abyssi (archaea) Pyrococcus abyssi (archaea) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / MOLECULAR REPLACEMENT /  molecular replacement / Resolution: 2.608 Å molecular replacement / Resolution: 2.608 Å | ||||||
 Authors Authors | Rappas, M. / Ali, A. / Bennett, K.A. / Brown, J.D. / Bucknell, S.J. / Congreve, M. / Cooke, R.M. / Cseke, G. / de Graaf, C. / Dore, A.S. ...Rappas, M. / Ali, A. / Bennett, K.A. / Brown, J.D. / Bucknell, S.J. / Congreve, M. / Cooke, R.M. / Cseke, G. / de Graaf, C. / Dore, A.S. / Errey, J.C. / Jazayeri, A. / Marshall, F.H. / Mason, J.S. / Mould, R. / Patel, J.C. / Tehan, B.G. / Weir, M. / Christopher, J.A. | ||||||
| Funding support |  United States, 1items United States, 1items
| ||||||
 Citation Citation |  Journal: J.Med.Chem. / Year: 2020 Journal: J.Med.Chem. / Year: 2020Title: Comparison of Orexin 1 and Orexin 2 Ligand Binding Modes Using X-ray Crystallography and Computational Analysis. Authors: Rappas, M. / Ali, A.A.E. / Bennett, K.A. / Brown, J.D. / Bucknell, S.J. / Congreve, M. / Cooke, R.M. / Cseke, G. / de Graaf, C. / Dore, A.S. / Errey, J.C. / Jazayeri, A. / Marshall, F.H. / ...Authors: Rappas, M. / Ali, A.A.E. / Bennett, K.A. / Brown, J.D. / Bucknell, S.J. / Congreve, M. / Cooke, R.M. / Cseke, G. / de Graaf, C. / Dore, A.S. / Errey, J.C. / Jazayeri, A. / Marshall, F.H. / Mason, J.S. / Mould, R. / Patel, J.C. / Tehan, B.G. / Weir, M. / Christopher, J.A. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  6tpn.cif.gz 6tpn.cif.gz | 230.7 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb6tpn.ent.gz pdb6tpn.ent.gz | 183 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  6tpn.json.gz 6tpn.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/tp/6tpn https://data.pdbj.org/pub/pdb/validation_reports/tp/6tpn ftp://data.pdbj.org/pub/pdb/validation_reports/tp/6tpn ftp://data.pdbj.org/pub/pdb/validation_reports/tp/6tpn | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  6to7C  6todC  6tosC  6totC 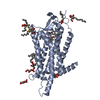 6tp3C 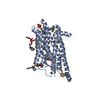 6tp4C  6tp6C  6tpgC  6tpjC  6tq4C  6tq6C  6tq7C  6tq9C  5wqcS S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
-Protein , 1 types, 1 molecules A
| #1: Protein | Mass: 64520.121 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Homo sapiens (human), (gene. exp.) Homo sapiens (human), (gene. exp.)   Pyrococcus abyssi (strain GE5 / Orsay) (archaea) Pyrococcus abyssi (strain GE5 / Orsay) (archaea)Gene: HCRTR2, PAB2292 / Production host:  |
|---|
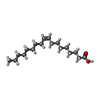
-Non-polymers , 5 types, 55 molecules 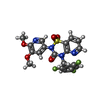







| #2: Chemical | ChemComp-NU8 / | ||||||
|---|---|---|---|---|---|---|---|
| #3: Chemical | | #4: Chemical | #5: Chemical | ChemComp-OLA / #6: Water | ChemComp-HOH / | |
-Details
| Has ligand of interest | Y |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.4 Å3/Da / Density % sol: 48.76 % |
|---|---|
| Crystal grow | Temperature: 293 K / Method: lipidic cubic phase Details: 100 mM trisodium citrate buffer 150-300 mM lithium nitrate or 150-300 mM potassium nitrate 28-43 % (v/v) polyethylene glycol 400 PH range: 5.0-6.0 |
-Data collection
| Diffraction | Mean temperature: 100 K / Serial crystal experiment: N |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  Diamond Diamond  / Beamline: I24 / Wavelength: 0.96863 Å / Beamline: I24 / Wavelength: 0.96863 Å |
| Detector | Type: DECTRIS PILATUS 6M / Detector: PIXEL / Date: Apr 23, 2018 |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 0.96863 Å / Relative weight: 1 |
| Reflection | Resolution: 2.608→43.488 Å / Num. obs: 11699 / % possible obs: 91.6 % / Redundancy: 8.3 % / Biso Wilson estimate: 40.91 Å2 / CC1/2: 0.996 / Net I/σ(I): 5.9 |
| Reflection shell | Resolution: 2.608→2.794 Å / Num. unique obs: 4223 / CC1/2: 0.426 |
-Phasing
| Phasing | Method:  molecular replacement molecular replacement |
|---|
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 5WQC Resolution: 2.608→41.475 Å / SU ML: 0.27 / Cross valid method: THROUGHOUT / σ(F): 1.34 / Phase error: 24.99
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 186.58 Å2 / Biso mean: 56.3158 Å2 / Biso min: 19.31 Å2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: final / Resolution: 2.608→41.475 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Rfactor Rfree error: 0
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller












 PDBj
PDBj













