+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6pw9 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of human NatE/HYPK complex | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | TRANSFERASE / NatA / Naa50 / NatE / HYPK | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報negative regulation of maintenance of mitotic sister chromatid cohesion, centromeric / mitotic sister chromatid cohesion, centromeric / protein-N-terminal-glutamate acetyltransferase activity / N-terminal methionine Nalpha-acetyltransferase NatE / N-terminal amino-acid Nalpha-acetyltransferase NatA / N-terminal protein amino acid acetylation / NatA complex / protein N-terminal-serine acetyltransferase activity / protein N-terminal-methionine acetyltransferase activity / protein-N-terminal-alanine acetyltransferase activity ...negative regulation of maintenance of mitotic sister chromatid cohesion, centromeric / mitotic sister chromatid cohesion, centromeric / protein-N-terminal-glutamate acetyltransferase activity / N-terminal methionine Nalpha-acetyltransferase NatE / N-terminal amino-acid Nalpha-acetyltransferase NatA / N-terminal protein amino acid acetylation / NatA complex / protein N-terminal-serine acetyltransferase activity / protein N-terminal-methionine acetyltransferase activity / protein-N-terminal-alanine acetyltransferase activity / protein-N-terminal amino-acid acetyltransferase activity / internal protein amino acid acetylation / N-acetyltransferase activity / histone H4 acetyltransferase activity / establishment of mitotic sister chromatid cohesion / acetyltransferase activator activity / mitotic sister chromatid cohesion / protein-lysine-acetyltransferase activity / protein acetylation / chromosome organization / 転移酵素; アシル基を移すもの; アミノアシル基以外のアシル基を移すもの / protein folding chaperone / post-translational protein modification / ribosome binding / microtubule cytoskeleton / angiogenesis / transcription regulator complex / cell differentiation / protein stabilization / nuclear body / intracellular membrane-bounded organelle / negative regulation of apoptotic process / positive regulation of DNA-templated transcription / nucleolus / protein-containing complex / RNA binding / extracellular exosome / nucleoplasm / nucleus / membrane / cytosol / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.03 Å | ||||||
 データ登録者 データ登録者 | Deng, S. / Marmorstein, R. | ||||||
| 資金援助 |  米国, 1件 米国, 1件
| ||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2020 ジャーナル: Nat Commun / 年: 2020タイトル: Molecular basis for N-terminal acetylation by human NatE and its modulation by HYPK. 著者: Sunbin Deng / Nina McTiernan / Xuepeng Wei / Thomas Arnesen / Ronen Marmorstein /   要旨: The human N-terminal acetyltransferase E (NatE) contains NAA10 and NAA50 catalytic, and NAA15 auxiliary subunits and associates with HYPK, a protein with intrinsic NAA10 inhibitory activity. NatE co- ...The human N-terminal acetyltransferase E (NatE) contains NAA10 and NAA50 catalytic, and NAA15 auxiliary subunits and associates with HYPK, a protein with intrinsic NAA10 inhibitory activity. NatE co-translationally acetylates the N-terminus of half the proteome to mediate diverse biological processes, including protein half-life, localization, and interaction. The molecular basis for how NatE and HYPK cooperate is unknown. Here, we report the cryo-EM structures of human NatE and NatE/HYPK complexes and associated biochemistry. We reveal that NAA50 and HYPK exhibit negative cooperative binding to NAA15 in vitro and in human cells by inducing NAA15 shifts in opposing directions. NAA50 and HYPK each contribute to NAA10 activity inhibition through structural alteration of the NAA10 substrate-binding site. NAA50 activity is increased through NAA15 tethering, but is inhibited by HYPK through structural alteration of the NatE substrate-binding site. These studies reveal the molecular basis for coordinated N-terminal acetylation by NatE and HYPK. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6pw9.cif.gz 6pw9.cif.gz | 213.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6pw9.ent.gz pdb6pw9.ent.gz | 164.1 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6pw9.json.gz 6pw9.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  6pw9_validation.pdf.gz 6pw9_validation.pdf.gz | 1 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  6pw9_full_validation.pdf.gz 6pw9_full_validation.pdf.gz | 1.1 MB | 表示 | |
| XML形式データ |  6pw9_validation.xml.gz 6pw9_validation.xml.gz | 34.8 KB | 表示 | |
| CIF形式データ |  6pw9_validation.cif.gz 6pw9_validation.cif.gz | 52.4 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/pw/6pw9 https://data.pdbj.org/pub/pdb/validation_reports/pw/6pw9 ftp://data.pdbj.org/pub/pdb/validation_reports/pw/6pw9 ftp://data.pdbj.org/pub/pdb/validation_reports/pw/6pw9 | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-N-alpha-acetyltransferase ... , 3種, 3分子 ABC
| #1: タンパク質 | 分子量: 19427.373 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: NAA50, MAK3, NAT13, NAT5 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: NAA50, MAK3, NAT13, NAT5 / 発現宿主:  参照: UniProt: Q9GZZ1, N-terminal methionine Nalpha-acetyltransferase NatE, 転移酵素; アシル基を移すもの; アミノアシル基以外のアシル基を移すもの |
|---|---|
| #2: タンパク質 | 分子量: 101427.562 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: NAA15, GA19, NARG1, NATH, TBDN100 Homo sapiens (ヒト) / 遺伝子: NAA15, GA19, NARG1, NATH, TBDN100発現宿主:  参照: UniProt: Q9BXJ9 |
| #3: タンパク質 | 分子量: 26522.602 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: NAA10, ARD1, ARD1A, TE2 Homo sapiens (ヒト) / 遺伝子: NAA10, ARD1, ARD1A, TE2発現宿主:  参照: UniProt: P41227, N-terminal amino-acid Nalpha-acetyltransferase NatA |
-タンパク質 , 1種, 1分子 D
| #4: タンパク質 | 分子量: 14689.457 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: HYPK, C15orf63, HSPC136 Homo sapiens (ヒト) / 遺伝子: HYPK, C15orf63, HSPC136発現宿主:  参照: UniProt: Q9NX55 |
|---|
-非ポリマー , 2種, 2分子 
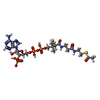

| #5: 化合物 | ChemComp-IHP / |
|---|---|
| #6: 化合物 | ChemComp-ACO / |
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 単位: MEGADALTONS / 実験値: NO | ||||||||||||||||||||||||
| 由来(天然) |
| ||||||||||||||||||||||||
| 由来(組換発現) |
| ||||||||||||||||||||||||
| 緩衝液 | pH: 7 | ||||||||||||||||||||||||
| 緩衝液成分 |
| ||||||||||||||||||||||||
| 試料 | 濃度: 1 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES | ||||||||||||||||||||||||
| 急速凍結 | 装置: FEI VITROBOT MARK II / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 289 K |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD |
| 撮影 | 電子線照射量: 1.6 e/Å2 フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) |
- 解析
解析
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION |
|---|---|
| 対称性 | 点対称性: C1 (非対称) |
| 3次元再構成 | 解像度: 4.03 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 168536 / 対称性のタイプ: POINT |
| 原子モデル構築 | プロトコル: RIGID BODY FIT / 空間: REAL |
 ムービー
ムービー コントローラー
コントローラー

















 PDBj
PDBj










