[English] 日本語
 Yorodumi
Yorodumi- PDB-6hxi: Structure of ATP citrate lyase from Methanothrix soehngenii in co... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 6hxi | ||||||
|---|---|---|---|---|---|---|---|
| Title | Structure of ATP citrate lyase from Methanothrix soehngenii in complex with citrate and coenzyme A | ||||||
 Components Components |
| ||||||
 Keywords Keywords | LYASE / ATP citrate lyase / central metabolism / acetyl-Coa / citrate shuttle / rTCA cycle / citryl-CoA / lipogenesis | ||||||
| Function / homology |  Function and homology information Function and homology informationacetate-CoA ligase (ADP-forming) activity / succinate-CoA ligase (ADP-forming) / succinate-CoA ligase complex / succinate-CoA ligase (ADP-forming) activity / ATP citrate synthase / ATP citrate synthase activity / succinyl-CoA metabolic process / acetyl-CoA biosynthetic process / tricarboxylic acid cycle / lipid metabolic process ...acetate-CoA ligase (ADP-forming) activity / succinate-CoA ligase (ADP-forming) / succinate-CoA ligase complex / succinate-CoA ligase (ADP-forming) activity / ATP citrate synthase / ATP citrate synthase activity / succinyl-CoA metabolic process / acetyl-CoA biosynthetic process / tricarboxylic acid cycle / lipid metabolic process / fatty acid biosynthetic process / lyase activity / ATP binding / cytosol Similarity search - Function | ||||||
| Biological species |  Methanosaeta concilii (archaea) Methanosaeta concilii (archaea) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 2.1 Å MOLECULAR REPLACEMENT / Resolution: 2.1 Å | ||||||
 Authors Authors | Verstraete, K. / Verschueren, K. | ||||||
| Funding support |  Belgium, 1items Belgium, 1items
| ||||||
 Citation Citation |  Journal: Nature / Year: 2019 Journal: Nature / Year: 2019Title: Structure of ATP citrate lyase and the origin of citrate synthase in the Krebs cycle. Authors: Verschueren, K.H.G. / Blanchet, C. / Felix, J. / Dansercoer, A. / De Vos, D. / Bloch, Y. / Van Beeumen, J. / Svergun, D. / Gutsche, I. / Savvides, S.N. / Verstraete, K. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  6hxi.cif.gz 6hxi.cif.gz | 839.5 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb6hxi.ent.gz pdb6hxi.ent.gz | 695.2 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  6hxi.json.gz 6hxi.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/hx/6hxi https://data.pdbj.org/pub/pdb/validation_reports/hx/6hxi ftp://data.pdbj.org/pub/pdb/validation_reports/hx/6hxi ftp://data.pdbj.org/pub/pdb/validation_reports/hx/6hxi | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  6hxhC  6hxjC  6hxkC  6hxlC  6hxmC  6hxnC  6hxoC  6hxpC  6hxqC  6qclC  6qfbC C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| Unit cell |
|
- Components
Components
-Protein , 2 types, 4 molecules ACBD
| #1: Protein | Mass: 47307.359 Da / Num. of mol.: 2 Source method: isolated from a genetically manipulated source Details: ACL-A subunit of the heteromeric ACL-A/B ATP citrate lyase Source: (gene. exp.)  Methanosaeta concilii (archaea) / Plasmid: pET11a / Details (production host): Bicistronic construct / Production host: Methanosaeta concilii (archaea) / Plasmid: pET11a / Details (production host): Bicistronic construct / Production host:  #2: Protein | Mass: 69192.578 Da / Num. of mol.: 2 Source method: isolated from a genetically manipulated source Details: ACL-B subunit of the heteromeric ACL-A/B ATP citrate lyase Source: (gene. exp.)  Methanosaeta concilii (archaea) / Plasmid: pET11a / Details (production host): Bicistronic construct / Production host: Methanosaeta concilii (archaea) / Plasmid: pET11a / Details (production host): Bicistronic construct / Production host:  References: UniProt: A0A1V4VDZ9, succinate-CoA ligase (ADP-forming) |
|---|
-Non-polymers , 8 types, 737 molecules 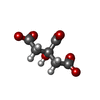

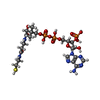



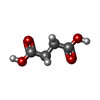








| #3: Chemical | | #4: Chemical | #5: Chemical | #6: Chemical | #7: Chemical | ChemComp-PG4 / | #8: Chemical | #9: Chemical | ChemComp-SIN / | #10: Water | ChemComp-HOH / | |
|---|
-Details
| Has protein modification | Y |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.54 Å3/Da / Density % sol: 51.61 % |
|---|---|
| Crystal grow | Temperature: 293 K / Method: vapor diffusion, sitting drop / pH: 8 Details: 14% PEG3350 4% tacsimate pH 8.0 Protein sample buffer: 20 mM citrate pH 6.0, 150 mM NaCl 10 mM CoASH |
-Data collection
| Diffraction | Mean temperature: 100 K / Serial crystal experiment: N |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  SLS SLS  / Beamline: X06DA / Wavelength: 1.00003 Å / Beamline: X06DA / Wavelength: 1.00003 Å |
| Detector | Type: DECTRIS PILATUS3 2M / Detector: PIXEL / Date: Oct 25, 2017 |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 1.00003 Å / Relative weight: 1 |
| Reflection | Resolution: 2.1→39.1 Å / Num. obs: 138565 / % possible obs: 99.4 % / Redundancy: 6.1 % / Biso Wilson estimate: 38.49 Å2 / CC1/2: 0.999 / Rrim(I) all: 0.112 / Net I/σ(I): 13.07 |
| Reflection shell | Resolution: 2.1→2.23 Å / Redundancy: 5.1 % / Mean I/σ(I) obs: 1.09 / Num. unique obs: 21584 / CC1/2: 0.387 / Rrim(I) all: 0.1415 / % possible all: 97.1 |
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: ACL structure from C. limicola Resolution: 2.1→30.75 Å / Cor.coef. Fo:Fc: 0.951 / Cor.coef. Fo:Fc free: 0.941 / SU R Cruickshank DPI: 0.182 / Cross valid method: THROUGHOUT / σ(F): 0 / SU R Blow DPI: 0.183 / SU Rfree Blow DPI: 0.151 / SU Rfree Cruickshank DPI: 0.152
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso mean: 63.6 Å2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze | Luzzati coordinate error obs: 0.29 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: 1 / Resolution: 2.1→30.75 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Resolution: 2.1→2.15 Å / Rfactor Rfree error: 0 / Total num. of bins used: 20
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller










 PDBj
PDBj
















