+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6h4z | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Crystal structure of human KDM5B in complex with compound 16a | ||||||
 要素 要素 | Lysine-specific demethylase 5B,Lysine-specific demethylase 5B | ||||||
 キーワード キーワード | OXIDOREDUCTASE / Histone demethylase / Inhibitor / transcription | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報regulation of estradiol secretion / mammary duct terminal end bud growth / uterus morphogenesis / TFAP2 (AP-2) family regulates transcription of cell cycle factors / positive regulation of mammary gland epithelial cell proliferation / [histone H3]-trimethyl-L-lysine4 demethylase / histone H3K4me/H3K4me2/H3K4me3 demethylase activity / lens fiber cell differentiation / histone H3K4 demethylase activity / branching involved in mammary gland duct morphogenesis ...regulation of estradiol secretion / mammary duct terminal end bud growth / uterus morphogenesis / TFAP2 (AP-2) family regulates transcription of cell cycle factors / positive regulation of mammary gland epithelial cell proliferation / [histone H3]-trimethyl-L-lysine4 demethylase / histone H3K4me/H3K4me2/H3K4me3 demethylase activity / lens fiber cell differentiation / histone H3K4 demethylase activity / branching involved in mammary gland duct morphogenesis / histone demethylase activity / single fertilization / response to fungicide / cellular response to fibroblast growth factor stimulus / cellular response to leukemia inhibitory factor / Chromatin modifications during the maternal to zygotic transition (MZT) / post-embryonic development / HDMs demethylate histones / sequence-specific double-stranded DNA binding / rhythmic process / transcription corepressor activity / histone binding / nucleic acid binding / chromatin remodeling / negative regulation of DNA-templated transcription / positive regulation of gene expression / regulation of DNA-templated transcription / chromatin / DNA binding / zinc ion binding / nucleoplasm / nucleus / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.3 Å 分子置換 / 解像度: 2.3 Å | ||||||
 データ登録者 データ登録者 | Le Bihan, Y.V. / Velupillai, S. / van Montfort, R.L.M. | ||||||
| 資金援助 |  英国, 1件 英国, 1件
| ||||||
 引用 引用 |  ジャーナル: Eur.J.Med.Chem. / 年: 2019 ジャーナル: Eur.J.Med.Chem. / 年: 2019タイトル: C8-substituted pyrido[3,4-d]pyrimidin-4(3H)-ones: Studies towards the identification of potent, cell penetrant Jumonji C domain containing histone lysine demethylase 4 subfamily (KDM4) ...タイトル: C8-substituted pyrido[3,4-d]pyrimidin-4(3H)-ones: Studies towards the identification of potent, cell penetrant Jumonji C domain containing histone lysine demethylase 4 subfamily (KDM4) inhibitors, compound profiling in cell-based target engagement assays. 著者: Le Bihan, Y.V. / Lanigan, R.M. / Atrash, B. / McLaughlin, M.G. / Velupillai, S. / Malcolm, A.G. / England, K.S. / Ruda, G.F. / Mok, N.Y. / Tumber, A. / Tomlin, K. / Saville, H. / Shehu, E. / ...著者: Le Bihan, Y.V. / Lanigan, R.M. / Atrash, B. / McLaughlin, M.G. / Velupillai, S. / Malcolm, A.G. / England, K.S. / Ruda, G.F. / Mok, N.Y. / Tumber, A. / Tomlin, K. / Saville, H. / Shehu, E. / McAndrew, C. / Carmichael, L. / Bennett, J.M. / Jeganathan, F. / Eve, P. / Donovan, A. / Hayes, A. / Wood, F. / Raynaud, F.I. / Fedorov, O. / Brennan, P.E. / Burke, R. / van Montfort, R.L.M. / Rossanese, O.W. / Blagg, J. / Bavetsias, V. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6h4z.cif.gz 6h4z.cif.gz | 216.1 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6h4z.ent.gz pdb6h4z.ent.gz | 171.1 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6h4z.json.gz 6h4z.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  6h4z_validation.pdf.gz 6h4z_validation.pdf.gz | 870.4 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  6h4z_full_validation.pdf.gz 6h4z_full_validation.pdf.gz | 871.6 KB | 表示 | |
| XML形式データ |  6h4z_validation.xml.gz 6h4z_validation.xml.gz | 21.6 KB | 表示 | |
| CIF形式データ |  6h4z_validation.cif.gz 6h4z_validation.cif.gz | 32.3 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/h4/6h4z https://data.pdbj.org/pub/pdb/validation_reports/h4/6h4z ftp://data.pdbj.org/pub/pdb/validation_reports/h4/6h4z ftp://data.pdbj.org/pub/pdb/validation_reports/h4/6h4z | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6h4oC  6h4pC  6h4qC  6h4rC  6h4sC  6h4tC  6h4uC  6h4vC  6h4wC  6h4xC  6h4yC  6h50C  6h51C  6h52C  5a1fS S: 精密化の開始モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
| ||||||||
| Components on special symmetry positions |
|
- 要素
要素
-タンパク質 , 1種, 1分子 A
| #1: タンパク質 | 分子量: 55457.578 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: KDM5B, JARID1B, PLU1, RBBP2H1 / 細胞株 (発現宿主): SF9 Homo sapiens (ヒト) / 遺伝子: KDM5B, JARID1B, PLU1, RBBP2H1 / 細胞株 (発現宿主): SF9発現宿主:  参照: UniProt: Q9UGL1, 酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; 2- ...参照: UniProt: Q9UGL1, 酸化還元酵素; 電子対供与作用を持つ; 分子酸素を取り込むないしは分子酸素を還元する; 2-オキソグルタル酸類を片方の電子供与体とする; 酸素分をそれぞれの電子供与体に取り込む |
|---|
-非ポリマー , 6種, 326分子 

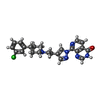








| #2: 化合物 | | #3: 化合物 | #4: 化合物 | #5: 化合物 | ChemComp-DMS / #6: 化合物 | ChemComp-EDO / #7: 水 | ChemComp-HOH / | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 4.19 Å3/Da / 溶媒含有率: 70.66 % |
|---|---|
| 結晶化 | 温度: 277 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 7.5 詳細: 100 nL of protein is mixed with 200 nL of crystallisation solution containing 1.6 M Na/K phosphate, 0.1 M HEPES pH 7.5, and with 20 nL of seeds obtained in the same conditions. Inhibitor is ...詳細: 100 nL of protein is mixed with 200 nL of crystallisation solution containing 1.6 M Na/K phosphate, 0.1 M HEPES pH 7.5, and with 20 nL of seeds obtained in the same conditions. Inhibitor is soaked in crystals by addition directly to the drops of DMSO dissolved compound |
-データ収集
| 回折 | 平均測定温度: 100 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  Diamond Diamond  / ビームライン: I04-1 / 波長: 0.9282 Å / ビームライン: I04-1 / 波長: 0.9282 Å |
| 検出器 | タイプ: DECTRIS PILATUS 6M-F / 検出器: PIXEL / 日付: 2015年11月27日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 0.9282 Å / 相対比: 1 |
| 反射 | 解像度: 2.3→77.18 Å / Num. obs: 42633 / % possible obs: 99.7 % / 冗長度: 19.6 % / Biso Wilson estimate: 56.64 Å2 / CC1/2: 0.999 / Rmerge(I) obs: 0.113 / Net I/σ(I): 21 |
| 反射 シェル | 解像度: 2.3→2.36 Å / 冗長度: 19.6 % / Rmerge(I) obs: 1.738 / Mean I/σ(I) obs: 1.8 / Num. unique obs: 2975 / CC1/2: 0.656 / % possible all: 96.5 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: 5a1f 解像度: 2.3→65.69 Å / Cor.coef. Fo:Fc: 0.949 / Cor.coef. Fo:Fc free: 0.936 / SU R Cruickshank DPI: 0.169 / 交差検証法: THROUGHOUT / σ(F): 0 / SU R Blow DPI: 0.181 / SU Rfree Blow DPI: 0.155 / SU Rfree Cruickshank DPI: 0.15
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 60.51 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze | Luzzati coordinate error obs: 0.28 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: 1 / 解像度: 2.3→65.69 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 2.3→2.36 Å / Total num. of bins used: 20
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLS | 手法: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLSグループ |
|
 ムービー
ムービー コントローラー
コントローラー




















 PDBj
PDBj






