| 登録情報 | データベース: PDB / ID: 5wle
|
|---|
| タイトル | Crystal structure of the PPS PHD finger in complex with H3K4me3 |
|---|
 要素 要素 | - H3K4me3 Peptide
- Protein partner of snf, isoform A
|
|---|
 キーワード キーワード | HYDROLASE / Epigenetic / PHD / Histone / trimethylated |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
加水分解酵素; 酸無水物に作用 / small nuclear ribonucleoprotein complex / regulation of alternative mRNA splicing, via spliceosome / Chromatin modifying enzymes / epigenetic regulation of gene expression / telomere organization / RNA Polymerase I Promoter Opening / Interleukin-7 signaling / Assembly of the ORC complex at the origin of replication / DNA methylation ...加水分解酵素; 酸無水物に作用 / small nuclear ribonucleoprotein complex / regulation of alternative mRNA splicing, via spliceosome / Chromatin modifying enzymes / epigenetic regulation of gene expression / telomere organization / RNA Polymerase I Promoter Opening / Interleukin-7 signaling / Assembly of the ORC complex at the origin of replication / DNA methylation / helicase activity / Condensation of Prophase Chromosomes / ERCC6 (CSB) and EHMT2 (G9a) positively regulate rRNA expression / SIRT1 negatively regulates rRNA expression / Chromatin modifications during the maternal to zygotic transition (MZT) / HCMV Late Events / PRC2 methylates histones and DNA / Defective pyroptosis / HDACs deacetylate histones / RNA Polymerase I Promoter Escape / Transcriptional regulation by small RNAs / Formation of the beta-catenin:TCF transactivating complex / RUNX1 regulates genes involved in megakaryocyte differentiation and platelet function / NoRC negatively regulates rRNA expression / Activated PKN1 stimulates transcription of AR (androgen receptor) regulated genes KLK2 and KLK3 / B-WICH complex positively regulates rRNA expression / HDMs demethylate histones / PKMTs methylate histone lysines / Meiotic recombination / RMTs methylate histone arginines / Pre-NOTCH Transcription and Translation / Activation of anterior HOX genes in hindbrain development during early embryogenesis / HCMV Early Events / Transcriptional regulation of granulopoiesis / structural constituent of chromatin / nucleosome / nucleosome assembly / chromatin organization / RUNX1 regulates transcription of genes involved in differentiation of HSCs / Factors involved in megakaryocyte development and platelet production / HATs acetylate histones / gene expression / Senescence-Associated Secretory Phenotype (SASP) / Oxidative Stress Induced Senescence / Estrogen-dependent gene expression / hydrolase activity / cadherin binding / protein heterodimerization activity / Amyloid fiber formation / DNA-templated transcription / protein-containing complex / DNA binding / extracellular exosome / extracellular region / nucleoplasm / membrane / nucleus / metal ion binding類似検索 - 分子機能 Spen paralogue and orthologue SPOC, C-terminal / SPOC domain / BRK domain / BRK domain / BRK domain superfamily / domain in transcription and CHROMO domain helicases / Transcription factor S-II (TFIIS), central domain / Domain in the central regions of transcription elongation factor S-II (and elsewhere) / Transcription elongation factor S-II, central domain / Transcription elongation factor S-II, central domain superfamily ...Spen paralogue and orthologue SPOC, C-terminal / SPOC domain / BRK domain / BRK domain / BRK domain superfamily / domain in transcription and CHROMO domain helicases / Transcription factor S-II (TFIIS), central domain / Domain in the central regions of transcription elongation factor S-II (and elsewhere) / Transcription elongation factor S-II, central domain / Transcription elongation factor S-II, central domain superfamily / TFIIS central domain profile. / Zinc/RING finger domain, C3HC4 (zinc finger) / Herpes Virus-1 / Zinc finger, PHD-type, conserved site / PHD-finger / Zinc finger PHD-type signature. / Zinc finger PHD-type profile. / Zinc finger, PHD-finger / Histone H3 signature 1. / Zinc finger, PHD-type / PHD zinc finger / Histone H3 signature 2. / Histone H3 / Histone H3/CENP-A / Histone H2A/H2B/H3 / Core histone H2A/H2B/H3/H4 / Zinc finger, FYVE/PHD-type / Histone-fold / Zinc finger, RING/FYVE/PHD-type / 2-Layer Sandwich / Alpha Beta類似検索 - ドメイン・相同性 Histone H3.1 / Protein partner of snf, isoform A類似検索 - 構成要素 |
|---|
| 生物種 |   Drosophila melanogaster (キイロショウジョウバエ) Drosophila melanogaster (キイロショウジョウバエ)
 Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  分子置換 / 解像度: 1.952 Å 分子置換 / 解像度: 1.952 Å |
|---|
 データ登録者 データ登録者 | Klein, B.J. / Kutateladze, T.G. |
|---|
| 資金援助 |  米国, 4件 米国, 4件 | 組織 | 認可番号 | 国 |
|---|
| National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS) | GM106416 |  米国 米国 | | National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS) | GM101664 |  米国 米国 | | National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS) | GM100907 |  米国 米国 | | National Institutes of Health/National Institute on Alcohol Abuse and Alcoholism (NIH/NIAAA) | T32AA007464 |  米国 米国 |
|
|---|
 引用 引用 |  ジャーナル: Structure / 年: 2017 ジャーナル: Structure / 年: 2017
タイトル: A Unique pH-Dependent Recognition of Methylated Histone H3K4 by PPS and DIDO.
著者: Tencer, A.H. / Gatchalian, J. / Klein, B.J. / Khan, A. / Zhang, Y. / Strahl, B.D. / van Wely, K.H.M. / Kutateladze, T.G. |
|---|
| 履歴 | | 登録 | 2017年7月26日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2017年10月4日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2017年10月18日 | Group: Database references / カテゴリ: citation
Item: _citation.journal_volume / _citation.page_first / _citation.page_last |
|---|
| 改定 1.2 | 2019年12月11日 | Group: Author supporting evidence / カテゴリ: pdbx_audit_support / Item: _pdbx_audit_support.funding_organization |
|---|
| 改定 1.3 | 2023年10月4日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / struct_conn / struct_conn_type
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _struct_conn.conn_type_id / _struct_conn.id / _struct_conn.pdbx_dist_value / _struct_conn.pdbx_leaving_atom_flag / _struct_conn.ptnr1_auth_asym_id / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_asym_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_conn_type.id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  分子置換 / 解像度: 1.952 Å
分子置換 / 解像度: 1.952 Å  データ登録者
データ登録者 米国, 4件
米国, 4件  引用
引用 ジャーナル: Structure / 年: 2017
ジャーナル: Structure / 年: 2017 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5wle.cif.gz
5wle.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5wle.ent.gz
pdb5wle.ent.gz PDB形式
PDB形式 5wle.json.gz
5wle.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 5wle_validation.pdf.gz
5wle_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 5wle_full_validation.pdf.gz
5wle_full_validation.pdf.gz 5wle_validation.xml.gz
5wle_validation.xml.gz 5wle_validation.cif.gz
5wle_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/wl/5wle
https://data.pdbj.org/pub/pdb/validation_reports/wl/5wle ftp://data.pdbj.org/pub/pdb/validation_reports/wl/5wle
ftp://data.pdbj.org/pub/pdb/validation_reports/wl/5wle リンク
リンク 集合体
集合体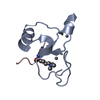
 要素
要素

 Homo sapiens (ヒト) / 参照: UniProt: P68431*PLUS
Homo sapiens (ヒト) / 参照: UniProt: P68431*PLUS X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 回転陽極 / タイプ: RIGAKU MICROMAX-007 / 波長: 1.54 Å
回転陽極 / タイプ: RIGAKU MICROMAX-007 / 波長: 1.54 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー



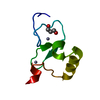




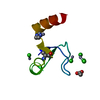
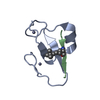




 PDBj
PDBj










