Entry Database : PDB / ID : 5k28Title Structure of the unbound SH3 domain of MLK3 Mitogen-activated protein kinase kinase kinase 11 Keywords / / / / Function / homology Function Domain/homology Component
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / Biological species Homo sapiens (human)Method / / / Resolution : 1.5 Å Authors Kall, S.K. / Lavie, A. Journal : J. Biol. Chem. / Year : 2018Title : Identification of two distinct peptide-binding pockets in the SH3 domain of human mixed-lineage kinase 3.Authors : Kokoszka, M.E. / Kall, S.L. / Khosla, S. / McGinnis, J.E. / Lavie, A. / Kay, B.K. History Deposition May 18, 2016 Deposition site / Processing site Revision 1.0 Dec 13, 2017 Provider / Type Revision 1.1 Dec 26, 2018 Group / Database references / Category / citation_authorItem _citation.country / _citation.journal_abbrev ... _citation.country / _citation.journal_abbrev / _citation.journal_id_ASTM / _citation.journal_id_CSD / _citation.journal_id_ISSN / _citation.journal_volume / _citation.page_first / _citation.page_last / _citation.pdbx_database_id_DOI / _citation.pdbx_database_id_PubMed / _citation.title / _citation.year Revision 1.2 Sep 27, 2023 Group / Database references / Refinement descriptionCategory chem_comp_atom / chem_comp_bond ... chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / struct_ncs_dom_lim Item _database_2.pdbx_DOI / _database_2.pdbx_database_accession ... _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _struct_ncs_dom_lim.beg_auth_comp_id / _struct_ncs_dom_lim.beg_label_asym_id / _struct_ncs_dom_lim.beg_label_comp_id / _struct_ncs_dom_lim.beg_label_seq_id / _struct_ncs_dom_lim.end_auth_comp_id / _struct_ncs_dom_lim.end_label_asym_id / _struct_ncs_dom_lim.end_label_comp_id / _struct_ncs_dom_lim.end_label_seq_id
Show all Show less
 Open data
Open data Basic information
Basic information Components
Components Keywords
Keywords Function and homology information
Function and homology information Homo sapiens (human)
Homo sapiens (human) X-RAY DIFFRACTION /
X-RAY DIFFRACTION /  SYNCHROTRON /
SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 1.5 Å
MOLECULAR REPLACEMENT / Resolution: 1.5 Å  Authors
Authors Citation
Citation Journal: J. Biol. Chem. / Year: 2018
Journal: J. Biol. Chem. / Year: 2018 Structure visualization
Structure visualization Molmil
Molmil Jmol/JSmol
Jmol/JSmol Downloads & links
Downloads & links Download
Download 5k28.cif.gz
5k28.cif.gz PDBx/mmCIF format
PDBx/mmCIF format pdb5k28.ent.gz
pdb5k28.ent.gz PDB format
PDB format 5k28.json.gz
5k28.json.gz PDBx/mmJSON format
PDBx/mmJSON format Other downloads
Other downloads https://data.pdbj.org/pub/pdb/validation_reports/k2/5k28
https://data.pdbj.org/pub/pdb/validation_reports/k2/5k28 ftp://data.pdbj.org/pub/pdb/validation_reports/k2/5k28
ftp://data.pdbj.org/pub/pdb/validation_reports/k2/5k28
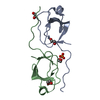
 Links
Links Assembly
Assembly


 Components
Components Homo sapiens (human) / Gene: MAP3K11, MLK3, PTK1, SPRK / Production host:
Homo sapiens (human) / Gene: MAP3K11, MLK3, PTK1, SPRK / Production host: 
 X-RAY DIFFRACTION / Number of used crystals: 1
X-RAY DIFFRACTION / Number of used crystals: 1  Sample preparation
Sample preparation SYNCHROTRON / Site:
SYNCHROTRON / Site:  APS
APS  / Beamline: 21-ID-F / Wavelength: 0.97872 Å
/ Beamline: 21-ID-F / Wavelength: 0.97872 Å Processing
Processing MOLECULAR REPLACEMENT
MOLECULAR REPLACEMENT Movie
Movie Controller
Controller







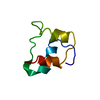





 PDBj
PDBj

