+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-3364 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Sub-tomogram averaging of Tula virus glycoprotein spike | |||||||||
 マップデータ マップデータ | Sub-tomogram average of Tula virus surface | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Tula virus / membrane protein / glycoprotein / hantavirus / bunyavirus / receptor binding | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報symbiont-mediated suppression of host TRAF-mediated signal transduction / host cell Golgi membrane / host cell mitochondrion / host cell surface / host cell endoplasmic reticulum membrane / symbiont-mediated suppression of host innate immune response / fusion of virus membrane with host endosome membrane / symbiont entry into host cell / virion attachment to host cell / virion membrane ...symbiont-mediated suppression of host TRAF-mediated signal transduction / host cell Golgi membrane / host cell mitochondrion / host cell surface / host cell endoplasmic reticulum membrane / symbiont-mediated suppression of host innate immune response / fusion of virus membrane with host endosome membrane / symbiont entry into host cell / virion attachment to host cell / virion membrane / signal transduction / zinc ion binding / membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Tula virus (ウイルス) Tula virus (ウイルス) | |||||||||
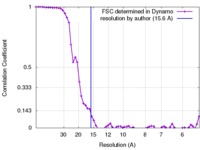
| 手法 | サブトモグラム平均法 / クライオ電子顕微鏡法 / 解像度: 15.6 Å | |||||||||
 データ登録者 データ登録者 | Li S / Rissanen I / Zeltina A / Hepojoki J / Raghwani J / Harlos K / Pybus OG / Huiskonen JT / Bowden TA | |||||||||
 引用 引用 |  ジャーナル: Cell Rep / 年: 2016 ジャーナル: Cell Rep / 年: 2016タイトル: A Molecular-Level Account of the Antigenic Hantaviral Surface. 著者: Sai Li / Ilona Rissanen / Antra Zeltina / Jussi Hepojoki / Jayna Raghwani / Karl Harlos / Oliver G Pybus / Juha T Huiskonen / Thomas A Bowden /   要旨: Hantaviruses, a geographically diverse group of zoonotic pathogens, initiate cell infection through the concerted action of Gn and Gc viral surface glycoproteins. Here, we describe the high- ...Hantaviruses, a geographically diverse group of zoonotic pathogens, initiate cell infection through the concerted action of Gn and Gc viral surface glycoproteins. Here, we describe the high-resolution crystal structure of the antigenic ectodomain of Gn from Puumala hantavirus (PUUV), a causative agent of hemorrhagic fever with renal syndrome. Fitting of PUUV Gn into an electron cryomicroscopy reconstruction of intact Gn-Gc spike complexes from the closely related but non-pathogenic Tula hantavirus localized Gn tetramers to the membrane-distal surface of the virion. The accuracy of the fitting was corroborated by epitope mapping and genetic analysis of available PUUV sequences. Interestingly, Gn exhibits greater non-synonymous sequence diversity than the less accessible Gc, supporting a role of the host humoral immune response in exerting selective pressure on the virus surface. The fold of PUUV Gn is likely to be widely conserved across hantaviruses. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_3364.map.gz emd_3364.map.gz | 14.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-3364-v30.xml emd-3364-v30.xml emd-3364.xml emd-3364.xml | 11.6 KB 11.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_3364_fsc.xml emd_3364_fsc.xml | 6.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_3364.tif emd_3364.tif | 6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-3364 http://ftp.pdbj.org/pub/emdb/structures/EMD-3364 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-3364 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-3364 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_3364_validation.pdf.gz emd_3364_validation.pdf.gz | 271 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_3364_full_validation.pdf.gz emd_3364_full_validation.pdf.gz | 270.2 KB | 表示 | |
| XML形式データ |  emd_3364_validation.xml.gz emd_3364_validation.xml.gz | 8.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3364 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3364 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3364 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3364 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_3364.map.gz / 形式: CCP4 / 大きさ: 15.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_3364.map.gz / 形式: CCP4 / 大きさ: 15.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sub-tomogram average of Tula virus surface | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.7 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Glycoprotein spike of Tula hantavirus
| 全体 | 名称: Glycoprotein spike of Tula hantavirus |
|---|---|
| 要素 |
|
-超分子 #1000: Glycoprotein spike of Tula hantavirus
| 超分子 | 名称: Glycoprotein spike of Tula hantavirus / タイプ: sample / ID: 1000 / 集合状態: Lattice of GnGc tetramers / Number unique components: 1 |
|---|
-超分子 #1: Tula virus
| 超分子 | 名称: Tula virus / タイプ: virus / ID: 1 / Name.synonym: Tula hantavirus / NCBI-ID: 37133 / 生物種: Tula virus / Sci species strain: Moravia / ウイルスタイプ: VIRION / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: Yes / ウイルス・中空状態: No / Syn species name: Tula hantavirus |
|---|---|
| 宿主 | 生物種:  Microtus (ネズミ) / 別称: VERTEBRATES Microtus (ネズミ) / 別称: VERTEBRATES |
| Host system | 生物種: Chlorocebus / 組換細胞: Vero E6 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | サブトモグラム平均法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 / 詳細: 25 mM Tris, 75 mM NaCl |
|---|---|
| グリッド | 詳細: Grids (Cflat CF-2/1-2C-T) were glow-discharged for 15 s. 10-nm gold particles were added. |
| 凍結 | 凍結剤: ETHANE-PROPANE MIXTURE / チャンバー内湿度: 80 % / チャンバー内温度: 120 K / 装置: GATAN CRYOPLUNGE 3 / 手法: Blot for 3 seconds before plunging. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI POLARA 300 |
|---|---|
| 温度 | 最低: 80 K / 最高: 120 K |
| アライメント法 | Legacy - 非点収差: Objective lens astigmatism was corrected at 160,000 times magnification. |
| 特殊光学系 | エネルギーフィルター - 名称: GIF QUANTUM LS エネルギーフィルター - エネルギー下限: 0.0 eV エネルギーフィルター - エネルギー上限: 20.0 eV |
| 詳細 | Super-resolution counting mode |
| 日付 | 2014年8月14日 |
| 撮影 | カテゴリ: CCD フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) デジタル化 - サンプリング間隔: 5 µm / 実像数: 30 / 平均電子線量: 60 e/Å2 詳細: Each image is a tilt series of 19 movies, acquired at 5 degree intervals. Each movie consists of 8 frames. |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 37037 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.0 mm / 最大 デフォーカス(公称値): 3.8 µm / 最小 デフォーカス(公称値): 2.0 µm / 倍率(公称値): 160000 |
| 試料ステージ | 試料ホルダー: Liquid nitrogen cooled / 試料ホルダーモデル: OTHER / Tilt series - Axis1 - Min angle: -45 ° / Tilt series - Axis1 - Max angle: 45 ° |
| 実験機器 |  モデル: Tecnai Polara / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - #0 - Chain ID: A / Chain - #1 - Chain ID: B |
|---|---|
| ソフトウェア | 名称: Chimera, Segger |
| 詳細 | Density was segmented in 6 segments and 1000 evenly rotated fits were considered for each segment. |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT / 当てはまり具合の基準: Cross-correlation |
| 得られたモデル |  PDB-5fyn: |
 ムービー
ムービー コントローラー
コントローラー











 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)