+ Open data
Open data
- Basic information
Basic information
| Entry |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | DNA-devoid HCIV-1 virus particle | |||||||||
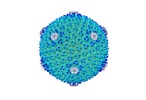
 Map data Map data | This map corresponds to DNA-devoid HCIV-1 particles. A cut through shows the lack of DNA and the unexpanded membrane vesicle. To better distinguish the membrane it is advisable to filter to 10 Ang. | |||||||||
 Sample Sample |
| |||||||||
| Biological species |  Haloarcula californiae ATCC 33799 (Halophile) Haloarcula californiae ATCC 33799 (Halophile) | |||||||||
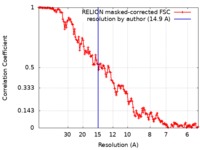
| Method | single particle reconstruction / cryo EM / Resolution: 14.9 Å | |||||||||
 Authors Authors | Santos-Perez I / Charro D / Gil-Carton D / Azkargorta M / Elortza F / Bamford DH / Oksanen HM / Abrescia NGA | |||||||||
 Citation Citation |  Journal: Nat Commun / Year: 2019 Journal: Nat Commun / Year: 2019Title: Structural basis for assembly of vertical single β-barrel viruses. Authors: Isaac Santos-Pérez / Diego Charro / David Gil-Carton / Mikel Azkargorta / Felix Elortza / Dennis H Bamford / Hanna M Oksanen / Nicola G A Abrescia /   Abstract: The vertical double β-barrel major capsid protein (MCP) fold, fingerprint of the PRD1-adeno viral lineage, is widespread in many viruses infecting organisms across the three domains of life. The ...The vertical double β-barrel major capsid protein (MCP) fold, fingerprint of the PRD1-adeno viral lineage, is widespread in many viruses infecting organisms across the three domains of life. The discovery of PRD1-like viruses with two MCPs challenged the known assembly principles. Here, we present the cryo-electron microscopy (cryo-EM) structures of the archaeal, halophilic, internal membrane-containing Haloarcula californiae icosahedral virus 1 (HCIV-1) and Haloarcula hispanica icosahedral virus 2 (HHIV-2) at 3.7 and 3.8 Å resolution, respectively. Our structures reveal proteins located beneath the morphologically distinct two- and three-tower capsomers and homopentameric membrane proteins at the vertices that orchestrate the positioning of pre-formed vertical single β-barrel MCP heterodimers. The cryo-EM based structures together with the proteomics data provide insights into the assembly mechanism of this type of viruses and into those with membrane-less double β-barrel MCPs. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | EM map:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|---|
| Supplemental images |
- Downloads & links
Downloads & links
-EMDB archive
| Map data |  emd_0050.map.gz emd_0050.map.gz | 201.6 MB |  EMDB map data format EMDB map data format | |
|---|---|---|---|---|
| Header (meta data) |  emd-0050-v30.xml emd-0050-v30.xml emd-0050.xml emd-0050.xml | 17.8 KB 17.8 KB | Display Display |  EMDB header EMDB header |
| FSC (resolution estimation) |  emd_0050_fsc.xml emd_0050_fsc.xml | 13.6 KB | Display |  FSC data file FSC data file |
| Images |  emd_0050.png emd_0050.png | 176.1 KB | ||
| Others |  emd_0050_half_map_1.map.gz emd_0050_half_map_1.map.gz emd_0050_half_map_2.map.gz emd_0050_half_map_2.map.gz | 170.7 MB 170.7 MB | ||
| Archive directory |  http://ftp.pdbj.org/pub/emdb/structures/EMD-0050 http://ftp.pdbj.org/pub/emdb/structures/EMD-0050 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0050 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0050 | HTTPS FTP |
-Related structure data
| Related structure data |  0072C  0073C  0131C  0172C  0174C  6h82C  6h9cC C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
| EMDB pages |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- Map
Map
| File |  Download / File: emd_0050.map.gz / Format: CCP4 / Size: 216 MB / Type: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) Download / File: emd_0050.map.gz / Format: CCP4 / Size: 216 MB / Type: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Annotation | This map corresponds to DNA-devoid HCIV-1 particles. A cut through shows the lack of DNA and the unexpanded membrane vesicle. To better distinguish the membrane it is advisable to filter to 10 Ang. | ||||||||||||||||||||||||||||||||||||
| Projections & slices | Image control
Images are generated by Spider. | ||||||||||||||||||||||||||||||||||||
| Voxel size | X=Y=Z: 2.8 Å | ||||||||||||||||||||||||||||||||||||
| Density |
| ||||||||||||||||||||||||||||||||||||
| Symmetry | Space group: 1 | ||||||||||||||||||||||||||||||||||||
| Details | EMDB XML:
|
-Supplemental data
-Half map: #2
| File | emd_0050_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Projections & Slices |
| ||||||||||||
| Density Histograms |
-Half map: #1
| File | emd_0050_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Projections & Slices |
| ||||||||||||
| Density Histograms |
- Sample components
Sample components
-Entire : Haloarcula californiae ATCC 33799
| Entire | Name:  Haloarcula californiae ATCC 33799 (Halophile) Haloarcula californiae ATCC 33799 (Halophile) |
|---|---|
| Components |
|
-Supramolecule #1: Haloarcula californiae ATCC 33799
| Supramolecule | Name: Haloarcula californiae ATCC 33799 / type: virus / ID: 1 / Parent: 0 / Details: Haloarcula californiae icosahedral virus - 1 / NCBI-ID: 662475 / Sci species name: Haloarcula californiae ATCC 33799 / Virus type: VIRION / Virus isolate: SPECIES / Virus enveloped: No / Virus empty: Yes |
|---|---|
| Host (natural) | Organism:  Haloarcula californiae ATCC 33799 (Halophile) Haloarcula californiae ATCC 33799 (Halophile) |
| Virus shell | Shell ID: 1 / Diameter: 800.0 Å / T number (triangulation number): 28 |
-Experimental details
-Structure determination
| Method | cryo EM |
|---|---|
 Processing Processing | single particle reconstruction |
| Aggregation state | particle |
- Sample preparation
Sample preparation
| Concentration | 1.2 mg/mL | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Buffer | pH: 7.2 Component:
| ||||||||||||||||||
| Grid | Model: Quantifoil R1.2/1.3 / Material: COPPER / Mesh: 200 / Support film - Material: CARBON / Support film - topology: HOLEY / Pretreatment - Type: PLASMA CLEANING | ||||||||||||||||||
| Vitrification | Cryogen name: ETHANE / Instrument: FEI VITROBOT MARK III |
- Electron microscopy
Electron microscopy
| Microscope | FEI TITAN KRIOS |
|---|---|
| Image recording | Film or detector model: FEI FALCON II (4k x 4k) / Detector mode: INTEGRATING / Digitization - Frames/image: 1-26 / Number grids imaged: 1 / Number real images: 3218 / Average electron dose: 36.0 e/Å2 |
| Electron beam | Acceleration voltage: 300 kV / Electron source:  FIELD EMISSION GUN FIELD EMISSION GUN |
| Electron optics | Illumination mode: FLOOD BEAM / Imaging mode: BRIGHT FIELD / Cs: 2.7 mm / Nominal defocus max: 3.9 µm / Nominal defocus min: 0.6 µm |
| Sample stage | Specimen holder model: FEI TITAN KRIOS AUTOGRID HOLDER / Cooling holder cryogen: NITROGEN |
| Experimental equipment |  Model: Titan Krios / Image courtesy: FEI Company |
 Movie
Movie Controller
Controller













 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)