-検索条件
-検索結果
検索 (著者・登録者: ge & x)の結果5,506件中、1から50件目までを表示しています

EMDB-50296: 
70S Escherichia coli ribosome with P-site initiatior tRNA.

PDB-9fbv: 
70S Escherichia coli ribosome with P-site initiatior tRNA.

EMDB-18723: 
Cryo-EM structure of the cross-exon pre-B complex (tri-snRNP region)

EMDB-18724: 
Cryo-EM structure of the cross-exon pre-B+5'ss complex (tri-snRNP region)

EMDB-18725: 
Cryo-EM structure of the cross-exon pre-B+5'ss+ATPgammaS complex(tri-snRNP region)

EMDB-18726: 
Cryo-EM structure of the cross-exon pre-B+5'ssLNG+ATPgammaS complex (tri-snRNP region)

EMDB-18727: 
Cryo-EM structure of the cross-exon pre-B+AMPPNP complex (tri-snRNP region)

EMDB-18202: 
Copper-transporting ATPase HMA4 in E1 state apo

EMDB-18203: 
Copper-transporting ATPase HMA4 in E1 state with Cu

EMDB-18204: 
Copper-transporting ATPase HMA4 in E2P state with AlF

EMDB-18205: 
Copper-transporting ATPase HMA4 in E2P state with BeF

PDB-8q73: 
Copper-transporting ATPase HMA4 in E1 state apo

PDB-8q74: 
Copper-transporting ATPase HMA4 in E1 state with Cu

PDB-8q75: 
Copper-transporting ATPase HMA4 in E2P state with AlF

PDB-8q76: 
Copper-transporting ATPase HMA4 in E2P state with BeF

EMDB-50229: 
Cryo-tomogram of FIB-milled vegetatively growing yeast cell with mitochondria

EMDB-50230: 
Cryo-tomogram of FIB-milled pre-meiotic yeast cell with mitochondria

EMDB-50231: 
Cryo-tomogram of FIB-milled meiotic yeast cell containing mitochondria with filaments
EMDB-50232: 
Cryo-tomogram of FIB-milled yeast spore with mitochondria

EMDB-50233: 
Cryo-tomogram of FIB-milled meiotic yeast cell containing mitochondria with filament arrays

EMDB-50234: 
Cryo-tomogram of purified meiotic yeast mitochondria with Ald4 filaments

EMDB-18438: 
mt-SSU assembly intermediate in GTPBP8 knock-out cells, state 1

EMDB-18439: 
mt-SSU assembly intermediate in GTPBP8 knock-out cells, state 2

EMDB-18440: 
mt-SSU assembly intermediate in GTPBP8 knock-out cells, state 3

EMDB-18443: 
mt-SSU assembly intermediate in GTPBP8 knock-out cells, state 4

EMDB-18460: 
mt-LSU assembly intermediate in GTPBP8 knock-out cells, state 1

EMDB-18461: 
mt-LSU assembly intermediate in GTPBP8 knock-out cells, state 2

EMDB-19548: 
cryoEM structure of Acs1 filament determined by FilamentID

EMDB-19549: 
cryoEM structure of the central Ald4 filament determined by FilamentID

EMDB-19550: 
cryoEM structure of purified Acs1 filament from meiotic yeast cells
EMDB-19551: 
cryo sub-tomogram average of Acs1 filament from spread meiotic yeast spheroplasts
EMDB-19552: 
cryo sub-tomogram average of Ald4 filaments from purified meiotic yeast mitochondria
EMDB-19553: 
cryo-tomogram of FIB-milled meiotic yeast cell containing filaments in mitochondria

EMDB-19554: 
cryo-tomogram of FIB-milled meiotic yeast cell containing filaments in the nucleus
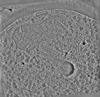
EMDB-19555: 
cryo-tomogram of FIB-milled meiotic yeast cell containing filaments in the cytoplasm
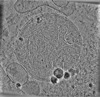
EMDB-19556: 
cryo-tomogram of purified meiotic yeast mitochondrion containing Ald4 filaments
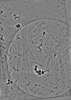
EMDB-19557: 
cryo-tomogram of spread meiotic yeast spheroplast containing Acs1 filaments

EMDB-19558: 
cryo-tomogram of spread starved yeast spheroplast containing filaments

PDB-8rwj: 
cryoEM structure of Acs1 filament determined by FilamentID

PDB-8rwk: 
cryoEM structure of the central Ald4 filament determined by FilamentID

EMDB-38966: 
Cryo-EM structure of human urate transporter GLUT9 bound to substrate urate

EMDB-38968: 
Cryo-EM structure of human urate transporter GLUT9 bound to inhibitor apigenin

PDB-8y65: 
Cryo-EM structure of human urate transporter GLUT9 bound to substrate urate

PDB-8y66: 
Cryo-EM structure of human urate transporter GLUT9 bound to inhibitor apigenin

EMDB-19395: 
CryoEM structure of recombinant human Bri2 BRICHOS oligomers

PDB-8rnu: 
CryoEM structure of recombinant human Bri2 BRICHOS oligomers

EMDB-44839: 
Intact V-ATPase State 2 and synaptophysin complex in mouse brain isolated synaptic vesicles

EMDB-44840: 
Intact V-ATPase State 3 and synaptophysin complex in mouse brain isolated synaptic vesicles

EMDB-44841: 
Intact V-ATPase State 3 in synaptophysin knock-out isolated synaptic vesicles

EMDB-44842: 
Intact V-ATPase State 2 in synaptophysin knock-out isolated synaptic vesicles
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
