+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-13438 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of Staphylococcus capitis divalent metal ion transporter (DMT) by NabFab-fiducial assisted cryo-EM | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | NabFab / Anti-nanobody Fab / Fiducial / DMT / MEMBRANE PROTEIN | |||||||||
| 機能・相同性 | NRAMP family / Natural resistance-associated macrophage protein-like / cadmium ion transmembrane transporter activity / manganese ion transmembrane transporter activity / iron ion transmembrane transport / symporter activity / metal ion binding / plasma membrane / Divalent metal cation transporter MntH 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 | synthetic construct (人工物) /  Staphylococcus capitis (バクテリア) / Staphylococcus capitis (バクテリア) /  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.78 Å | |||||||||
 データ登録者 データ登録者 | Bloch JS / Mukherjee S | |||||||||
| 資金援助 |  スイス, 1件 スイス, 1件
| |||||||||
 引用 引用 |  ジャーナル: Proc Natl Acad Sci U S A / 年: 2021 ジャーナル: Proc Natl Acad Sci U S A / 年: 2021タイトル: Development of a universal nanobody-binding Fab module for fiducial-assisted cryo-EM studies of membrane proteins. 著者: Joël S Bloch / Somnath Mukherjee / Julia Kowal / Ekaterina V Filippova / Martina Niederer / Els Pardon / Jan Steyaert / Anthony A Kossiakoff / Kaspar P Locher /    要旨: With conformation-specific nanobodies being used for a wide range of structural, biochemical, and cell biological applications, there is a demand for antigen-binding fragments (Fabs) that ...With conformation-specific nanobodies being used for a wide range of structural, biochemical, and cell biological applications, there is a demand for antigen-binding fragments (Fabs) that specifically and tightly bind these nanobodies without disturbing the nanobody-target protein interaction. Here, we describe the development of a synthetic Fab (termed NabFab) that binds the scaffold of an alpaca-derived nanobody with picomolar affinity. We demonstrate that upon complementary-determining region grafting onto this parent nanobody scaffold, nanobodies recognizing diverse target proteins and derived from llama or camel can cross-react with NabFab without loss of affinity. Using NabFab as a fiducial and size enhancer (50 kDa), we determined the high-resolution cryogenic electron microscopy (cryo-EM) structures of nanobody-bound VcNorM and ScaDMT, both small membrane proteins of ∼50 kDa. Using an additional anti-Fab nanobody further facilitated reliable initial three-dimensional structure determination from small cryo-EM test datasets. Given that NabFab is of synthetic origin, is humanized, and can be conveniently expressed in in large amounts, it may be useful not only for structural biology but also for biomedical applications. #1:  ジャーナル: Biorxiv / 年: 2021 ジャーナル: Biorxiv / 年: 2021タイトル: Development of a universal nanobody-binding Fab module for fiducial-assisted cryo-EM studies of membrane proteins 著者: Bloch JS / Mukherjee S / Kowal J / Filippova EV / Niederer M / Pardon E / Steyaert J / Kossiakoff AA / Locher KP | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_13438.map.gz emd_13438.map.gz | 323.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-13438-v30.xml emd-13438-v30.xml emd-13438.xml emd-13438.xml | 15.4 KB 15.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
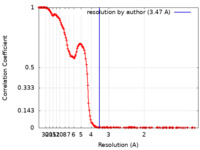
| FSC (解像度算出) |  emd_13438_fsc.xml emd_13438_fsc.xml | 20.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_13438.png emd_13438.png | 40.9 KB | ||
| Filedesc metadata |  emd-13438.cif.gz emd-13438.cif.gz | 6 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-13438 http://ftp.pdbj.org/pub/emdb/structures/EMD-13438 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13438 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13438 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_13438_validation.pdf.gz emd_13438_validation.pdf.gz | 463.6 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_13438_full_validation.pdf.gz emd_13438_full_validation.pdf.gz | 463.2 KB | 表示 | |
| XML形式データ |  emd_13438_validation.xml.gz emd_13438_validation.xml.gz | 15.1 KB | 表示 | |
| CIF形式データ |  emd_13438_validation.cif.gz emd_13438_validation.cif.gz | 20.5 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13438 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13438 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13438 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13438 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_13438.map.gz / 形式: CCP4 / 大きさ: 343 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_13438.map.gz / 形式: CCP4 / 大きさ: 343 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.66 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Complex of Staphylococcus capitis divalent metal ion transporter ...
| 全体 | 名称: Complex of Staphylococcus capitis divalent metal ion transporter (DMT), chimeric nanobody DMTNb16_4, NabFab, and anti-Fab nanobody |
|---|---|
| 要素 |
|
-超分子 #1: Complex of Staphylococcus capitis divalent metal ion transporter ...
| 超分子 | 名称: Complex of Staphylococcus capitis divalent metal ion transporter (DMT), chimeric nanobody DMTNb16_4, NabFab, and anti-Fab nanobody タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#5 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
-分子 #1: NabFab HC
| 分子 | 名称: NabFab HC / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 25.684463 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: EISEVQLVES GGGLVQPGGS LRLSCAASGF NFSYYSIHWV RQAPGKGLEW VAYISSSSSY TSYADSVKGR FTISADTSKN TAYLQMNSL RAEDTAVYYC ARGYQYWQYH ASWYWNGGLD YWGQGTLVTV SSASTKGPSV FPLAPSSKST SGGTAALGCL V KDYFPEPV ...文字列: EISEVQLVES GGGLVQPGGS LRLSCAASGF NFSYYSIHWV RQAPGKGLEW VAYISSSSSY TSYADSVKGR FTISADTSKN TAYLQMNSL RAEDTAVYYC ARGYQYWQYH ASWYWNGGLD YWGQGTLVTV SSASTKGPSV FPLAPSSKST SGGTAALGCL V KDYFPEPV TVSWNSGALT SGVHTFPAVL QSSGLYSLSS VVTVPSSSLG TQTYICNVNH KPSNTKVDKK VEPKSCDKTH T |
-分子 #2: NabFab LC
| 分子 | 名称: NabFab LC / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 23.258783 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: SDIQMTQSPS SLSASVGDRV TITCRASQSV SSAVAWYQQK PGKAPKLLIY SASSLYSGVP SRFSGSRSGT DFTLTISSLQ PEDFATYYC QQSSSSLITF GQGTKVEIKR TVAAPSVFIF PPSDSQLKSG TASVVCLLNN FYPREAKVQW KVDNALQSGN S QESVTEQD ...文字列: SDIQMTQSPS SLSASVGDRV TITCRASQSV SSAVAWYQQK PGKAPKLLIY SASSLYSGVP SRFSGSRSGT DFTLTISSLQ PEDFATYYC QQSSSSLITF GQGTKVEIKR TVAAPSVFIF PPSDSQLKSG TASVVCLLNN FYPREAKVQW KVDNALQSGN S QESVTEQD SKDSTYSLSS TLTLSKADYE KHKVYACEVT HQGLSSPVTK SFNRGEC |
-分子 #3: Divalent metal cation transporter MntH
| 分子 | 名称: Divalent metal cation transporter MntH / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Staphylococcus capitis (バクテリア) Staphylococcus capitis (バクテリア) |
| 分子量 | 理論値: 47.054531 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSVAVGYMDP GNWITSMQGG AQYGYTLLFV ILISSLAAML LQSMTVRLGI ATGKDLAQMT RHFLSKPVAI IFWIIAELAI IATDIAEVI GSAIALDLIF GIPLIVGALI TVFDVFLLLF IMRFGFRKIE AIVGTLIFTV LAIFVFEVFI SSPQLTDILN G FVPHKEIV ...文字列: MSVAVGYMDP GNWITSMQGG AQYGYTLLFV ILISSLAAML LQSMTVRLGI ATGKDLAQMT RHFLSKPVAI IFWIIAELAI IATDIAEVI GSAIALDLIF GIPLIVGALI TVFDVFLLLF IMRFGFRKIE AIVGTLIFTV LAIFVFEVFI SSPQLTDILN G FVPHKEIV TNQGILYIAL GIIGATIMPH NLYLHSSIVQ SRKYDRHDNQ EKAQAIKYAT IDSNLQLSIA FVVNCLLLTL GA ALFFGTK TNDLGGFYDL YHALKTEPVL GATLGGIMST LFAVALLASG QNSTITGTLA GQIVMEGFLR LSIPNWLRRL ITR ALAVIP VIICLIIFKG NSEKIEQLLV FSQVFLSIAL PFSLIPLQLA TSNKKLMGPF INKTWVNIIS WTLIVILSGL NVYL IIQTF QELALEVLFQ GPHHHHHHHH HH UniProtKB: Divalent metal cation transporter MntH |
-分子 #4: DMTNb16_4
| 分子 | 名称: DMTNb16_4 / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 14.423888 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: QRQLVESGGG LVQPGGSLRL SCAASRSIFS IDTAGWFRQA PGKEREGVAT ITRDGNANYA DSVKGRFTIS RDRARNTVYL QMNSLEPED TAVYYCNAAI RTTVRTSAQE YWGKGTPVTV SSHHHHHHEP EA |
-分子 #5: Anti-Fab nanobody
| 分子 | 名称: Anti-Fab nanobody / タイプ: protein_or_peptide / ID: 5 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 13.390644 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: GSQVQLQESG GGLVQPGGSL RLSCAASGRT ISRYAMSWFR QAPGKEREFV AVARRSGDGA FYADSVQGRF TVSRDDAKNT VYLQMNSLK PEDTAVYYCA IDSDTFYSGS YDYWGQGTQV TVSS |
-分子 #6: water
| 分子 | 名称: water / タイプ: ligand / ID: 6 / コピー数: 16 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE-PROPANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 26.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー



















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)