[English] 日本語
 Yorodumi
Yorodumi- PDB-7nn7: Crystal structure of Mycobacterium tuberculosis ArgB in complex w... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 7nn7 | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal structure of Mycobacterium tuberculosis ArgB in complex with dimethyl 5-hydroxyisophthalate. | ||||||
 Components Components | Acetylglutamate kinase | ||||||
 Keywords Keywords | TRANSFERASE / ArgB Acetylglutamate kinase | ||||||
| Function / homology |  Function and homology information Function and homology informationacetylglutamate kinase / acetylglutamate kinase activity / L-arginine biosynthetic process via ornithine / L-arginine biosynthetic process / peptidoglycan-based cell wall / ATP binding / plasma membrane / cytoplasm Similarity search - Function | ||||||
| Biological species |  Mycobacterium tuberculosis H37Rv (bacteria) Mycobacterium tuberculosis H37Rv (bacteria) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / MOLECULAR REPLACEMENT /  molecular replacement / Resolution: 2.172 Å molecular replacement / Resolution: 2.172 Å | ||||||
 Authors Authors | Mendes, V. / Thomas, S.E. / Cory-Wright, J. / Blundell, T.L. | ||||||
| Funding support |  United States, 1items United States, 1items
| ||||||
 Citation Citation |  Journal: Comput Struct Biotechnol J / Year: 2021 Journal: Comput Struct Biotechnol J / Year: 2021Title: A fragment-based approach to assess the ligandability of ArgB, ArgC, ArgD and ArgF in the L-arginine biosynthetic pathway of Mycobacterium tuberculosis Authors: Gupta, P. / Thomas, S.E. / Zaidan, S.A. / Pasillas, M.A. / Cory-Wright, J. / Sebastian-Perez, V. / Burgess, A. / Cattermole, E. / Meghir, C. / Abell, C. / Coyne, A.G. / Jacobs, W.R. / ...Authors: Gupta, P. / Thomas, S.E. / Zaidan, S.A. / Pasillas, M.A. / Cory-Wright, J. / Sebastian-Perez, V. / Burgess, A. / Cattermole, E. / Meghir, C. / Abell, C. / Coyne, A.G. / Jacobs, W.R. / Blundell, T.L. / Tiwari, S. / Mendes, V. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  7nn7.cif.gz 7nn7.cif.gz | 125.3 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb7nn7.ent.gz pdb7nn7.ent.gz | 97.2 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  7nn7.json.gz 7nn7.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Summary document |  7nn7_validation.pdf.gz 7nn7_validation.pdf.gz | 535 KB | Display |  wwPDB validaton report wwPDB validaton report |
|---|---|---|---|---|
| Full document |  7nn7_full_validation.pdf.gz 7nn7_full_validation.pdf.gz | 536.9 KB | Display | |
| Data in XML |  7nn7_validation.xml.gz 7nn7_validation.xml.gz | 12.6 KB | Display | |
| Data in CIF |  7nn7_validation.cif.gz 7nn7_validation.cif.gz | 16.7 KB | Display | |
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/nn/7nn7 https://data.pdbj.org/pub/pdb/validation_reports/nn/7nn7 ftp://data.pdbj.org/pub/pdb/validation_reports/nn/7nn7 ftp://data.pdbj.org/pub/pdb/validation_reports/nn/7nn7 | HTTPS FTP |
-Related structure data
| Related structure data |  7nlfC  7nlnC  7nloC  7nlpC  7nlqC  7nlrC  7nlsC  7nltC  7nluC  7nlwC  7nlxC  7nlyC  7nlzC  7nm0C  7nn1C  7nn4C  7nn8C  7nnbC  7nncC  7nnfC  7nniC  7nnqC  7nnrC  7nnvC  7nnwC  7nnyC  7nnzC  7norC  7nosC  7notC  7nouC  7novC  7np0C  7nphC  7npjC  2ap9S S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 | x 6
| |||||||||
| Unit cell |
| |||||||||
| Components on special symmetry positions |
|
- Components
Components
| #1: Protein | Mass: 31212.961 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Mycobacterium tuberculosis H37Rv (bacteria) Mycobacterium tuberculosis H37Rv (bacteria)Gene: argB, Rv1654, MTCY06H11.19 / Production host:  | ||||
|---|---|---|---|---|---|
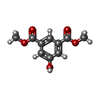
| #2: Chemical | ChemComp-98W / | ||||
| #3: Chemical | ChemComp-EDO / | ||||
| #4: Chemical | | #5: Water | ChemComp-HOH / | Has ligand of interest | Y | |
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 3.37 Å3/Da / Density % sol: 63.49 % |
|---|---|
| Crystal grow | Temperature: 291 K / Method: vapor diffusion / pH: 9.5 Details: 1260 mM ammonium sulphate 100 mM CHES pH 9.5 200 mM NaCl |
-Data collection
| Diffraction | Mean temperature: 100 K / Serial crystal experiment: N | ||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  Diamond Diamond  / Beamline: I03 / Wavelength: 0.9762 Å / Beamline: I03 / Wavelength: 0.9762 Å | ||||||||||||||||||||||||||||||
| Detector | Type: DECTRIS PILATUS 6M / Detector: PIXEL / Date: Feb 19, 2017 | ||||||||||||||||||||||||||||||
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | ||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength: 0.9762 Å / Relative weight: 1 | ||||||||||||||||||||||||||||||
| Reflection | Resolution: 2.17→65.02 Å / Num. obs: 21728 / % possible obs: 98.3 % / Redundancy: 8.9 % / Biso Wilson estimate: 59.54 Å2 / CC1/2: 0.999 / Rmerge(I) obs: 0.056 / Rpim(I) all: 0.02 / Rrim(I) all: 0.059 / Net I/σ(I): 19.1 / Num. measured all: 193857 | ||||||||||||||||||||||||||||||
| Reflection shell | Diffraction-ID: 1
|
-Phasing
| Phasing | Method:  molecular replacement molecular replacement | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Phasing MR |
|
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 2AP9 Resolution: 2.172→44.707 Å / SU ML: 0.27 / Cross valid method: THROUGHOUT / σ(F): 1.36 / Phase error: 27.65 / Stereochemistry target values: ML
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 151.35 Å2 / Biso mean: 76.1188 Å2 / Biso min: 45.4 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: final / Resolution: 2.172→44.707 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Rfactor Rfree error: 0
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller












 PDBj
PDBj