+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6wgt | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Crystal structure of HTR2A with hallucinogenic agonist | |||||||||
 要素 要素 | 5-hydroxytryptamine receptor 2A,Soluble cytochrome b562 fusion | |||||||||
 キーワード キーワード | MEMBRANE PROTEIN / HTR2A | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報protein localization to cytoskeleton / positive regulation of heat generation / 1-(4-iodo-2,5-dimethoxyphenyl)propan-2-amine binding / Gq/11-coupled serotonin receptor activity / positive regulation of phosphatidylinositol biosynthetic process / G protein-coupled serotonin receptor signaling pathway / G protein-coupled serotonin receptor complex / neurofilament / cell body fiber / Serotonin receptors ...protein localization to cytoskeleton / positive regulation of heat generation / 1-(4-iodo-2,5-dimethoxyphenyl)propan-2-amine binding / Gq/11-coupled serotonin receptor activity / positive regulation of phosphatidylinositol biosynthetic process / G protein-coupled serotonin receptor signaling pathway / G protein-coupled serotonin receptor complex / neurofilament / cell body fiber / Serotonin receptors / serotonin receptor activity / phospholipase C-activating serotonin receptor signaling pathway / artery smooth muscle contraction / G protein-coupled serotonin receptor activity / positive regulation of cytokine production involved in immune response / serotonin receptor signaling pathway / sensitization / neurotransmitter receptor activity / urinary bladder smooth muscle contraction / serotonin binding / positive regulation of platelet aggregation / negative regulation of synaptic transmission, glutamatergic / positive regulation of DNA biosynthetic process / temperature homeostasis / positive regulation of vasoconstriction / regulation of dopamine secretion / detection of temperature stimulus involved in sensory perception of pain / negative regulation of potassium ion transport / protein tyrosine kinase activator activity / G protein-coupled receptor signaling pathway, coupled to cyclic nucleotide second messenger / positive regulation of execution phase of apoptosis / positive regulation of fat cell differentiation / detection of mechanical stimulus involved in sensory perception of pain / behavioral response to cocaine / release of sequestered calcium ion into cytosol / presynaptic modulation of chemical synaptic transmission / positive regulation of glycolytic process / dendritic shaft / glycolytic process / electron transport chain / caveola / memory / intracellular calcium ion homeostasis / positive regulation of inflammatory response / positive regulation of neuron apoptotic process / positive regulation of cytosolic calcium ion concentration / virus receptor activity / presynaptic membrane / cytoplasmic vesicle / chemical synaptic transmission / G alpha (q) signalling events / postsynaptic membrane / periplasmic space / electron transfer activity / positive regulation of ERK1 and ERK2 cascade / iron ion binding / response to xenobiotic stimulus / axon / neuronal cell body / positive regulation of cell population proliferation / heme binding / dendrite / protein-containing complex binding / glutamatergic synapse / identical protein binding / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 3.4 Å 分子置換 / 解像度: 3.4 Å | |||||||||
 データ登録者 データ登録者 | Kim, K.L. / Che, T. / Krumm, B.E. / Roth, B.L. | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Cell(Cambridge,Mass.) / 年: 2020 ジャーナル: Cell(Cambridge,Mass.) / 年: 2020タイトル: Structure of a Hallucinogen-Activated Gq-Coupled 5-HT 2A Serotonin Receptor 著者: Kim, K.L. / Che, T. / Panova, O. / DiBerto, J.F. / Lyu, J. / Krumm, B.E. / Wacker, D. / Robertson, M.J. / Seven, A.B. / Nichols, D.E. / Shoichet, B.K. / Skiniotis, G. / Roth, B.L. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6wgt.cif.gz 6wgt.cif.gz | 270.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6wgt.ent.gz pdb6wgt.ent.gz | 171.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6wgt.json.gz 6wgt.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  6wgt_validation.pdf.gz 6wgt_validation.pdf.gz | 2 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  6wgt_full_validation.pdf.gz 6wgt_full_validation.pdf.gz | 2 MB | 表示 | |
| XML形式データ |  6wgt_validation.xml.gz 6wgt_validation.xml.gz | 45.1 KB | 表示 | |
| CIF形式データ |  6wgt_validation.cif.gz 6wgt_validation.cif.gz | 59.6 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/wg/6wgt https://data.pdbj.org/pub/pdb/validation_reports/wg/6wgt ftp://data.pdbj.org/pub/pdb/validation_reports/wg/6wgt ftp://data.pdbj.org/pub/pdb/validation_reports/wg/6wgt | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||||||
| 2 | 
| ||||||||||||
| 3 | 
| ||||||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 , 1種, 3分子 ABC
| #1: タンパク質 | 分子量: 50534.918 Da / 分子数: 3 / 由来タイプ: 組換発現 由来: (組換発現)  Homo sapiens (ヒト), (組換発現) Homo sapiens (ヒト), (組換発現)  遺伝子: HTR2A, HTR2, cybC 発現宿主:  参照: UniProt: P28223, UniProt: P0ABE7 |
|---|
-非ポリマー , 6種, 14分子 

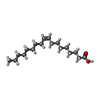








| #2: 化合物 | | #3: 化合物 | #4: 化合物 | #5: 化合物 | #6: 化合物 | #7: 化合物 | ChemComp-1PE / | |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 3.71 Å3/Da / 溶媒含有率: 66.89 % |
|---|---|
| 結晶化 | 温度: 293.15 K / 手法: 脂質キュービック相法 / pH: 7 詳細: 100 mM Tris (pH7.0) 370-410 mM KPO4-mono 90-120 mM GuHCl 28-34% PEG 400 PH範囲: 7.0 - 7.3 |
-データ収集
| 回折 | 平均測定温度: 80 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  APS APS  / ビームライン: 23-ID-B / 波長: 1.0332 Å / ビームライン: 23-ID-B / 波長: 1.0332 Å |
| 検出器 | タイプ: DECTRIS EIGER X 16M / 検出器: PIXEL / 日付: 2018年3月9日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.0332 Å / 相対比: 1 |
| 反射 | 解像度: 3.4→39.54 Å / Num. obs: 26609 / % possible obs: 94.7 % / 冗長度: 5.6 % / Biso Wilson estimate: 67.57 Å2 / CC1/2: 0.97 / Net I/σ(I): 5.5 |
| 反射 シェル | 解像度: 3.4→3.63 Å / Num. unique obs: 3887 / CC1/2: 0.611 / % possible all: 77.9 |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: 5TVN 解像度: 3.4→34.54 Å / SU ML: 0.5716 / 交差検証法: FREE R-VALUE / σ(F): 1.36 / 位相誤差: 33.7301 立体化学のターゲット値: GeoStd + Monomer Library + CDL v1.2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.11 Å / 溶媒モデル: FLAT BULK SOLVENT MODEL | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 51.37 Å2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 3.4→34.54 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル |
|
 ムービー
ムービー コントローラー
コントローラー















 PDBj
PDBj




















