| 登録情報 | データベース: PDB / ID: 6cte
|
|---|
| タイトル | 77Se-NMR probes the protein environment of selenomethionine |
|---|
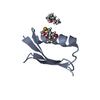
 要素 要素 | Immunoglobulin G-binding protein G |
|---|
 キーワード キーワード | IMMUNE SYSTEM / Immunoglobulin G-binding protein domain B1 |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
IgG-binding B / B domain / Ubiquitin-like (UB roll) - #10 / M protein-type anchor domain / GA-like domain / GA-like domain / Immunoglobulin/albumin-binding domain superfamily / YSIRK Gram-positive signal peptide / LPXTG cell wall anchor motif / Gram-positive cocci surface proteins LPxTG motif profile. ...IgG-binding B / B domain / Ubiquitin-like (UB roll) - #10 / M protein-type anchor domain / GA-like domain / GA-like domain / Immunoglobulin/albumin-binding domain superfamily / YSIRK Gram-positive signal peptide / LPXTG cell wall anchor motif / Gram-positive cocci surface proteins LPxTG motif profile. / LPXTG cell wall anchor domain / Ubiquitin-like (UB roll) / Roll / Alpha Beta類似検索 - ドメイン・相同性 ACETATE ION / PHOSPHATE ION / Immunoglobulin G-binding protein G類似検索 - 構成要素 |
|---|
| 生物種 |  Streptococcus sp. group G (バクテリア) Streptococcus sp. group G (バクテリア) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.2 Å 分子置換 / 解像度: 1.2 Å |
|---|
 データ登録者 データ登録者 | Chen, Q. / Rozovsky, S. |
|---|
| 資金援助 |  米国, 3件 米国, 3件 | 組織 | 認可番号 | 国 |
|---|
| National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS) | 5 P30 GM110758-02 |  米国 米国 | | National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS) | 5 P20 GM104316 |  米国 米国 | | National Science Foundation (NSF, United States) | MCB-1616178 |  米国 米国 |
|
|---|
 引用 引用 |  ジャーナル: J.Phys.Chem.B / 年: 2020 ジャーナル: J.Phys.Chem.B / 年: 2020
タイトル: 77Se NMR Probes the Protein Environment of Selenomethionine.
著者: Chen, Q. / Xu, S. / Lu, X. / Boeri, M.V. / Pepelyayeva, Y. / Diaz, E.L. / Soni, S.D. / Allaire, M. / Forstner, M.B. / Bahnson, B.J. / Rozovsky, S. |
|---|
| 履歴 | | 登録 | 2018年3月22日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2019年7月10日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2019年11月27日 | Group: Author supporting evidence / カテゴリ: pdbx_audit_support / Item: _pdbx_audit_support.funding_organization |
|---|
| 改定 1.2 | 2020年1月22日 | Group: Database references / カテゴリ: citation / citation_author
Item: _citation.country / _citation.journal_abbrev ..._citation.country / _citation.journal_abbrev / _citation.journal_id_ASTM / _citation.journal_id_CSD / _citation.journal_id_ISSN / _citation.pdbx_database_id_DOI / _citation.pdbx_database_id_PubMed / _citation.title / _citation.year |
|---|
| 改定 1.3 | 2020年2月12日 | Group: Database references / カテゴリ: citation / citation_author
Item: _citation.journal_volume / _citation.page_first ..._citation.journal_volume / _citation.page_first / _citation.page_last / _citation_author.identifier_ORCID |
|---|
| 改定 1.4 | 2023年10月4日 | Group: Data collection / Database references / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
| 改定 1.5 | 2023年11月15日 | Group: Data collection / カテゴリ: chem_comp_atom / chem_comp_bond / Item: _chem_comp_atom.atom_id / _chem_comp_bond.atom_id_2 |
|---|
| 改定 1.6 | 2024年11月20日 | Group: Structure summary
カテゴリ: pdbx_entry_details / pdbx_modification_feature |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Streptococcus sp. group G (バクテリア)
Streptococcus sp. group G (バクテリア) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.2 Å
分子置換 / 解像度: 1.2 Å  データ登録者
データ登録者 米国, 3件
米国, 3件  引用
引用 ジャーナル: J.Phys.Chem.B / 年: 2020
ジャーナル: J.Phys.Chem.B / 年: 2020 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 6cte.cif.gz
6cte.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb6cte.ent.gz
pdb6cte.ent.gz PDB形式
PDB形式 6cte.json.gz
6cte.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 6cte_validation.pdf.gz
6cte_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 6cte_full_validation.pdf.gz
6cte_full_validation.pdf.gz 6cte_validation.xml.gz
6cte_validation.xml.gz 6cte_validation.cif.gz
6cte_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/ct/6cte
https://data.pdbj.org/pub/pdb/validation_reports/ct/6cte ftp://data.pdbj.org/pub/pdb/validation_reports/ct/6cte
ftp://data.pdbj.org/pub/pdb/validation_reports/ct/6cte リンク
リンク 集合体
集合体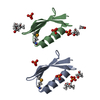


 要素
要素 Streptococcus sp. group G (バクテリア)
Streptococcus sp. group G (バクテリア)








 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  ALS
ALS  / ビームライン: 5.0.1 / 波長: 0.9795 Å
/ ビームライン: 5.0.1 / 波長: 0.9795 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー



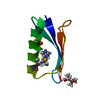










 PDBj
PDBj





