| 登録情報 | データベース: PDB / ID: 5znp
|
|---|
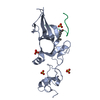
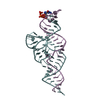
| タイトル | Crystal structure of PtSHL in complex with an H3K4me3 peptide |
|---|
 要素 要素 | - 15-mer peptide from Histone H3.2
- SHORT LIFE family protein
|
|---|
 キーワード キーワード | GENE REGULATION / BAH / PHD / SHL / plant / H3K4me3 / epigenetics |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
chromocenter / plastid / structural constituent of chromatin / nucleosome / protein heterodimerization activity / chromatin binding / DNA binding / extracellular region / zinc ion binding / nucleus ...chromocenter / plastid / structural constituent of chromatin / nucleosome / protein heterodimerization activity / chromatin binding / DNA binding / extracellular region / zinc ion binding / nucleus / plasma membrane / cytosol類似検索 - 分子機能 Bromo adjacent homology (BAH) domain / Bromo adjacent homology domain / BAH domain / Bromo adjacent homology (BAH) domain / Bromo adjacent homology (BAH) domain superfamily / BAH domain profile. / Zinc finger, PHD-type, conserved site / PHD-finger / Zinc finger PHD-type signature. / Zinc finger PHD-type profile. ...Bromo adjacent homology (BAH) domain / Bromo adjacent homology domain / BAH domain / Bromo adjacent homology (BAH) domain / Bromo adjacent homology (BAH) domain superfamily / BAH domain profile. / Zinc finger, PHD-type, conserved site / PHD-finger / Zinc finger PHD-type signature. / Zinc finger PHD-type profile. / Zinc finger, PHD-finger / Zinc finger, PHD-type / PHD zinc finger / Zinc finger, FYVE/PHD-type / Histone H3 signature 1. / SH3 type barrels. / Histone H3 signature 2. / Histone H3 / Histone H3/CENP-A / Histone H2A/H2B/H3 / Core histone H2A/H2B/H3/H4 / Histone-fold / Zinc finger, RING/FYVE/PHD-type / Roll / Mainly Beta類似検索 - ドメイン・相同性 PHD-type domain-containing protein / Histone H3.1類似検索 - 構成要素 |
|---|
| 生物種 |   Populus trichocarpa (ブラックコットンウッド(ポプラ)) Populus trichocarpa (ブラックコットンウッド(ポプラ))
  Arabidopsis thaliana (シロイヌナズナ) Arabidopsis thaliana (シロイヌナズナ) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.8 Å 分子置換 / 解像度: 2.8 Å |
|---|
 データ登録者 データ登録者 | Lv, X. / Du, J. |
|---|
| 資金援助 |  中国, 1件 中国, 1件 | 組織 | 認可番号 | 国 |
|---|
| Ministry of Science and Technology (China) | 2016YFA0503200 |  中国 中国 |
|
|---|
 引用 引用 |  ジャーナル: Nat Commun / 年: 2018 ジャーナル: Nat Commun / 年: 2018
タイトル: Dual recognition of H3K4me3 and H3K27me3 by a plant histone reader SHL.
著者: Qian, S. / Lv, X. / Scheid, R.N. / Lu, L. / Yang, Z. / Chen, W. / Liu, R. / Boersma, M.D. / Denu, J.M. / Zhong, X. / Du, J. |
|---|
| 履歴 | | 登録 | 2018年4月10日 | 登録サイト: PDBJ / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2018年7月18日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2023年11月22日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / struct_conn / struct_conn_type
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _struct_conn.conn_type_id / _struct_conn.id / _struct_conn.pdbx_dist_value / _struct_conn.pdbx_leaving_atom_flag / _struct_conn.ptnr1_auth_asym_id / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_asym_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_conn_type.id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報

 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.8 Å
分子置換 / 解像度: 2.8 Å  データ登録者
データ登録者 中国, 1件
中国, 1件  引用
引用 ジャーナル: Nat Commun / 年: 2018
ジャーナル: Nat Commun / 年: 2018 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5znp.cif.gz
5znp.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5znp.ent.gz
pdb5znp.ent.gz PDB形式
PDB形式 5znp.json.gz
5znp.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 5znp_validation.pdf.gz
5znp_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 5znp_full_validation.pdf.gz
5znp_full_validation.pdf.gz 5znp_validation.xml.gz
5znp_validation.xml.gz 5znp_validation.cif.gz
5znp_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/zn/5znp
https://data.pdbj.org/pub/pdb/validation_reports/zn/5znp ftp://data.pdbj.org/pub/pdb/validation_reports/zn/5znp
ftp://data.pdbj.org/pub/pdb/validation_reports/zn/5znp リンク
リンク 集合体
集合体


 要素
要素


 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  SSRF
SSRF  / ビームライン: BL19U1 / 波長: 0.9792 Å
/ ビームライン: BL19U1 / 波長: 0.9792 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー














 PDBj
PDBj





