[English] 日本語
 Yorodumi
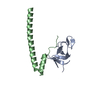
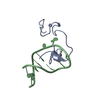
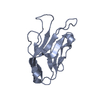
Yorodumi- PDB-3e2u: Crystal structure of the zink-knuckle 2 domain of human CLIP-170 ... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 3e2u | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | Crystal structure of the zink-knuckle 2 domain of human CLIP-170 in complex with CAP-Gly domain of human dynactin-1 (p150-GLUED) | |||||||||
 Components Components |
| |||||||||
 Keywords Keywords | PROTEIN BINDING / STRUCTURAL PROTEIN MICROTUBULE BINDING / DYNACTIN / CYTOSKELETON ASSOCIATED PROTEIN / P150GLUED / CLIP-170/RESTIN / +TIP PROTEIN COMPLEX STRUCTURE / ZINC-KNUCKLE / AUTOINHIBITION / Cytoskeleton / Dynein / Microtubule / Motor protein / Phosphoprotein | |||||||||
| Function / homology |  Function and homology information Function and homology informationcell cortex region / centriolar subdistal appendage / positive regulation of neuromuscular junction development / centriole-centriole cohesion / microtubule anchoring at centrosome / maintenance of synapse structure / ventral spinal cord development / mitotic nuclear membrane disassembly / dynein complex / microtubule plus-end ...cell cortex region / centriolar subdistal appendage / positive regulation of neuromuscular junction development / centriole-centriole cohesion / microtubule anchoring at centrosome / maintenance of synapse structure / ventral spinal cord development / mitotic nuclear membrane disassembly / dynein complex / microtubule plus-end / XBP1(S) activates chaperone genes / positive regulation of microtubule nucleation / melanosome transport / microtubule plus-end binding / microtubule bundle formation / non-motile cilium assembly / intermediate filament / Signaling by LTK in cancer / retrograde transport, endosome to Golgi / COPI-independent Golgi-to-ER retrograde traffic / microtubule associated complex / nuclear migration / perinuclear theca / neuromuscular process / establishment of mitotic spindle orientation / neuromuscular junction development / motor behavior / cell leading edge / RHO GTPases activate IQGAPs / positive regulation of microtubule polymerization / intercellular bridge / COPI-mediated anterograde transport / ruffle / cytoplasmic microtubule organization / neuron projection maintenance / Amplification of signal from unattached kinetochores via a MAD2 inhibitory signal / Loss of Nlp from mitotic centrosomes / Loss of proteins required for interphase microtubule organization from the centrosome / Recruitment of mitotic centrosome proteins and complexes / MHC class II antigen presentation / Recruitment of NuMA to mitotic centrosomes / Anchoring of the basal body to the plasma membrane / Mitotic Prometaphase / EML4 and NUDC in mitotic spindle formation / HSP90 chaperone cycle for steroid hormone receptors (SHR) in the presence of ligand / cytoplasmic vesicle membrane / acrosomal vesicle / AURKA Activation by TPX2 / Resolution of Sister Chromatid Cohesion / regulation of mitotic spindle organization / centriole / tubulin binding / neuron cellular homeostasis / RHO GTPases Activate Formins / kinetochore / tau protein binding / spindle / spindle pole / mitotic spindle / Signaling by ALK fusions and activated point mutants / Separation of Sister Chromatids / Regulation of PLK1 Activity at G2/M Transition / nuclear envelope / nervous system development / mitotic cell cycle / microtubule cytoskeleton / cell cortex / microtubule binding / microtubule / neuron projection / cilium / ciliary basal body / cell division / axon / neuronal cell body / centrosome / protein kinase binding / zinc ion binding / membrane / identical protein binding / nucleus / plasma membrane / cytoplasm / cytosol Similarity search - Function | |||||||||
| Biological species |  Homo sapiens (human) Homo sapiens (human) | |||||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  FOURIER SYNTHESIS / Resolution: 2.6 Å FOURIER SYNTHESIS / Resolution: 2.6 Å | |||||||||
 Authors Authors | Weisbrich, A. / Honnappa, S. / Capitani, G. / Steinmetz, M.O. | |||||||||
 Citation Citation |  Journal: Nat.Struct.Mol.Biol. / Year: 2007 Journal: Nat.Struct.Mol.Biol. / Year: 2007Title: Structure-function relationship of CAP-Gly domains Authors: Weisbrich, A. / Honnappa, S. / Jaussi, R. / Okhrimenko, O. / Frey, D. / Jelesarov, I. / Akhmanova, A. / Steinmetz, M.O. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  3e2u.cif.gz 3e2u.cif.gz | 170.6 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb3e2u.ent.gz pdb3e2u.ent.gz | 135.4 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  3e2u.json.gz 3e2u.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/e2/3e2u https://data.pdbj.org/pub/pdb/validation_reports/e2/3e2u ftp://data.pdbj.org/pub/pdb/validation_reports/e2/3e2u ftp://data.pdbj.org/pub/pdb/validation_reports/e2/3e2u | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  2pzo S: Starting model for refinement |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 2 | 
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 3 | 
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 4 | 
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 5 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Unit cell |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Noncrystallographic symmetry (NCS) | NCS domain:
NCS domain segments:
NCS ensembles :
|
- Components
Components
| #1: Protein | Mass: 10309.413 Da / Num. of mol.: 4 / Fragment: CAP-Gly domain Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Homo sapiens (human) / Gene: DCTN1 / Plasmid: pET15b / Production host: Homo sapiens (human) / Gene: DCTN1 / Plasmid: pET15b / Production host:  #2: Protein/peptide | Mass: 4804.103 Da / Num. of mol.: 4 / Fragment: Zn-knuckle 2 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Homo sapiens (human) / Gene: CLIP1, CYLN1, RSN / Plasmid: pETG20 MTA / Production host: Homo sapiens (human) / Gene: CLIP1, CYLN1, RSN / Plasmid: pETG20 MTA / Production host:  #3: Chemical | ChemComp-ZN / #4: Water | ChemComp-HOH / | |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.23 Å3/Da / Density % sol: 44.91 % |
|---|---|
| Crystal grow | Temperature: 293 K / Method: vapor diffusion, sitting drop / pH: 7 Details: 1.2M Trisodium Citrate, 0.1M HEPES, pH 7.0, VAPOR DIFFUSION, SITTING DROP, temperature 293K |
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  SLS SLS  / Beamline: X06SA / Wavelength: 1.039 Å / Beamline: X06SA / Wavelength: 1.039 Å |
| Detector | Type: MARMOSAIC 225 mm CCD / Detector: CCD / Date: Oct 26, 2006 / Details: dynamically bendable mirror |
| Radiation | Monochromator: LN2 cooled fixed-exit Si(111) / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 1.039 Å / Relative weight: 1 |
| Reflection twin | Operator: -k,h,l / Fraction: 0.352 |
| Reflection | Resolution: 2.6→47.02 Å / Num. obs: 16917 / % possible obs: 99.5 % / Observed criterion σ(I): -3 / Redundancy: 5.2 % / Biso Wilson estimate: 33.3 Å2 / Rsym value: 0.13 / Net I/σ(I): 10 |
| Reflection shell | Resolution: 2.6→2.8 Å / Redundancy: 5.2 % / Mean I/σ(I) obs: 3.3 / Num. measured obs: 17204 / Num. unique obs: 3307 / Rsym value: 0.563 / % possible all: 99.7 |
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  FOURIER SYNTHESIS FOURIER SYNTHESISStarting model: 2PZO (SOLVED BY MOLECULAR REPLACEMENT USING MOLREP)  2pzo Resolution: 2.6→47.015 Å / Occupancy max: 1 / Occupancy min: 0 / FOM work R set: 0.628 / Isotropic thermal model: isotropic / Cross valid method: THROUGHOUT / σ(F): 1.36 / Stereochemistry target values: TWIN_LSQ_F
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL / Bsol: 84.11 Å2 / ksol: 0.391 e/Å3 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 163.85 Å2 / Biso mean: 72.982 Å2 / Biso min: 9.64 Å2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 2.6→47.015 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints NCS |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Total num. of bins used: 8 / % reflection obs: 98 %
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller












 PDBj
PDBj

























