| 登録情報 | データベース: PDB / ID: 2zeq
|
|---|
| タイトル | Crystal structure of ubiquitin-like domain of murine Parkin |
|---|
 要素 要素 | E3 ubiquitin-protein ligase parkin |
|---|
 キーワード キーワード | LIGASE / Parkin / ubiquitin-like domain / Alternative splicing / Cell junction / Cell projection / Cytoplasm / Endoplasmic reticulum / Membrane / Metal-binding / Nucleus / Postsynaptic cell membrane / S-nitrosylation / Synapse / Ubl conjugation / Ubl conjugation pathway / Zinc / Zinc-finger |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
positive regulation of neurotransmitter uptake / negative regulation of endoplasmic reticulum stress-induced neuron intrinsic apoptotic signaling pathway / mitochondrion-derived vesicle / negative regulation of spontaneous neurotransmitter secretion / negative regulation of intralumenal vesicle formation / regulation protein catabolic process at presynapse / Josephin domain DUBs / PINK1-PRKN Mediated Mitophagy / cellular response to L-glutamine / negative regulation of exosomal secretion ...positive regulation of neurotransmitter uptake / negative regulation of endoplasmic reticulum stress-induced neuron intrinsic apoptotic signaling pathway / mitochondrion-derived vesicle / negative regulation of spontaneous neurotransmitter secretion / negative regulation of intralumenal vesicle formation / regulation protein catabolic process at presynapse / Josephin domain DUBs / PINK1-PRKN Mediated Mitophagy / cellular response to L-glutamine / negative regulation of exosomal secretion / mitochondrion to lysosome vesicle-mediated transport / Regulation of necroptotic cell death / Aggrephagy / type 2 mitophagy / response to curcumin / cellular response to hydrogen sulfide / negative regulation of mitochondrial fusion / Parkin-FBXW7-Cul1 ubiquitin ligase complex / free ubiquitin chain polymerization / positive regulation of protein linear polyubiquitination / negative regulation of actin filament bundle assembly / host-mediated suppression of viral genome replication / RBR-type E3 ubiquitin transferase / F-box domain binding / positive regulation of mitochondrial fusion / regulation of cellular response to oxidative stress / mitochondrial fragmentation involved in apoptotic process / mitochondrion localization / positive regulation of dendrite extension / regulation of dopamine metabolic process / negative regulation of excitatory postsynaptic potential / regulation of neurotransmitter secretion / protein K6-linked ubiquitination / norepinephrine metabolic process / autophagy of mitochondrion / dopaminergic synapse / positive regulation of type 2 mitophagy / protein localization to mitochondrion / synaptic transmission, dopaminergic / cellular response to toxic substance / positive regulation of protein localization to membrane / mitochondrial fission / negative regulation of oxidative stress-induced neuron intrinsic apoptotic signaling pathway / positive regulation of tumor necrosis factor-mediated signaling pathway / Antigen processing: Ubiquitination & Proteasome degradation / aggresome assembly / protein K11-linked ubiquitination / negative regulation of intrinsic apoptotic signaling pathway by p53 class mediator / cellular response to L-glutamate / negative regulation of synaptic transmission, glutamatergic / regulation of mitochondrion organization / ubiquitin conjugating enzyme binding / positive regulation of mitochondrial membrane potential / negative regulation of JNK cascade / aggresome / response to corticosterone / positive regulation of mitochondrial fission / dopamine uptake involved in synaptic transmission / ubiquitin-specific protease binding / response to muscle activity / negative regulation of release of cytochrome c from mitochondria / startle response / dopamine metabolic process / positive regulation of ATP biosynthetic process / cullin family protein binding / protein K63-linked ubiquitination / regulation of synaptic vesicle endocytosis / protein monoubiquitination / negative regulation of mitochondrial fission / response to unfolded protein / positive regulation of insulin secretion involved in cellular response to glucose stimulus / regulation of postsynaptic membrane neurotransmitter receptor levels / protein K48-linked ubiquitination / negative regulation of endoplasmic reticulum stress-induced intrinsic apoptotic signaling pathway / phospholipase binding / mitophagy / protein autoubiquitination / negative regulation of reactive oxygen species biosynthetic process / cellular response to manganese ion / Hsp70 protein binding / regulation of mitochondrial membrane potential / tubulin binding / response to endoplasmic reticulum stress / adult locomotory behavior / ubiquitin binding / learning / synaptic transmission, glutamatergic / mitochondrion organization / PDZ domain binding / locomotory behavior / protein catabolic process / negative regulation of insulin secretion / G protein-coupled receptor binding / negative regulation of canonical Wnt signaling pathway / protein destabilization / modulation of chemical synaptic transmission / neuron cellular homeostasis / beta-catenin binding / kinase binding / histone deacetylase binding類似検索 - 分子機能 : / E3 ubiquitin-protein ligase parkin / RING/Ubox-like zinc-binding domain / Parkin, RING/Ubox like zinc-binding domain / : / : / : / RING/Ubox like zinc-binding domain / RING/Ubox like zinc-binding domain / IBR domain ...: / E3 ubiquitin-protein ligase parkin / RING/Ubox-like zinc-binding domain / Parkin, RING/Ubox like zinc-binding domain / : / : / : / RING/Ubox like zinc-binding domain / RING/Ubox like zinc-binding domain / IBR domain / : / IBR domain / In Between Ring fingers / TRIAD supradomain / TRIAD supradomain profile. / Phosphatidylinositol 3-kinase Catalytic Subunit; Chain A, domain 1 / Ubiquitin-like (UB roll) / Ubiquitin family / Ubiquitin homologues / Ubiquitin domain profile. / Ubiquitin-like domain / Ubiquitin-like domain superfamily / Roll / Alpha Beta類似検索 - ドメイン・相同性 |
|---|
| 生物種 |   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) |
|---|
| 手法 |  X線回折 / X線回折 /  単波長異常分散 / 解像度: 1.65 Å 単波長異常分散 / 解像度: 1.65 Å |
|---|
 データ登録者 データ登録者 | Tomoo, K. |
|---|
 引用 引用 |  ジャーナル: Biochim.Biophys.Acta / 年: 2008 ジャーナル: Biochim.Biophys.Acta / 年: 2008
タイトル: Crystal structure and molecular dynamics simulation of ubiquitin-like domain of murine parkin
著者: Tomoo, K. / Mukai, Y. / In, Y. / Miyagawa, H. / Kitamura, K. / Yamano, A. / Shindo, H. / Ishida, T. |
|---|
| 履歴 | | 登録 | 2007年12月14日 | 登録サイト: PDBJ / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2008年8月19日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2024年3月13日 | Group: Data collection / Database references
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / struct_ref_seq_dif
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _struct_ref_seq_dif.details |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  単波長異常分散 / 解像度: 1.65 Å
単波長異常分散 / 解像度: 1.65 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Biochim.Biophys.Acta / 年: 2008
ジャーナル: Biochim.Biophys.Acta / 年: 2008 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2zeq.cif.gz
2zeq.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2zeq.ent.gz
pdb2zeq.ent.gz PDB形式
PDB形式 2zeq.json.gz
2zeq.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 2zeq_validation.pdf.gz
2zeq_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 2zeq_full_validation.pdf.gz
2zeq_full_validation.pdf.gz 2zeq_validation.xml.gz
2zeq_validation.xml.gz 2zeq_validation.cif.gz
2zeq_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/ze/2zeq
https://data.pdbj.org/pub/pdb/validation_reports/ze/2zeq ftp://data.pdbj.org/pub/pdb/validation_reports/ze/2zeq
ftp://data.pdbj.org/pub/pdb/validation_reports/ze/2zeq リンク
リンク 集合体
集合体
 要素
要素

 X線回折 / 使用した結晶の数: 2
X線回折 / 使用した結晶の数: 2  試料調製
試料調製 回転陽極 / タイプ: RIGAKU FR-E+ DW / 波長: 1.5418 Å
回転陽極 / タイプ: RIGAKU FR-E+ DW / 波長: 1.5418 Å 解析
解析 単波長異常分散 / 解像度: 1.65→39.89 Å / 交差検証法: THROUGHOUT
単波長異常分散 / 解像度: 1.65→39.89 Å / 交差検証法: THROUGHOUT ムービー
ムービー コントローラー
コントローラー



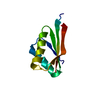









 PDBj
PDBj



