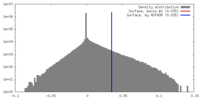
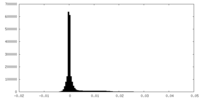
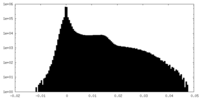
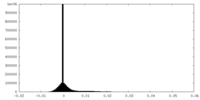
登録情報 データベース : EMDB / ID : EMD-13904タイトル The cryoEM density map of human gamma-secretase complex with various ice thickness subset 2 (EMPIAR-10194 reprocessing) Sharpened and masked map 複合体 : Human gamma-secretase機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Homo sapiens (ヒト)手法 / / 解像度 : 4.48 Å Olek M / Zhang P / Cowtan K / Chaban Y / Webb D 資金援助 European Union, 4件 Organization Grant number 国 Wellcome Trust 206422/Z/17/Z European Union Biotechnology and Biological Sciences Research Council (BBSRC) BB/S003339/1 European Union Medical Research Council (MRC, United Kingdom) MR/V000403/1 European Union European Research Council (ERC) 101021133 European Union
ジャーナル : Structure / 年 : 2022タイトル : IceBreaker: Software for high-resolution single-particle cryo-EM with non-uniform ice.
著者 :
Mateusz Olek / Kevin Cowtan / Donovan Webb / Yuriy Chaban / Peijun Zhang / 要旨 :
Despite the abundance of available software tools, optimal particle selection is still a vital issue in single-particle cryoelectron microscopy (cryo-EM). Regardless of the method used, most pickers ... Despite the abundance of available software tools, optimal particle selection is still a vital issue in single-particle cryoelectron microscopy (cryo-EM). Regardless of the method used, most pickers struggle when ice thickness varies on a micrograph. IceBreaker allows users to estimate the relative ice gradient and flatten it by equalizing the local contrast. It allows the differentiation of particles from the background and improves overall particle picking performance. Furthermore, we introduce an additional parameter corresponding to local ice thickness for each particle. Particles with a defined ice thickness can be grouped and filtered based on this parameter during processing. These functionalities are especially valuable for on-the-fly processing to automatically pick as many particles as possible from each micrograph and to select optimal regions for data collection. Finally, estimated ice gradient distributions can be stored separately and used to inspect the quality of prepared samples. 履歴 登録 2021年11月26日 - ヘッダ(付随情報) 公開 2021年12月8日 - マップ公開 2021年12月8日 - 更新 2022年4月20日 - 現状 2022年4月20日 処理サイト : PDBe / 状態 : 公開
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 マップデータ
マップデータ 試料
試料 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) データ登録者
データ登録者 引用
引用 ジャーナル: Structure / 年: 2022
ジャーナル: Structure / 年: 2022
 ジャーナル: Nature / 年: 2015
ジャーナル: Nature / 年: 2015 構造の表示
構造の表示 ムービービューア
ムービービューア SurfView
SurfView Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク emd_13904.map.gz
emd_13904.map.gz EMDBマップデータ形式
EMDBマップデータ形式 emd-13904-v30.xml
emd-13904-v30.xml emd-13904.xml
emd-13904.xml EMDBヘッダ
EMDBヘッダ emd_13904_fsc.xml
emd_13904_fsc.xml FSCデータファイル
FSCデータファイル emd_13904.png
emd_13904.png emd_13904_msk_1.map
emd_13904_msk_1.map マスクマップ
マスクマップ emd_13904_additional_1.map.gz
emd_13904_additional_1.map.gz emd_13904_additional_2.map.gz
emd_13904_additional_2.map.gz emd_13904_half_map_1.map.gz
emd_13904_half_map_1.map.gz emd_13904_half_map_2.map.gz
emd_13904_half_map_2.map.gz http://ftp.pdbj.org/pub/emdb/structures/EMD-13904
http://ftp.pdbj.org/pub/emdb/structures/EMD-13904 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13904
ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13904 リンク
リンク EMDB (EBI/PDBe) /
EMDB (EBI/PDBe) /  EMDataResource
EMDataResource マップ
マップ ダウンロード / ファイル: emd_13904.map.gz / 形式: CCP4 / 大きさ: 8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES)
ダウンロード / ファイル: emd_13904.map.gz / 形式: CCP4 / 大きさ: 8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) emd_13904_msk_1.map
emd_13904_msk_1.map 試料の構成要素
試料の構成要素 Homo sapiens (ヒト)
Homo sapiens (ヒト) Homo sapiens (ヒト)
Homo sapiens (ヒト) 解析
解析 試料調製
試料調製 電子顕微鏡法
電子顕微鏡法 FIELD EMISSION GUN
FIELD EMISSION GUN
 ムービー
ムービー コントローラー
コントローラー

































 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)