+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-12903 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of tobacco mosaic virus in nanofluidic channels | |||||||||
 マップデータ マップデータ | Sharpened and symmetrized cryo-EM density | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 | Tobacco mosaic virus-like, coat protein / Tobacco mosaic virus-like, coat protein superfamily / Virus coat protein (TMV like) / helical viral capsid / structural molecule activity / identical protein binding / Capsid protein 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |   Tobacco mosaic virus (ウイルス) Tobacco mosaic virus (ウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.7 Å | |||||||||
 データ登録者 データ登録者 | Huber ST / Sarajlic E / Huijink R / Evers WH / Jakobi AJ | |||||||||
| 資金援助 | European Union,  オランダ, 2件 オランダ, 2件
| |||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2022 ジャーナル: Elife / 年: 2022タイトル: Nanofluidic chips for cryo-EM structure determination from picoliter sample volumes. 著者: Stefan T Huber / Edin Sarajlic / Roeland Huijink / Felix Weis / Wiel H Evers / Arjen J Jakobi /   要旨: Cryogenic electron microscopy has become an essential tool for structure determination of biological macromolecules. In practice, the difficulty to reliably prepare samples with uniform ice thickness ...Cryogenic electron microscopy has become an essential tool for structure determination of biological macromolecules. In practice, the difficulty to reliably prepare samples with uniform ice thickness still represents a barrier for routine high-resolution imaging and limits the current throughput of the technique. We show that a nanofluidic sample support with well-defined geometry can be used to prepare cryo-EM specimens with reproducible ice thickness from picoliter sample volumes. The sample solution is contained in electron-transparent nanochannels that provide uniform thickness gradients without further optimisation and eliminate the potentially destructive air-water interface. We demonstrate the possibility to perform high-resolution structure determination with three standard protein specimens. Nanofabricated sample supports bear potential to automate the cryo-EM workflow, and to explore new frontiers for cryo-EM applications such as time-resolved imaging and high-throughput screening. #1:  ジャーナル: Biorxiv / 年: 2021 ジャーナル: Biorxiv / 年: 2021タイトル: Nanofluidic chips for cryo-EM structure determination from picoliter sample volumes 著者: Huber ST / Sarajlic E / Huijink R / Weis F / Evers WH / Jakobi AJ | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_12903.map.gz emd_12903.map.gz | 18.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-12903-v30.xml emd-12903-v30.xml emd-12903.xml emd-12903.xml | 19.3 KB 19.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_12903_fsc.xml emd_12903_fsc.xml | 8.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_12903.png emd_12903.png | 177.4 KB | ||
| マスクデータ |  emd_12903_msk_1.map emd_12903_msk_1.map | 64 MB |  マスクマップ マスクマップ | |
| その他 |  emd_12903_additional_1.map.gz emd_12903_additional_1.map.gz emd_12903_additional_2.map.gz emd_12903_additional_2.map.gz emd_12903_half_map_1.map.gz emd_12903_half_map_1.map.gz emd_12903_half_map_2.map.gz emd_12903_half_map_2.map.gz | 18.6 MB 12.3 MB 59.4 MB 59.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-12903 http://ftp.pdbj.org/pub/emdb/structures/EMD-12903 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12903 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12903 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_12903_validation.pdf.gz emd_12903_validation.pdf.gz | 674.5 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_12903_full_validation.pdf.gz emd_12903_full_validation.pdf.gz | 674.1 KB | 表示 | |
| XML形式データ |  emd_12903_validation.xml.gz emd_12903_validation.xml.gz | 16.2 KB | 表示 | |
| CIF形式データ |  emd_12903_validation.cif.gz emd_12903_validation.cif.gz | 21.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12903 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12903 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12903 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12903 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7ohfC C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10708 (タイトル: Apoferritin, TMV and T20S proteasome in nanofluidic channels EMPIAR-10708 (タイトル: Apoferritin, TMV and T20S proteasome in nanofluidic channelsData size: 308.3 Data #1: Unaligned multi-frame movies of pyrococcus furiosus apoferritin in silicon nitride nanochannels [micrographs - multiframe] Data #2: Multi-frame movies of T20S proteasome in silicon nitride nanochannels [micrographs - multiframe] Data #3: Multi-frame movies of TMV in silicon nitride nanochannels [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_12903.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_12903.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened and symmetrized cryo-EM density | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
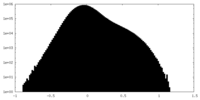
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.288 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
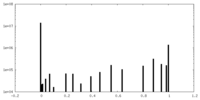
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_12903_msk_1.map emd_12903_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
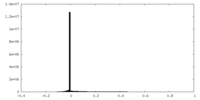
| 投影像・断面図 |
| ||||||||||||
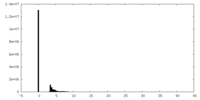
| 密度ヒストグラム |
-追加マップ: Unsharpened and symmetrized cryo-EM density
| ファイル | emd_12903_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened and symmetrized cryo-EM density | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Local resolution map
| ファイル | emd_12903_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Local resolution map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map A
| ファイル | emd_12903_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map B
| ファイル | emd_12903_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map B | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Tobacco mosaic virus in nanofluidic channels
| 全体 | 名称: Tobacco mosaic virus in nanofluidic channels |
|---|---|
| 要素 |
|
-超分子 #1: Tobacco mosaic virus in nanofluidic channels
| 超分子 | 名称: Tobacco mosaic virus in nanofluidic channels / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Tobacco mosaic virus (ウイルス) Tobacco mosaic virus (ウイルス) |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | filament |
- 試料調製
試料調製
| 濃度 | 1.1 mg/mL |
|---|---|
| 緩衝液 | pH: 7 |
| グリッド | モデル: Homemade / 材質: SILICON NITRIDE |
| 凍結 | 凍結剤: ETHANE / 装置: LEICA PLUNGER 詳細: The sample was filled into cryoChips through the cantilever and then transferred within ~10 seconds to the Leica plunger for freezing.. |
| 詳細 | The sample was filled into nanofluidic channels. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | JEOL 3200FSC |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 撮影したグリッド数: 2 / 実像数: 82 / 平均露光時間: 11.0 sec. / 平均電子線量: 59.7 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 4.1 mm |
| 試料ステージ | 試料ホルダーモデル: JEOL 3200FSC CRYOHOLDER |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: |
|---|
 ムービー
ムービー コントローラー
コントローラー















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)