登録情報 データベース : EMDB / ID : EMD-10860タイトル Cryo-EM structure of Tetrahymena thermophila mitochondrial ATP synthase - F1Fo dimer Local-resolution filtered full map of T. thermophila ATP synthase 複合体 : Mitochondrial ATP synthase, F1Fo dimerリガンド : x 9種 / / / / 機能・相同性 分子機能 ドメイン・相同性 構成要素
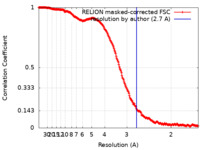
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Tetrahymena thermophila (真核生物)手法 / / 解像度 : 2.7 Å Kock Flygaard R / Muhleip A 資金援助 Organization Grant number 国 Swedish Research Council NT_2015-04107 European Research Council (ERC) ERC-2018-StG-805230 Knut and Alice Wallenberg Foundation 2018.0080
ジャーナル : Nat Commun / 年 : 2020タイトル : Type III ATP synthase is a symmetry-deviated dimer that induces membrane curvature through tetramerization.著者 : Rasmus Kock Flygaard / Alexander Mühleip / Victor Tobiasson / Alexey Amunts / 要旨 : Mitochondrial ATP synthases form functional homodimers to induce cristae curvature that is a universal property of mitochondria. To expand on the understanding of this fundamental phenomenon, we ... Mitochondrial ATP synthases form functional homodimers to induce cristae curvature that is a universal property of mitochondria. To expand on the understanding of this fundamental phenomenon, we characterized the unique type III mitochondrial ATP synthase in its dimeric and tetrameric form. The cryo-EM structure of a ciliate ATP synthase dimer reveals an unusual U-shaped assembly of 81 proteins, including a substoichiometrically bound ATPTT2, 40 lipids, and co-factors NAD and CoQ. A single copy of subunit ATPTT2 functions as a membrane anchor for the dimeric inhibitor IF. Type III specific linker proteins stably tie the ATP synthase monomers in parallel to each other. The intricate dimer architecture is scaffolded by an extended subunit-a that provides a template for both intra- and inter-dimer interactions. The latter results in the formation of tetramer assemblies, the membrane part of which we determined to 3.1 Å resolution. The structure of the type III ATP synthase tetramer and its associated lipids suggests that it is the intact unit propagating the membrane curvature. 履歴 登録 2020年4月14日 - ヘッダ(付随情報) 公開 2020年9月30日 - マップ公開 2020年9月30日 - 更新 2025年10月1日 - 現状 2025年10月1日 処理サイト : PDBe / 状態 : 公開
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 マップデータ
マップデータ 試料
試料 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 データ登録者
データ登録者 スウェーデン, 3件
スウェーデン, 3件  引用
引用 ジャーナル: Nat Commun / 年: 2020
ジャーナル: Nat Commun / 年: 2020
 構造の表示
構造の表示 ムービービューア
ムービービューア SurfView
SurfView Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク emd_10860.map.gz
emd_10860.map.gz EMDBマップデータ形式
EMDBマップデータ形式 emd-10860-v30.xml
emd-10860-v30.xml emd-10860.xml
emd-10860.xml EMDBヘッダ
EMDBヘッダ emd_10860_fsc.xml
emd_10860_fsc.xml FSCデータファイル
FSCデータファイル emd_10860.png
emd_10860.png emd_10860_msk_1.map
emd_10860_msk_1.map マスクマップ
マスクマップ emd-10860.cif.gz
emd-10860.cif.gz emd_10860_half_map_1.map.gz
emd_10860_half_map_1.map.gz emd_10860_half_map_2.map.gz
emd_10860_half_map_2.map.gz http://ftp.pdbj.org/pub/emdb/structures/EMD-10860
http://ftp.pdbj.org/pub/emdb/structures/EMD-10860 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10860
ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10860 リンク
リンク EMDB (EBI/PDBe) /
EMDB (EBI/PDBe) /  EMDataResource
EMDataResource マップ
マップ ダウンロード / ファイル: emd_10860.map.gz / 形式: CCP4 / 大きさ: 824 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES)
ダウンロード / ファイル: emd_10860.map.gz / 形式: CCP4 / 大きさ: 824 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) emd_10860_msk_1.map
emd_10860_msk_1.map 試料の構成要素
試料の構成要素 解析
解析 試料調製
試料調製 電子顕微鏡法
電子顕微鏡法 FIELD EMISSION GUN
FIELD EMISSION GUN
 ムービー
ムービー コントローラー
コントローラー






























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)