+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-9599 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of mouse heavy-chain apoferritin at 1.62 A | |||||||||
 マップデータ マップデータ | mouse heavy chain apoferritin sharpened map | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 1.62 Å | |||||||||
 データ登録者 データ登録者 | Danev R / Yanagisawa H / Kikkawa M | |||||||||
| 資金援助 |  日本, 1件 日本, 1件
| |||||||||
 引用 引用 |  ジャーナル: Trends Biochem Sci / 年: 2019 ジャーナル: Trends Biochem Sci / 年: 2019タイトル: Cryo-Electron Microscopy Methodology: Current Aspects and Future Directions. 著者: Radostin Danev / Haruaki Yanagisawa / Masahide Kikkawa /  要旨: Cryo-electron microscopy (cryo-EM) has emerged as a powerful structure determination technique. Its most prolific branch is single particle analysis (SPA), a method being used in a growing number of ...Cryo-electron microscopy (cryo-EM) has emerged as a powerful structure determination technique. Its most prolific branch is single particle analysis (SPA), a method being used in a growing number of laboratories worldwide to determine high-resolution protein structures. Cryo-electron tomography (cryo-ET) is another powerful approach that enables visualization of protein complexes in their native cellular environment. Despite the wide-ranging success of cryo-EM, there are many methodological aspects that could be improved. Those include sample preparation, sample screening, data acquisition, image processing, and structure validation. Future developments will increase the reliability and throughput of the technique and reduce the cost and skill level barrier for its adoption. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_9599.map.gz emd_9599.map.gz | 166.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-9599-v30.xml emd-9599-v30.xml emd-9599.xml emd-9599.xml | 16.7 KB 16.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_9599.png emd_9599.png | 250.1 KB | ||
| マスクデータ |  emd_9599_msk_1.map emd_9599_msk_1.map | 178 MB |  マスクマップ マスクマップ | |
| その他 |  emd_9599_half_map_1.map.gz emd_9599_half_map_1.map.gz emd_9599_half_map_2.map.gz emd_9599_half_map_2.map.gz | 135.4 MB 135.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-9599 http://ftp.pdbj.org/pub/emdb/structures/EMD-9599 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9599 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9599 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_9599_validation.pdf.gz emd_9599_validation.pdf.gz | 78.1 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_9599_full_validation.pdf.gz emd_9599_full_validation.pdf.gz | 77.2 KB | 表示 | |
| XML形式データ |  emd_9599_validation.xml.gz emd_9599_validation.xml.gz | 494 B | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9599 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9599 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9599 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9599 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9914C C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10216 (タイトル: Cryo-EM structure of mouse heavy-chain apoferritin at 1.62 A EMPIAR-10216 (タイトル: Cryo-EM structure of mouse heavy-chain apoferritin at 1.62 AData size: 3.0 TB / Data #1: RAW movies [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_9599.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_9599.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | mouse heavy chain apoferritin sharpened map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.517 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
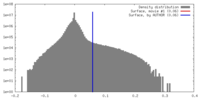
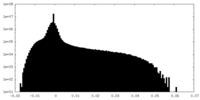
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_9599_msk_1.map emd_9599_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
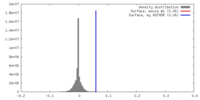
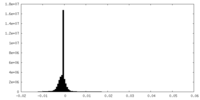
| 密度ヒストグラム |
-ハーフマップ: mouse heavy chain apoferritin unfiltered half map 2
| ファイル | emd_9599_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | mouse heavy chain apoferritin unfiltered half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
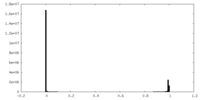
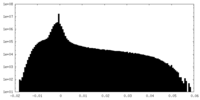
| 密度ヒストグラム |
-ハーフマップ: mouse heavy chain apoferritin unfiltered half map 1
| ファイル | emd_9599_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | mouse heavy chain apoferritin unfiltered half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
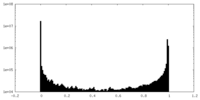
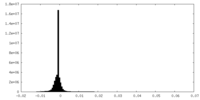
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : apoferritin
| 全体 | 名称: apoferritin |
|---|---|
| 要素 |
|
-超分子 #1: apoferritin
| 超分子 | 名称: apoferritin / タイプ: complex / ID: 1 / 親要素: 0 |
|---|---|
| 由来(天然) | 生物種:  |
| 組換発現 | 生物種:  |
| 分子量 | 理論値: 500 KDa |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 4 mg/mL |
|---|---|
| 緩衝液 | pH: 7 |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY ARRAY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 雰囲気: AIR / 詳細: JEOL Ion Bombarder on Soft setting |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 4 K / 装置: FEI VITROBOT MARK IV / 詳細: blot for 5 s. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| アライメント法 | Coma free - Residual tilt: 0.02 mrad |
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: COUNTING / デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / デジタル化 - サンプリング間隔: 15.0 µm / 撮影したグリッド数: 1 / 実像数: 1647 / 平均露光時間: 18.21 sec. / 平均電子線量: 50.0 e/Å2 / 詳細: Exposure rate 0.74 e/pix/s |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 最大 デフォーカス(補正後): 1.3 µm / 最小 デフォーカス(補正後): 0.2 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 1.3 µm / 最小 デフォーカス(公称値): 0.2 µm / 倍率(公称値): 155000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: |
|---|---|
| 精密化 | プロトコル: RIGID BODY FIT |
 ムービー
ムービー コントローラー
コントローラー

























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)